BRPI0921843B1 - composição de vacina, e, uso de uma composição de vacina - Google Patents
composição de vacina, e, uso de uma composição de vacina Download PDFInfo
- Publication number
- BRPI0921843B1 BRPI0921843B1 BRPI0921843-2A BRPI0921843A BRPI0921843B1 BR PI0921843 B1 BRPI0921843 B1 BR PI0921843B1 BR PI0921843 A BRPI0921843 A BR PI0921843A BR PI0921843 B1 BRPI0921843 B1 BR PI0921843B1
- Authority
- BR
- Brazil
- Prior art keywords
- seq
- meleagrimitis
- eimeria
- species
- oocysts
- Prior art date
Links
- 229960005486 vaccine Drugs 0.000 title claims abstract description 67
- 239000000203 mixture Substances 0.000 title claims abstract description 35
- 241001278028 Eimeria meleagrimitis Species 0.000 claims abstract description 151
- 241000223924 Eimeria Species 0.000 claims abstract description 133
- 241000894007 species Species 0.000 claims abstract description 106
- 208000003495 Coccidiosis Diseases 0.000 claims abstract description 23
- 206010023076 Isosporiasis Diseases 0.000 claims abstract description 22
- 210000003250 oocyst Anatomy 0.000 claims description 103
- 241000224483 Coccidia Species 0.000 claims description 32
- 241000289819 Eimeria adenoeides Species 0.000 claims description 31
- 241001327860 Eimeria dispersa Species 0.000 claims description 26
- 241001327857 Eimeria gallopavonis Species 0.000 claims description 25
- 230000002238 attenuated effect Effects 0.000 claims description 19
- 238000004519 manufacturing process Methods 0.000 claims description 16
- 244000045947 parasite Species 0.000 claims description 14
- 241001452550 Eimeria meleagridis Species 0.000 claims description 6
- 210000003936 merozoite Anatomy 0.000 claims description 6
- 241001452562 Eimeria innocua Species 0.000 claims description 5
- 241000223935 Cryptosporidium Species 0.000 claims description 4
- 241000567229 Isospora Species 0.000 claims description 4
- 241000987822 Cystoisospora Species 0.000 claims description 3
- 239000003814 drug Substances 0.000 claims description 3
- 238000003752 polymerase chain reaction Methods 0.000 abstract description 85
- 108091034117 Oligonucleotide Proteins 0.000 abstract description 78
- 238000000034 method Methods 0.000 abstract description 50
- 239000012472 biological sample Substances 0.000 abstract description 25
- 241000286209 Phasianidae Species 0.000 abstract description 24
- 230000001717 pathogenic effect Effects 0.000 abstract description 17
- 238000012408 PCR amplification Methods 0.000 abstract description 6
- 239000003223 protective agent Substances 0.000 abstract description 2
- 239000002773 nucleotide Substances 0.000 description 93
- 125000003729 nucleotide group Chemical group 0.000 description 93
- 239000013615 primer Substances 0.000 description 85
- 150000007523 nucleic acids Chemical group 0.000 description 61
- 108020004707 nucleic acids Proteins 0.000 description 53
- 102000039446 nucleic acids Human genes 0.000 description 53
- 241000271566 Aves Species 0.000 description 43
- 239000012634 fragment Substances 0.000 description 36
- 241001465754 Metazoa Species 0.000 description 35
- 108091028043 Nucleic acid sequence Proteins 0.000 description 34
- 239000000047 product Substances 0.000 description 32
- JLCPHMBAVCMARE-UHFFFAOYSA-N [3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-hydroxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methyl [5-(6-aminopurin-9-yl)-2-(hydroxymethyl)oxolan-3-yl] hydrogen phosphate Polymers Cc1cn(C2CC(OP(O)(=O)OCC3OC(CC3OP(O)(=O)OCC3OC(CC3O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c3nc(N)[nH]c4=O)C(COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3CO)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cc(C)c(=O)[nH]c3=O)n3cc(C)c(=O)[nH]c3=O)n3ccc(N)nc3=O)n3cc(C)c(=O)[nH]c3=O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)O2)c(=O)[nH]c1=O JLCPHMBAVCMARE-UHFFFAOYSA-N 0.000 description 31
- 108020004414 DNA Proteins 0.000 description 30
- 208000015181 infectious disease Diseases 0.000 description 23
- 210000003608 fece Anatomy 0.000 description 17
- 239000000463 material Substances 0.000 description 17
- 230000024241 parasitism Effects 0.000 description 17
- 239000002671 adjuvant Substances 0.000 description 14
- 239000000499 gel Substances 0.000 description 14
- 230000036039 immunity Effects 0.000 description 14
- 244000052769 pathogen Species 0.000 description 14
- KMUONIBRACKNSN-UHFFFAOYSA-N potassium dichromate Chemical compound [K+].[K+].[O-][Cr](=O)(=O)O[Cr]([O-])(=O)=O KMUONIBRACKNSN-UHFFFAOYSA-N 0.000 description 14
- 230000007170 pathology Effects 0.000 description 13
- 230000006378 damage Effects 0.000 description 12
- 230000003902 lesion Effects 0.000 description 12
- 239000000725 suspension Substances 0.000 description 12
- XLYOFNOQVPJJNP-UHFFFAOYSA-N water Substances O XLYOFNOQVPJJNP-UHFFFAOYSA-N 0.000 description 12
- 238000006243 chemical reaction Methods 0.000 description 11
- 238000011081 inoculation Methods 0.000 description 11
- 239000000523 sample Substances 0.000 description 11
- 239000006228 supernatant Substances 0.000 description 11
- 208000027418 Wounds and injury Diseases 0.000 description 10
- 210000001198 duodenum Anatomy 0.000 description 10
- 208000014674 injury Diseases 0.000 description 10
- 210000000936 intestine Anatomy 0.000 description 10
- 230000007918 pathogenicity Effects 0.000 description 9
- 241000287828 Gallus gallus Species 0.000 description 8
- 235000013330 chicken meat Nutrition 0.000 description 8
- 201000010099 disease Diseases 0.000 description 8
- 208000037265 diseases, disorders, signs and symptoms Diseases 0.000 description 8
- 230000037406 food intake Effects 0.000 description 8
- 230000003053 immunization Effects 0.000 description 8
- 210000000813 small intestine Anatomy 0.000 description 8
- 241000288147 Meleagris gallopavo Species 0.000 description 7
- 238000002649 immunization Methods 0.000 description 7
- 230000002458 infectious effect Effects 0.000 description 7
- 230000000968 intestinal effect Effects 0.000 description 7
- 238000012300 Sequence Analysis Methods 0.000 description 6
- 238000004458 analytical method Methods 0.000 description 6
- 239000000872 buffer Substances 0.000 description 6
- 210000001563 schizont Anatomy 0.000 description 6
- 210000003046 sporozoite Anatomy 0.000 description 6
- 210000002534 adenoid Anatomy 0.000 description 5
- 239000000427 antigen Substances 0.000 description 5
- 102000036639 antigens Human genes 0.000 description 5
- 108091007433 antigens Proteins 0.000 description 5
- 210000004027 cell Anatomy 0.000 description 5
- 239000013256 coordination polymer Substances 0.000 description 5
- 235000020188 drinking water Nutrition 0.000 description 5
- 239000003651 drinking water Substances 0.000 description 5
- 210000003097 mucus Anatomy 0.000 description 5
- 239000003921 oil Substances 0.000 description 5
- 235000019198 oils Nutrition 0.000 description 5
- 230000008569 process Effects 0.000 description 5
- 230000009467 reduction Effects 0.000 description 5
- 239000013049 sediment Substances 0.000 description 5
- 239000008399 tap water Substances 0.000 description 5
- 235000020679 tap water Nutrition 0.000 description 5
- 238000012360 testing method Methods 0.000 description 5
- 238000012546 transfer Methods 0.000 description 5
- 210000001325 yolk sac Anatomy 0.000 description 5
- ZSZFUDFOPOMEET-UHFFFAOYSA-N 2-(4-chlorophenyl)-2-[2,6-dichloro-4-(3,5-dioxo-1,2,4-triazin-2-yl)phenyl]acetonitrile Chemical compound C1=CC(Cl)=CC=C1C(C#N)C1=C(Cl)C=C(N2C(NC(=O)C=N2)=O)C=C1Cl ZSZFUDFOPOMEET-UHFFFAOYSA-N 0.000 description 4
- 239000003155 DNA primer Substances 0.000 description 4
- 108090000790 Enzymes Proteins 0.000 description 4
- 102000004190 Enzymes Human genes 0.000 description 4
- 208000032843 Hemorrhage Diseases 0.000 description 4
- 108020001027 Ribosomal DNA Proteins 0.000 description 4
- 229920002125 Sokalan® Polymers 0.000 description 4
- 229940024194 amprol Drugs 0.000 description 4
- LCTXBFGHZLGBNU-UHFFFAOYSA-M amprolium Chemical compound [Cl-].NC1=NC(CCC)=NC=C1C[N+]1=CC=CC=C1C LCTXBFGHZLGBNU-UHFFFAOYSA-M 0.000 description 4
- 230000001580 bacterial effect Effects 0.000 description 4
- 210000004534 cecum Anatomy 0.000 description 4
- 230000002550 fecal effect Effects 0.000 description 4
- 238000005188 flotation Methods 0.000 description 4
- 210000001630 jejunum Anatomy 0.000 description 4
- 238000011068 loading method Methods 0.000 description 4
- 238000012163 sequencing technique Methods 0.000 description 4
- 239000007921 spray Substances 0.000 description 4
- 230000009466 transformation Effects 0.000 description 4
- 238000002255 vaccination Methods 0.000 description 4
- 229920001817 Agar Polymers 0.000 description 3
- 108091035707 Consensus sequence Proteins 0.000 description 3
- 241000179197 Cyclospora Species 0.000 description 3
- 241000223934 Eimeria maxima Species 0.000 description 3
- 241000530449 Eimeria mivati Species 0.000 description 3
- 241000499563 Eimeria necatrix Species 0.000 description 3
- 241000223932 Eimeria tenella Species 0.000 description 3
- 241000588724 Escherichia coli Species 0.000 description 3
- 206010020565 Hyperaemia Diseases 0.000 description 3
- 108091023242 Internal transcribed spacer Proteins 0.000 description 3
- 238000010222 PCR analysis Methods 0.000 description 3
- FAPWRFPIFSIZLT-UHFFFAOYSA-M Sodium chloride Chemical class [Na+].[Cl-] FAPWRFPIFSIZLT-UHFFFAOYSA-M 0.000 description 3
- 239000008272 agar Substances 0.000 description 3
- 239000011543 agarose gel Substances 0.000 description 3
- 230000003321 amplification Effects 0.000 description 3
- 238000000137 annealing Methods 0.000 description 3
- 230000001165 anti-coccidial effect Effects 0.000 description 3
- 230000000692 anti-sense effect Effects 0.000 description 3
- 238000005119 centrifugation Methods 0.000 description 3
- 230000029087 digestion Effects 0.000 description 3
- 238000001962 electrophoresis Methods 0.000 description 3
- 210000002919 epithelial cell Anatomy 0.000 description 3
- 235000012907 honey Nutrition 0.000 description 3
- 210000003405 ileum Anatomy 0.000 description 3
- 230000028993 immune response Effects 0.000 description 3
- 238000003199 nucleic acid amplification method Methods 0.000 description 3
- 239000002245 particle Substances 0.000 description 3
- 238000013081 phylogenetic analysis Methods 0.000 description 3
- 239000013612 plasmid Substances 0.000 description 3
- -1 polyethylene Polymers 0.000 description 3
- 230000000644 propagated effect Effects 0.000 description 3
- 108090000623 proteins and genes Proteins 0.000 description 3
- 238000000746 purification Methods 0.000 description 3
- 210000000664 rectum Anatomy 0.000 description 3
- 230000002829 reductive effect Effects 0.000 description 3
- 238000011160 research Methods 0.000 description 3
- 230000001568 sexual effect Effects 0.000 description 3
- 239000002002 slurry Substances 0.000 description 3
- 239000000243 solution Substances 0.000 description 3
- 239000000126 substance Substances 0.000 description 3
- 210000001519 tissue Anatomy 0.000 description 3
- GVJHHUAWPYXKBD-UHFFFAOYSA-N (±)-α-Tocopherol Chemical compound OC1=C(C)C(C)=C2OC(CCCC(C)CCCC(C)CCCC(C)C)(C)CCC2=C1C GVJHHUAWPYXKBD-UHFFFAOYSA-N 0.000 description 2
- 108020004565 5.8S Ribosomal RNA Proteins 0.000 description 2
- 241000321096 Adenoides Species 0.000 description 2
- 229920000936 Agarose Polymers 0.000 description 2
- CPELXLSAUQHCOX-UHFFFAOYSA-M Bromide Chemical compound [Br-] CPELXLSAUQHCOX-UHFFFAOYSA-M 0.000 description 2
- 241000223931 Eimeria acervulina Species 0.000 description 2
- 244000309702 Eimeria hagani Species 0.000 description 2
- 241000179199 Eimeria mitis Species 0.000 description 2
- 241000499544 Eimeria praecox Species 0.000 description 2
- LFQSCWFLJHTTHZ-UHFFFAOYSA-N Ethanol Chemical compound CCO LFQSCWFLJHTTHZ-UHFFFAOYSA-N 0.000 description 2
- 241000288145 Meleagris Species 0.000 description 2
- 240000007594 Oryza sativa Species 0.000 description 2
- 235000007164 Oryza sativa Nutrition 0.000 description 2
- 208000009182 Parasitemia Diseases 0.000 description 2
- 208000030852 Parasitic disease Diseases 0.000 description 2
- 102000006382 Ribonucleases Human genes 0.000 description 2
- 108010083644 Ribonucleases Proteins 0.000 description 2
- CZMRCDWAGMRECN-UGDNZRGBSA-N Sucrose Chemical compound O[C@H]1[C@H](O)[C@@H](CO)O[C@@]1(CO)O[C@@H]1[C@H](O)[C@@H](O)[C@H](O)[C@@H](CO)O1 CZMRCDWAGMRECN-UGDNZRGBSA-N 0.000 description 2
- 229930006000 Sucrose Natural products 0.000 description 2
- 238000005273 aeration Methods 0.000 description 2
- XAGFODPZIPBFFR-UHFFFAOYSA-N aluminium Chemical compound [Al] XAGFODPZIPBFFR-UHFFFAOYSA-N 0.000 description 2
- 229910052782 aluminium Inorganic materials 0.000 description 2
- 229940124536 anticoccidial agent Drugs 0.000 description 2
- VEZXCJBBBCKRPI-UHFFFAOYSA-N beta-propiolactone Chemical compound O=C1CCO1 VEZXCJBBBCKRPI-UHFFFAOYSA-N 0.000 description 2
- 230000004071 biological effect Effects 0.000 description 2
- 230000000740 bleeding effect Effects 0.000 description 2
- 210000004369 blood Anatomy 0.000 description 2
- 239000008280 blood Substances 0.000 description 2
- 238000012512 characterization method Methods 0.000 description 2
- 239000003795 chemical substances by application Substances 0.000 description 2
- 238000010367 cloning Methods 0.000 description 2
- 230000007423 decrease Effects 0.000 description 2
- 238000011161 development Methods 0.000 description 2
- 230000018109 developmental process Effects 0.000 description 2
- SOCTUWSJJQCPFX-UHFFFAOYSA-N dichromate(2-) Chemical compound [O-][Cr](=O)(=O)O[Cr]([O-])(=O)=O SOCTUWSJJQCPFX-UHFFFAOYSA-N 0.000 description 2
- 235000005911 diet Nutrition 0.000 description 2
- 230000037213 diet Effects 0.000 description 2
- 238000010790 dilution Methods 0.000 description 2
- 239000012895 dilution Substances 0.000 description 2
- 239000006185 dispersion Substances 0.000 description 2
- 239000000839 emulsion Substances 0.000 description 2
- 238000005516 engineering process Methods 0.000 description 2
- 230000007613 environmental effect Effects 0.000 description 2
- 238000002474 experimental method Methods 0.000 description 2
- 238000000605 extraction Methods 0.000 description 2
- 238000001914 filtration Methods 0.000 description 2
- 235000013305 food Nutrition 0.000 description 2
- 230000002496 gastric effect Effects 0.000 description 2
- 210000001035 gastrointestinal tract Anatomy 0.000 description 2
- 208000037824 growth disorder Diseases 0.000 description 2
- 230000008105 immune reaction Effects 0.000 description 2
- 230000005847 immunogenicity Effects 0.000 description 2
- 229960001438 immunostimulant agent Drugs 0.000 description 2
- 238000011065 in-situ storage Methods 0.000 description 2
- 239000012678 infectious agent Substances 0.000 description 2
- 229910052500 inorganic mineral Inorganic materials 0.000 description 2
- 238000002955 isolation Methods 0.000 description 2
- 230000000670 limiting effect Effects 0.000 description 2
- 239000011707 mineral Substances 0.000 description 2
- 235000010755 mineral Nutrition 0.000 description 2
- 238000013425 morphometry Methods 0.000 description 2
- 210000004877 mucosa Anatomy 0.000 description 2
- 102000042567 non-coding RNA Human genes 0.000 description 2
- 239000013600 plasmid vector Substances 0.000 description 2
- 239000013641 positive control Substances 0.000 description 2
- 244000144977 poultry Species 0.000 description 2
- 235000013594 poultry meat Nutrition 0.000 description 2
- 108090000765 processed proteins & peptides Proteins 0.000 description 2
- 102000004196 processed proteins & peptides Human genes 0.000 description 2
- 229960000380 propiolactone Drugs 0.000 description 2
- 230000000717 retained effect Effects 0.000 description 2
- 235000009566 rice Nutrition 0.000 description 2
- 229920006395 saturated elastomer Polymers 0.000 description 2
- 238000011218 seed culture Methods 0.000 description 2
- 238000000926 separation method Methods 0.000 description 2
- 238000002864 sequence alignment Methods 0.000 description 2
- 239000007787 solid Substances 0.000 description 2
- 230000028070 sporulation Effects 0.000 description 2
- 239000005720 sucrose Substances 0.000 description 2
- 238000011282 treatment Methods 0.000 description 2
- 210000003812 trophozoite Anatomy 0.000 description 2
- 230000004584 weight gain Effects 0.000 description 2
- 235000019786 weight gain Nutrition 0.000 description 2
- 230000004580 weight loss Effects 0.000 description 2
- ASWBNKHCZGQVJV-UHFFFAOYSA-N (3-hexadecanoyloxy-2-hydroxypropyl) 2-(trimethylazaniumyl)ethyl phosphate Chemical compound CCCCCCCCCCCCCCCC(=O)OCC(O)COP([O-])(=O)OCC[N+](C)(C)C ASWBNKHCZGQVJV-UHFFFAOYSA-N 0.000 description 1
- 108091032973 (ribonucleotides)n+m Proteins 0.000 description 1
- 102000040650 (ribonucleotides)n+m Human genes 0.000 description 1
- FJLUATLTXUNBOT-UHFFFAOYSA-N 1-Hexadecylamine Chemical compound CCCCCCCCCCCCCCCCN FJLUATLTXUNBOT-UHFFFAOYSA-N 0.000 description 1
- FPIPGXGPPPQFEQ-UHFFFAOYSA-N 13-cis retinol Natural products OCC=C(C)C=CC=C(C)C=CC1=C(C)CCCC1(C)C FPIPGXGPPPQFEQ-UHFFFAOYSA-N 0.000 description 1
- 108020004463 18S ribosomal RNA Proteins 0.000 description 1
- MGADZUXDNSDTHW-UHFFFAOYSA-N 2H-pyran Chemical compound C1OC=CC=C1 MGADZUXDNSDTHW-UHFFFAOYSA-N 0.000 description 1
- GNMSJGSGAXHQRC-UHFFFAOYSA-N 3,3-diamino-2-methylpropan-1-ol Chemical compound OCC(C)C(N)N GNMSJGSGAXHQRC-UHFFFAOYSA-N 0.000 description 1
- AWIGZBIWTRYADH-UHFFFAOYSA-N 3-methoxynonadecane-1,2,3-triol Chemical compound CCCCCCCCCCCCCCCCC(O)(OC)C(O)CO AWIGZBIWTRYADH-UHFFFAOYSA-N 0.000 description 1
- OPIFSICVWOWJMJ-AEOCFKNESA-N 5-bromo-4-chloro-3-indolyl beta-D-galactoside Chemical compound O[C@@H]1[C@@H](O)[C@@H](O)[C@@H](CO)O[C@H]1OC1=CNC2=CC=C(Br)C(Cl)=C12 OPIFSICVWOWJMJ-AEOCFKNESA-N 0.000 description 1
- 108010042708 Acetylmuramyl-Alanyl-Isoglutamine Proteins 0.000 description 1
- 235000010585 Ammi visnaga Nutrition 0.000 description 1
- 244000153158 Ammi visnaga Species 0.000 description 1
- 208000031295 Animal disease Diseases 0.000 description 1
- 241000283690 Bos taurus Species 0.000 description 1
- 241000252983 Caecum Species 0.000 description 1
- ZAMOUSCENKQFHK-UHFFFAOYSA-N Chlorine atom Chemical compound [Cl] ZAMOUSCENKQFHK-UHFFFAOYSA-N 0.000 description 1
- 102000004127 Cytokines Human genes 0.000 description 1
- 108090000695 Cytokines Proteins 0.000 description 1
- 238000007400 DNA extraction Methods 0.000 description 1
- 238000009007 Diagnostic Kit Methods 0.000 description 1
- 241000499566 Eimeria brunetti Species 0.000 description 1
- 241000196324 Embryophyta Species 0.000 description 1
- 108010067770 Endopeptidase K Proteins 0.000 description 1
- 229920001503 Glucan Polymers 0.000 description 1
- WQZGKKKJIJFFOK-GASJEMHNSA-N Glucose Natural products OC[C@H]1OC(O)[C@H](O)[C@@H](O)[C@@H]1O WQZGKKKJIJFFOK-GASJEMHNSA-N 0.000 description 1
- 206010024264 Lethargy Diseases 0.000 description 1
- 239000006137 Luria-Bertani broth Substances 0.000 description 1
- 229920000057 Mannan Polymers 0.000 description 1
- 206010061298 Mucosal haemorrhage Diseases 0.000 description 1
- FFDGPVCHZBVARC-UHFFFAOYSA-N N,N-dimethylglycine Chemical compound CN(C)CC(O)=O FFDGPVCHZBVARC-UHFFFAOYSA-N 0.000 description 1
- REYJJPSVUYRZGE-UHFFFAOYSA-N Octadecylamine Chemical compound CCCCCCCCCCCCCCCCCCN REYJJPSVUYRZGE-UHFFFAOYSA-N 0.000 description 1
- 238000009004 PCR Kit Methods 0.000 description 1
- 238000002944 PCR assay Methods 0.000 description 1
- 235000019483 Peanut oil Nutrition 0.000 description 1
- 102100029251 Phagocytosis-stimulating peptide Human genes 0.000 description 1
- 239000004698 Polyethylene Substances 0.000 description 1
- 208000035415 Reinfection Diseases 0.000 description 1
- BUGBHKTXTAQXES-UHFFFAOYSA-N Selenium Chemical compound [Se] BUGBHKTXTAQXES-UHFFFAOYSA-N 0.000 description 1
- 230000024932 T cell mediated immunity Effects 0.000 description 1
- 241001314440 Triphora trianthophoros Species 0.000 description 1
- 108010084754 Tuftsin Proteins 0.000 description 1
- 241000700605 Viruses Species 0.000 description 1
- FPIPGXGPPPQFEQ-BOOMUCAASA-N Vitamin A Natural products OC/C=C(/C)\C=C\C=C(\C)/C=C/C1=C(C)CCCC1(C)C FPIPGXGPPPQFEQ-BOOMUCAASA-N 0.000 description 1
- 229930003779 Vitamin B12 Natural products 0.000 description 1
- 229930003427 Vitamin E Natural products 0.000 description 1
- UZQJVUCHXGYFLQ-AYDHOLPZSA-N [(2s,3r,4s,5r,6r)-4-[(2s,3r,4s,5r,6r)-4-[(2r,3r,4s,5r,6r)-4-[(2s,3r,4s,5r,6r)-3,5-dihydroxy-6-(hydroxymethyl)-4-[(2s,3r,4s,5s,6r)-3,4,5-trihydroxy-6-(hydroxymethyl)oxan-2-yl]oxyoxan-2-yl]oxy-3,5-dihydroxy-6-(hydroxymethyl)oxan-2-yl]oxy-3,5-dihydroxy-6-(hy Chemical compound O([C@H]1[C@H](O)[C@@H](CO)O[C@H]([C@@H]1O)O[C@H]1[C@H](O)[C@@H](CO)O[C@H]([C@@H]1O)O[C@H]1CC[C@]2(C)[C@H]3CC=C4[C@@]([C@@]3(CC[C@H]2[C@@]1(C=O)C)C)(C)CC(O)[C@]1(CCC(CC14)(C)C)C(=O)O[C@H]1[C@@H]([C@@H](O[C@H]2[C@@H]([C@@H](O[C@H]3[C@@H]([C@@H](O[C@H]4[C@@H]([C@@H](O[C@H]5[C@@H]([C@@H](O)[C@H](O)[C@@H](CO)O5)O)[C@H](O)[C@@H](CO)O4)O)[C@H](O)[C@@H](CO)O3)O)[C@H](O)[C@@H](CO)O2)O)[C@H](O)[C@@H](CO)O1)O)[C@@H]1O[C@H](CO)[C@@H](O)[C@H](O)[C@H]1O UZQJVUCHXGYFLQ-AYDHOLPZSA-N 0.000 description 1
- 230000004913 activation Effects 0.000 description 1
- 230000001154 acute effect Effects 0.000 description 1
- 230000000240 adjuvant effect Effects 0.000 description 1
- FPIPGXGPPPQFEQ-OVSJKPMPSA-N all-trans-retinol Chemical compound OC\C=C(/C)\C=C\C=C(/C)\C=C\C1=C(C)CCCC1(C)C FPIPGXGPPPQFEQ-OVSJKPMPSA-N 0.000 description 1
- AZDRQVAHHNSJOQ-UHFFFAOYSA-N alumane Chemical class [AlH3] AZDRQVAHHNSJOQ-UHFFFAOYSA-N 0.000 description 1
- WNROFYMDJYEPJX-UHFFFAOYSA-K aluminium hydroxide Chemical compound [OH-].[OH-].[OH-].[Al+3] WNROFYMDJYEPJX-UHFFFAOYSA-K 0.000 description 1
- ILRRQNADMUWWFW-UHFFFAOYSA-K aluminium phosphate Chemical compound O1[Al]2OP1(=O)O2 ILRRQNADMUWWFW-UHFFFAOYSA-K 0.000 description 1
- 230000036528 appetite Effects 0.000 description 1
- 235000019789 appetite Nutrition 0.000 description 1
- 238000013459 approach Methods 0.000 description 1
- 238000003556 assay Methods 0.000 description 1
- 229940031567 attenuated vaccine Drugs 0.000 description 1
- 230000003115 biocidal effect Effects 0.000 description 1
- 230000015572 biosynthetic process Effects 0.000 description 1
- 239000007844 bleaching agent Substances 0.000 description 1
- 210000001124 body fluid Anatomy 0.000 description 1
- 239000010839 body fluid Substances 0.000 description 1
- 230000037396 body weight Effects 0.000 description 1
- 210000004556 brain Anatomy 0.000 description 1
- 230000005587 bubbling Effects 0.000 description 1
- 239000007853 buffer solution Substances 0.000 description 1
- 239000002775 capsule Substances 0.000 description 1
- FPPNZSSZRUTDAP-UWFZAAFLSA-N carbenicillin Chemical compound N([C@H]1[C@H]2SC([C@@H](N2C1=O)C(O)=O)(C)C)C(=O)C(C(O)=O)C1=CC=CC=C1 FPPNZSSZRUTDAP-UWFZAAFLSA-N 0.000 description 1
- 229960003669 carbenicillin Drugs 0.000 description 1
- 150000001720 carbohydrates Chemical class 0.000 description 1
- 235000014633 carbohydrates Nutrition 0.000 description 1
- 230000006037 cell lysis Effects 0.000 description 1
- 210000002421 cell wall Anatomy 0.000 description 1
- 230000008859 change Effects 0.000 description 1
- 239000000460 chlorine Substances 0.000 description 1
- 229910052801 chlorine Inorganic materials 0.000 description 1
- 239000013599 cloning vector Substances 0.000 description 1
- FDJOLVPMNUYSCM-WZHZPDAFSA-L cobalt(3+);[(2r,3s,4r,5s)-5-(5,6-dimethylbenzimidazol-1-yl)-4-hydroxy-2-(hydroxymethyl)oxolan-3-yl] [(2r)-1-[3-[(1r,2r,3r,4z,7s,9z,12s,13s,14z,17s,18s,19r)-2,13,18-tris(2-amino-2-oxoethyl)-7,12,17-tris(3-amino-3-oxopropyl)-3,5,8,8,13,15,18,19-octamethyl-2 Chemical compound [Co+3].N#[C-].N([C@@H]([C@]1(C)[N-]\C([C@H]([C@@]1(CC(N)=O)C)CCC(N)=O)=C(\C)/C1=N/C([C@H]([C@@]1(CC(N)=O)C)CCC(N)=O)=C\C1=N\C([C@H](C1(C)C)CCC(N)=O)=C/1C)[C@@H]2CC(N)=O)=C\1[C@]2(C)CCC(=O)NC[C@@H](C)OP([O-])(=O)O[C@H]1[C@@H](O)[C@@H](N2C3=CC(C)=C(C)C=C3N=C2)O[C@@H]1CO FDJOLVPMNUYSCM-WZHZPDAFSA-L 0.000 description 1
- 230000000295 complement effect Effects 0.000 description 1
- 239000012141 concentrate Substances 0.000 description 1
- 239000000356 contaminant Substances 0.000 description 1
- 230000001186 cumulative effect Effects 0.000 description 1
- 238000007405 data analysis Methods 0.000 description 1
- 229940009976 deoxycholate Drugs 0.000 description 1
- KXGVEGMKQFWNSR-LLQZFEROSA-N deoxycholic acid Chemical compound C([C@H]1CC2)[C@H](O)CC[C@]1(C)[C@@H]1[C@@H]2[C@@H]2CC[C@H]([C@@H](CCC(O)=O)C)[C@@]2(C)[C@@H](O)C1 KXGVEGMKQFWNSR-LLQZFEROSA-N 0.000 description 1
- 229960000633 dextran sulfate Drugs 0.000 description 1
- 239000008121 dextrose Substances 0.000 description 1
- UGMCXQCYOVCMTB-UHFFFAOYSA-K dihydroxy(stearato)aluminium Chemical compound CCCCCCCCCCCCCCCCCC(=O)O[Al](O)O UGMCXQCYOVCMTB-UHFFFAOYSA-K 0.000 description 1
- PSLWZOIUBRXAQW-UHFFFAOYSA-M dimethyl(dioctadecyl)azanium;bromide Chemical compound [Br-].CCCCCCCCCCCCCCCCCC[N+](C)(C)CCCCCCCCCCCCCCCCCC PSLWZOIUBRXAQW-UHFFFAOYSA-M 0.000 description 1
- 108700003601 dimethylglycine Proteins 0.000 description 1
- 229940079593 drug Drugs 0.000 description 1
- 229920001971 elastomer Polymers 0.000 description 1
- 239000002158 endotoxin Substances 0.000 description 1
- ZMMJGEGLRURXTF-UHFFFAOYSA-N ethidium bromide Chemical compound [Br-].C12=CC(N)=CC=C2C2=CC=C(N)C=C2[N+](CC)=C1C1=CC=CC=C1 ZMMJGEGLRURXTF-UHFFFAOYSA-N 0.000 description 1
- 229960005542 ethidium bromide Drugs 0.000 description 1
- 230000002349 favourable effect Effects 0.000 description 1
- 210000003746 feather Anatomy 0.000 description 1
- 230000035558 fertility Effects 0.000 description 1
- 239000012530 fluid Substances 0.000 description 1
- 230000002538 fungal effect Effects 0.000 description 1
- 230000004927 fusion Effects 0.000 description 1
- WIGCFUFOHFEKBI-UHFFFAOYSA-N gamma-tocopherol Natural products CC(C)CCCC(C)CCCC(C)CCCC1CCC2C(C)C(O)C(C)C(C)C2O1 WIGCFUFOHFEKBI-UHFFFAOYSA-N 0.000 description 1
- 238000003304 gavage Methods 0.000 description 1
- 230000002068 genetic effect Effects 0.000 description 1
- 239000011521 glass Substances 0.000 description 1
- 230000036541 health Effects 0.000 description 1
- 239000005556 hormone Substances 0.000 description 1
- 229940088597 hormone Drugs 0.000 description 1
- 238000009396 hybridization Methods 0.000 description 1
- 238000013095 identification testing Methods 0.000 description 1
- 230000001900 immune effect Effects 0.000 description 1
- 210000000987 immune system Anatomy 0.000 description 1
- 230000006058 immune tolerance Effects 0.000 description 1
- 238000003018 immunoassay Methods 0.000 description 1
- 230000002163 immunogen Effects 0.000 description 1
- 230000003308 immunostimulating effect Effects 0.000 description 1
- 230000001524 infective effect Effects 0.000 description 1
- 239000003999 initiator Substances 0.000 description 1
- 238000002347 injection Methods 0.000 description 1
- 239000007924 injection Substances 0.000 description 1
- 238000003780 insertion Methods 0.000 description 1
- 230000037431 insertion Effects 0.000 description 1
- 208000028774 intestinal disease Diseases 0.000 description 1
- 210000002490 intestinal epithelial cell Anatomy 0.000 description 1
- 210000004347 intestinal mucosa Anatomy 0.000 description 1
- 230000003834 intracellular effect Effects 0.000 description 1
- 238000007918 intramuscular administration Methods 0.000 description 1
- 238000007912 intraperitoneal administration Methods 0.000 description 1
- 238000001990 intravenous administration Methods 0.000 description 1
- 229920006008 lipopolysaccharide Polymers 0.000 description 1
- 239000007788 liquid Substances 0.000 description 1
- 244000144972 livestock Species 0.000 description 1
- 238000005259 measurement Methods 0.000 description 1
- 239000013028 medium composition Substances 0.000 description 1
- 230000005001 merogony Effects 0.000 description 1
- 239000004005 microsphere Substances 0.000 description 1
- 238000012544 monitoring process Methods 0.000 description 1
- 230000003843 mucus production Effects 0.000 description 1
- BSOQXXWZTUDTEL-ZUYCGGNHSA-N muramyl dipeptide Chemical compound OC(=O)CC[C@H](C(N)=O)NC(=O)[C@H](C)NC(=O)[C@@H](C)O[C@H]1[C@H](O)[C@@H](CO)O[C@@H](O)[C@@H]1NC(C)=O BSOQXXWZTUDTEL-ZUYCGGNHSA-N 0.000 description 1
- 238000002703 mutagenesis Methods 0.000 description 1
- 231100000350 mutagenesis Toxicity 0.000 description 1
- 230000007935 neutral effect Effects 0.000 description 1
- 108091027963 non-coding RNA Proteins 0.000 description 1
- 238000003305 oral gavage Methods 0.000 description 1
- 230000003071 parasitic effect Effects 0.000 description 1
- 231100000255 pathogenic effect Toxicity 0.000 description 1
- 230000036285 pathological change Effects 0.000 description 1
- 231100000915 pathological change Toxicity 0.000 description 1
- 230000004796 pathophysiological change Effects 0.000 description 1
- 239000000312 peanut oil Substances 0.000 description 1
- 239000008188 pellet Substances 0.000 description 1
- 210000003899 penis Anatomy 0.000 description 1
- 239000000825 pharmaceutical preparation Substances 0.000 description 1
- 229940127557 pharmaceutical product Drugs 0.000 description 1
- 230000019612 pigmentation Effects 0.000 description 1
- 238000007747 plating Methods 0.000 description 1
- 229920001983 poloxamer Polymers 0.000 description 1
- 239000004584 polyacrylic acid Substances 0.000 description 1
- 229920000447 polyanionic polymer Polymers 0.000 description 1
- 229920000573 polyethylene Polymers 0.000 description 1
- 229920000642 polymer Polymers 0.000 description 1
- 229920005862 polyol Polymers 0.000 description 1
- 150000003077 polyols Chemical class 0.000 description 1
- 239000000843 powder Substances 0.000 description 1
- 238000002360 preparation method Methods 0.000 description 1
- 230000002265 prevention Effects 0.000 description 1
- 238000011321 prophylaxis Methods 0.000 description 1
- 230000001681 protective effect Effects 0.000 description 1
- 102000004169 proteins and genes Human genes 0.000 description 1
- 244000000040 protozoan parasite Species 0.000 description 1
- 239000011541 reaction mixture Substances 0.000 description 1
- 238000010188 recombinant method Methods 0.000 description 1
- 238000005057 refrigeration Methods 0.000 description 1
- 230000004044 response Effects 0.000 description 1
- 230000000284 resting effect Effects 0.000 description 1
- 229930182490 saponin Natural products 0.000 description 1
- 150000007949 saponins Chemical class 0.000 description 1
- 235000017709 saponins Nutrition 0.000 description 1
- 238000004062 sedimentation Methods 0.000 description 1
- 235000011649 selenium Nutrition 0.000 description 1
- 229910052711 selenium Inorganic materials 0.000 description 1
- 239000011669 selenium Substances 0.000 description 1
- 229940091258 selenium supplement Drugs 0.000 description 1
- 230000035945 sensitivity Effects 0.000 description 1
- 239000010802 sludge Substances 0.000 description 1
- 239000011780 sodium chloride Substances 0.000 description 1
- 239000002689 soil Substances 0.000 description 1
- 239000011343 solid material Substances 0.000 description 1
- 239000008223 sterile water Substances 0.000 description 1
- 230000001954 sterilising effect Effects 0.000 description 1
- 238000004659 sterilization and disinfection Methods 0.000 description 1
- 238000007920 subcutaneous administration Methods 0.000 description 1
- 239000004094 surface-active agent Substances 0.000 description 1
- 238000003786 synthesis reaction Methods 0.000 description 1
- 101150075675 tatC gene Proteins 0.000 description 1
- 230000000451 tissue damage Effects 0.000 description 1
- 231100000827 tissue damage Toxicity 0.000 description 1
- IESDGNYHXIOKRW-LEOABGAYSA-N tuftsin Chemical compound C[C@@H](O)[C@H](N)C(=O)N[C@@H](CCCCN)C(=O)N1CCC[C@H]1C(=O)N[C@H](CCCNC(N)=N)C(O)=O IESDGNYHXIOKRW-LEOABGAYSA-N 0.000 description 1
- 229940035670 tuftsin Drugs 0.000 description 1
- 230000003966 vascular damage Effects 0.000 description 1
- 239000013598 vector Substances 0.000 description 1
- 230000001018 virulence Effects 0.000 description 1
- 239000011782 vitamin Substances 0.000 description 1
- 229930003231 vitamin Natural products 0.000 description 1
- 235000013343 vitamin Nutrition 0.000 description 1
- 229940088594 vitamin Drugs 0.000 description 1
- 235000019155 vitamin A Nutrition 0.000 description 1
- 239000011719 vitamin A Substances 0.000 description 1
- 235000019163 vitamin B12 Nutrition 0.000 description 1
- 239000011715 vitamin B12 Substances 0.000 description 1
- 235000019165 vitamin E Nutrition 0.000 description 1
- 229940046009 vitamin E Drugs 0.000 description 1
- 239000011709 vitamin E Substances 0.000 description 1
- 229940045997 vitamin a Drugs 0.000 description 1
- 238000003260 vortexing Methods 0.000 description 1
- 238000005406 washing Methods 0.000 description 1
- 230000003313 weakening effect Effects 0.000 description 1
- 230000003442 weekly effect Effects 0.000 description 1
- NWONKYPBYAMBJT-UHFFFAOYSA-L zinc sulfate Chemical compound [Zn+2].[O-]S([O-])(=O)=O NWONKYPBYAMBJT-UHFFFAOYSA-L 0.000 description 1
- 229960001763 zinc sulfate Drugs 0.000 description 1
- 229910000368 zinc sulfate Inorganic materials 0.000 description 1
Images
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
- C12Q1/6888—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for detection or identification of organisms
- C12Q1/6893—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for detection or identification of organisms for protozoa
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K39/00—Medicinal preparations containing antigens or antibodies
- A61K39/002—Protozoa antigens
- A61K39/012—Coccidia antigens
-
- C—CHEMISTRY; METALLURGY
- C07—ORGANIC CHEMISTRY
- C07K—PEPTIDES
- C07K14/00—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof
- C07K14/435—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans
- C07K14/44—Peptides having more than 20 amino acids; Gastrins; Somatostatins; Melanotropins; Derivatives thereof from animals; from humans from protozoa
- C07K14/455—Eimeria
-
- A—HUMAN NECESSITIES
- A61—MEDICAL OR VETERINARY SCIENCE; HYGIENE
- A61K—PREPARATIONS FOR MEDICAL, DENTAL OR TOILETRY PURPOSES
- A61K39/00—Medicinal preparations containing antigens or antibodies
- A61K2039/55—Medicinal preparations containing antigens or antibodies characterised by the host/recipient, e.g. newborn with maternal antibodies
- A61K2039/552—Veterinary vaccine
-
- Y—GENERAL TAGGING OF NEW TECHNOLOGICAL DEVELOPMENTS; GENERAL TAGGING OF CROSS-SECTIONAL TECHNOLOGIES SPANNING OVER SEVERAL SECTIONS OF THE IPC; TECHNICAL SUBJECTS COVERED BY FORMER USPC CROSS-REFERENCE ART COLLECTIONS [XRACs] AND DIGESTS
- Y02—TECHNOLOGIES OR APPLICATIONS FOR MITIGATION OR ADAPTATION AGAINST CLIMATE CHANGE
- Y02A—TECHNOLOGIES FOR ADAPTATION TO CLIMATE CHANGE
- Y02A40/00—Adaptation technologies in agriculture, forestry, livestock or agroalimentary production
- Y02A40/70—Adaptation technologies in agriculture, forestry, livestock or agroalimentary production in livestock or poultry
Landscapes
- Chemical & Material Sciences (AREA)
- Health & Medical Sciences (AREA)
- Life Sciences & Earth Sciences (AREA)
- Organic Chemistry (AREA)
- Proteomics, Peptides & Aminoacids (AREA)
- General Health & Medical Sciences (AREA)
- Analytical Chemistry (AREA)
- Zoology (AREA)
- Biochemistry (AREA)
- Tropical Medicine & Parasitology (AREA)
- Immunology (AREA)
- Microbiology (AREA)
- Molecular Biology (AREA)
- Engineering & Computer Science (AREA)
- Wood Science & Technology (AREA)
- Biophysics (AREA)
- Medicinal Chemistry (AREA)
- Genetics & Genomics (AREA)
- Mycology (AREA)
- Public Health (AREA)
- Bioinformatics & Cheminformatics (AREA)
- Toxicology (AREA)
- Gastroenterology & Hepatology (AREA)
- Physics & Mathematics (AREA)
- Epidemiology (AREA)
- Pharmacology & Pharmacy (AREA)
- Biotechnology (AREA)
- Animal Behavior & Ethology (AREA)
- General Engineering & Computer Science (AREA)
- Veterinary Medicine (AREA)
- Medicines Containing Antibodies Or Antigens For Use As Internal Diagnostic Agents (AREA)
- Measuring Or Testing Involving Enzymes Or Micro-Organisms (AREA)
Abstract
COMPOSIQAO DE VACINA, USO DE UMA VACINA, PAR DE OLIGONUCLEOTIDEO INICIADOR DE REAQAO EM CADEIA DA POLIMERASE, KIT DE AMPLIFICAQAO DE PCR, E, METODOS DE IDENTIFICAR UM ISOLADO DE EIMERIA COMO E. MELEAGRIMITIS 2, MELEAGRIMITIS 2 EM UMA AMOSTRA BIOLOGICA, E AS ESPECIES DE EIMERIA PATOGENICA NO PERU PRESENTE EM UMA AMOSTRA BIOLOGICA A presente invengSo revela uma vacina que fornece protegSo a perus contra coccidiose, e mStodos de preparar e usar a vacina sozinha, ou em combinagbes com outros agentes protetores. Alem do mais, a presente invenção revela conjuntos de oligonucleotideo iniciador para PCR que sao usados para identificar cis especies de Eimeria em uma amostra biologica.
Description
[0001] Este pedido reivindica a prioridade em 35 U.S.C. § 119(e) do pedido provisorio US numero de serie 61/114.208, depositado em 13 de novembro de 2008.
[0002] A presente invenção diz respeito a uma vacina para penis que fornece protegao contra coccidiose. Os metodos de preparar e usar a vacina sozinha, ou em combinagoes com outros agentes protetores, tambem sao fornecidos. Alem do mais, a presente invenção fornece conjuntos de oligonucleotfdeo iniciador para PCR que sao usados para identificar especies patogenicas de Eimeria em peru.
[0003] A coccidiose e uma doenga enterica de animais que aflige aves domesticas e gado em todo o mundo. Os negocios que dependem da produgao animal encaram frequentemente custos significativos em decorrencia da coccidiose, incluindo perdas financeiras em virtude do gado doente, bem como os gastos com os tratamentos profilaticos cujo objetivo e reduzir e/ou prevenir a doenga. Tais custos sao especialmente relevantes nas industrias intensivas comerciais e de animal, tai como a industria de aves, onde o alojamento intensive de passaros favorece a dispersao da coccidiose.
[0004] Elementos da subclasse de esporozoarios intracelulares obrigatorios, Coccidia, sao o agente etiologico da coccidiose. Um genero de Coccidia, Eimeria, apresenta um impacto significative na produgao animal. Assim como para os generos muito relacionados Isospora, Cyclospora (Cystoisospord) e Cryptosporidium, Eimeria exige apenas um unico hospedeiro para completar seu ciclo de vida. Em condigoes naturais, este ciclo de vida comega com a ingestao de oocistos esporulados a partir do ambiente.
[0005] Eimeria sao parasitas unicelulares com um ciclo de vida complexo monoxeno, que exibem um alto grau tanto de especies hospedeiras quanto da especificidade tecidual. Especies de Eimeria incluem aquelas que sao observadas em galinhas: E. tenella, E. acervulina, E. maxima, E. necatrix, E. mitis, E. praecox, E. mivati, E. hagani e E. brunetti, e aquelas observadas em perus: E. meleagrimitis 1 (ate o momento conhecida simplesmente como E. meleagrimitis), E. adenoeides, E. gallopavonis, E. dispersa, E. meleagridis, E. innocua e E. subrotunda.
[0006] No campo da coccidiose aviaria, o numero de pesquisa de Coccidia em peru nao e ample em decorrencia do numero de pesquisa realizada em galinhas. De fato, em todo o mundo, ao passo que existem apenas duas vacinas contra Coccidia em peru disponiveis comercialmente (Coccivac-T®, usada pela primeira vez nos anos 60 e Immucox®, usada pela primeira vez nos anos 80), existem aproximadamente uma duzia de vacinas contra Coccidia em galinha. Portanto, existe uma necessidade particularmente acentuada de vacinas adicionais e melhores que podem fornecer protegao para perus contra a coccidiose aviaria.
[0007] Varias especies de Eimeria podem infectar um unico hospedeiro por meio da via oral, via nasal e/ou pela entrada das partfculas infecciosas no duto lacrimal. Uma vez ingeridos, os parasitas penetram nas celulas da mucosa intestinal e passam por estagios assexual e sexual do ciclo de vida. O dano intestinal resultante pode levar por fim ao retardo do crescimento (nanismo), menos utilizagao do alimento, perda de pigmentagao e aumento da mortalidade. Alem do mais, o dano ao revestimento intestinal pode predispor perus a outros agentes infecciosos.
[0008] Os estagios do ciclo de vida de Eimeria sao essencialmente os mesmos para todas as especies Eimeria, embora cada especie apreesente um sitio preferido no intestino para o desenvolvimento e o tempo exigido para completar o ciclo de vida varia de especie para especie. A infeegao comega com ingestao por um hospedeiro de oocistos esporulados de Eimeria. Os oocistos ingeridos liberam entao esporocistos no intestino do hospedeiro. Os esporocistos liberam esporozoitas que entram nas celulas epiteliais intestinais e transformam-se entao em trofozoitas. Os trofozoitas, ao contrario, passarn por um processo conhecido como merogonia para formar a primeira geragao de esquizontes. Em virtude dos esquizontes relativamente grandes, tais como no caso de E. necatrix ou E. tenella, ou do numero excessivo do esquizontes, tai como E. mivati, ou dos grandes gamontes como no caso de E. maxima, estes sao os estagios que causam o principal efeito patogenico da infecgao, isto e, o dano tecidual no hospedeiro.
[0009] Os esquizontes de primeira geragao maduros produzem varios merozoftas que sao liberados e invadem novas celulas epiteliais, e entao crescem e formam os esquizontes da proxima geragao. Estas fases assexuais continuam por inumeras geragoes antes do comego da fase sexual. A fase sexual comega quando os esquizontes se desenvolvem nos gamontes; microgamontes e macrogamontes. Os microgamontes desenvolvem-se subsequentemente em microgametas que fertilizam os macrogamontes para produzir progenie de oocisto nao esporulado. Os oocistos nao esporulados sao entao liberados no lumen intestinal e excretados com as fezes do hospedeiro. A conclusao do ciclo de vida endogeno, anunciado pelo aparecimento de oocistos nao esporulados nas fezes do hospedeiro, e conhecido como patencia.
[0010] A esporulagao dos oocistos ocorre fora do hospedeiro, quando as condigoes ambientais sao favoraveis. A ingestao inevitavel por um hospedeiro dos oocistos esporulados comega no proximo ciclo de infecgao. O periodo da ingestao pelo hospedeiro dos oocistos esporulados ate o aparecimento dos oocistos nao esporulados nas fezes e denominado o periodo pre-patente. O periodo pre-patente difere entre as varias especies de Eimeria.
[0011] Aves que que sao repetidamente expostas a infecgoes por Eimeria podem adquirir imunidade a coccidiose. De fato, dependendo da imunogenicidade de cada especie de Eimeria, a infeegao diaria de perus com poucos oocistos esporulados pode resultar nos passaros que adquirem imunidade total apos apenas duas infecgoes repetidas. Consequentemente, os protocolos atuais que empregam vacinas com Eimeria viva baseiam-se no prinefpio da imunidade adquirida, isto e, infecgoes repetidas com um pequeno numero de oocistos infectivos.
[0012] A vacinagao e realizada em geral no viveiro no dia do nascimento da ave administrando a vacina contra Eimeria viva por meio de uma aplicagao por aspersao (diretamente nos passaros). A ingestao dos oocistos esporulados durante o alisamento normal das penas resulta entao em uma inoculagao oral da vacina. Alternativamente, ou em conjunto, as vacinas podem ser aplicadas em uma data posterior na ragao e/ou agua. Os oocistos infectivos completam seu ciclo de vida dentro do trato intestinal do passaro, da maneira descrita anteriormente, culminando com a liberagao de uma nova geragao de oocistos nao esporulados em 5 a 11 dias, dependendo das especies de Eimeria. Os oocistos nao esporulados excretados com as fezes se tomam entao infectivos, isto e, esporulam fora do hospedeiro, e re-infectam os passaros por meio da ingestao do hospedeiro. Apos dois ou tres tais ciclos, os passaros se tomam imunizados contra as especies de Coccidia, as quais eles foram previamente expostos. Esta imunidade e caracterizada por protegao contra a doenga ou agentes infecciosos da maneira determinada por: (i) uma diminuigao e/ou ausencia de parasitas observados microscopicamente no intestino, (ii) uma redugao da mudanga dos oocistos, (iii) uma redugao das lesoes intestinais, (iv) uma redugao da doenga cimica, (v) uma redugao ou prevengao da perda de peso, e/ou (vi) uma redugao no enfraquecimento da eficiencia da utilizagao da ragao. A imunidade adquirida diminui com o tempo na ausencia da exposigao subsequente aos oocistos infectivos.
[0013] Eimeria tipo selvagem e em geral isolada de epidemias de doenga clmica em grupos de aves e pode ser propagada para uso as cepas de desafio patogenico. As vacinas nao atenuadas tfpicas sao compostas de oocistos infectivos a partir de cepas pouco a moderadamente patogenicas de diferentes especies de Eimeria que foram mantidas em laboratorio. Estas especies de Eimeria nao atenuadas sao capazes de causar coccidiose quando ingeridas em numeros muito elevados. Os comerciantes e usuarios da vacina devem ter cuidado para assegurar que a vacinagao fomega apenas oocistos infectivos suficientes para obter imunidade, mas nao a doenga no hospedeiro natural. Apos a dose initial, o processo de vacinagao conta apenas com a reinfecgao por meio da ingestao do hospedeiro dos oocistos esporulados nos detritos.
[0014] A patogenicidade, patologia e sinais clmicos para coccidiose nos perus podem ser caracteristicas para cada especie de Eimeria. As especies de Eimeria isoladas em geral de perus comerciais de fazenda sao E. adenoeides, E. meleagrimitis 1, E. dispersa, e E. gallopavonis; as quatro especies de Coccidia que, ate o momento, foram consideradas patogenicas apenas em especies de Eimeria em peru. E. adenoeides e E. gallopavonis parasitam principalmente o ceco e reto e, em muitos casos, a menor porgao do fleo. Ao contrario, E. dispersa e E. meleagrimitis 1 parasitam o intestino delgado com o parasitismo que se aloja principalmente no intestino delgado superior e medio. Mudangas fisiopatologicas, tais como maior perda de agua por meio das fezes, maior produgao de muco e/ou perda sangumea em virtude de dano vascular, resultam em menor desempenho, tais como menor taxa de crescimento, de utilizagao de ragao e ainda de mortalidade.
[0015] As epidemias recentes da coccidiose em grupos comerciais de peru demonstram que a existencia de metodos controle nao pode impedir sozinho as infecgoes de Eimeria. De fato, em vista da necessidade do bom controle dos produtos farmaceuticos e ou vacinas para neutralizar tais infecgoes por Eimeria, permanece uma necessidade d elonga data com relagao a novas e/ou melhores vacinas que podem proteger melhor perus desta doenga enterica dispendiosa.
[0016] A citagao de qualquer referencia aqui nao pode ser interpretada como uma admissao, de maneira tai que a referencia e disponfvel como "tecnica anterior" ao presente pedido.
[0017] Dessa maneira, a presente invenção fornece novas composigoes imunogenicas que compreendem uma ou mais especies de Eimeria que podem ajudar na protegao de perus contra a coccidiose. Em um aspecto da presente invenção, e fornecida uma vacina que compreende E. meleagrimitis 2 (tambem referida como E edgar) e E. meleagrimitis 1. Em uma modalidade particular deste tipo, a vacina compreende adicionalmente uma ou mais especies adicionais de Eimeria selecionadas do grupo que consiste em E. adenoeides, E. gallopavonis, E. dispersa, E. innocua e E. subrotunda. Em uma modalidade particular, a especie adicional de Eimeria e E adenoeides. Em uma outra modalidade, a especie adicional de Eimeria e E. gallopavonis. Ainda em uma outra modalidade, a especie adicional de Eimeria e E. dispersa. Mesmo em uma outra modalidade, a especie adicional de Eimeria e E innocua. Ainda em uma outra modalidade, a especie adicional de Eimeria & E subrotunda. Sao tambem fomecidas vacinas que compreendem qualquer e todas as combinagoes de tais especies de Eimeria. Alem do mais, sao fomecidas vacinas que compreendem duas ou mais cepas de duas ou mais de tais especies individuals. Em uma modalidade deste tipo, a vacina compreende pares de cepas de multiplas especies de Eimeria, em que multiples pares de cepas de especies unicas de Eimeria possuem penodos prepatentes assmeronos. Em uma modalidade particular deste tipo, todos os pares de cepas de especie unica de Eimeria na vacina possuem penodos prepatentes assmeronos.
[0018] Em um outro aspecto da invenção, sao fornecidos metodos de imunizar um peru contra a coccidiose. Em uma tai modalidade, o metodo de imunizar um peru contra a coccidiose compreende administrar ao peru uma vacina contra E. meleagrimitis 2 que compreende uma quantidade imunologicamente efetiva de E. meleagrimitis 2. Em uma outra modalidade, o metodo compreende adicionalmente administrar ao peru uma ou mais vacinas adicionais contra uma especie de Eimeria sem ser E meleagrimitis 2. Em uma modalidade particular deste tipo, cada vacina adicional compreende uma quantidade imunologicamente efetiva de uma ou mais especies de Eimeria selecionadas do grupo que consiste em E. meleagrimitis 1, E. adenoeides, E. gallopavonis, E. dispersa, E. meleagridis, E. innocua e E. subrotunda. A administragao da vacina contra E. meleagrimitis 2 e a administragao de uma ou mais vacinas adicionais contra uma especie de Eimeria, sem ser E. meleagrimitis 2, podem ser realizadas em qualquer ordem, incluindo simultaneamente em uma administragao multivalente combinada.
[0019] Assim, a presente invenção fomece metodos que compreendem administrar a um peru uma quantidade imunologicamente efetiva de uma ou mais especies de Eimeria no peru em uma vacina da presente invenção. Em uma modalidade particular, uma vacina como esta e administrada por aplicagao por aspersao no peru. Em uma outra modalidade, a vacina e administrada na agua de beber do peru. Ainda em uma outra modalidade, a vacina e administrada na ragao do peru. Mesmo em uma outra modalidade, a vacina e administrada tanto na ragao quanto na agua de beber do peru. Ainda em uma outra modalidade, a vacina e administrada por aplicagao por aspersao no peru, na ragao do peru e/ou na agua de beber.
[0020] Alem do mais, quaisquer das vacinas da presente invenção que compreendam cepas de Eimeria, tambem podem incluir uma ou mais especies e/ou cepas de Isospora, de Cyclospora (Cystoisospora) e/ou de Cryptosporidium. Em uma modalidade particular deste tipo, a(s) cepa(s) das especies de Isospora, de Cyclospora (Cystoisospora) e/ou de Cryptosporidium tambem pode(m) possuir um periodo pre-patente assmcrono.
[0021] A presente invenção fomece adicionalmente metodos de identificar um isolado de Eimeria, tai como E. meleagrimitis 2. Uma tai modalidade compreende comparar a sequencia de nucleotfdeos da regiao ITS1 do genoma do isolado de Eimeria com a sequencia de nucleotfdeos da regiao ITS-1 em SEQ ID NO: 44. O isolado de Eimeria Q identificado como E. meleagrimitis 2 quando a sequencia completa de nucleotfdeos da regiao ITS-1 do genoma do isolado de Eimeria exibe mais de 87 % de homologia com a sequencia completa de nucleotfdeos da regiao ITS-1 em SEQ ID NO: 44. Em uma modalidade particular deste metodo, o isolado de Eimeria e identificado como E. meleagrimitis 2 quando a sequencia completa de nucleotfdeos da regiao ITS-1 do genoma do isolado de Eimeria exibe mais de 95 % de homologia com a sequencia completa de nucleotfdeos da regiao ITS1 em SEQ ID NO: 44. Em uma outra modalidade deste metodo, o isolado de Eimeria € identificado como um E. meleagrimitis 2 quando a sequencia completa de nucleotfdeos da regiao ITS-1 do genoma do isolado de Eimeria exibe 100 % de identidade com a sequencia completa de nucleotfdeos da regiao ITS-1 em SEQ ID NO: 44.
[0022] Em modalidades particulares, a sequencia completa de nucleotfdeos da regiao ITS-1 de SEQ ID NO: 44 contem entre 394 e 409 nucleotfdeos. Em outras tais modalidades, a sequencia completa de nucleotfdeos da regiao ITS-1 de SEQ ID NO: 44 contem entre 400 e 409 nucleotfdeos. Ainda em outras modalidades, a sequencia completa de nucleotfdeos da regiao ITS-1 de SEQ ID NO: 44 contem entre 395 e 400 nucleotfdeos. Mesmo em outras modalidades, a sequencia completa de nucleotfdeos da regiao ITS-1 de SEQ ID NO: 44 contem entre 394 e 398 nucleotfdeos. Ainda em outras modalidades, a sequencia completa de nucleotfdeos da regiao ITS-1 de SEQ ID NO: 44 contem entre 405 e 409 nucleotfdeos. Mesmo em outras modalidades, a sequencia completa de nucleotfdeos da regiao ITS-1 de SEQ ID NO: 44 content 409 nucleotfdeos.
[0023] Em modalidades relacionadas, os metodos compreendem comparar a sequencia de acidos nucleicos da regiao ITS-1 do genoma de um isolado de Eimeria com aquelas identificadas aqui especificamente. Em uma tai modalidade, o metodo compreende comparar a sequencia de acidos nucleicos da regiao ITS-1 do genoma de um isolado de Eimeria com a sequencia de acidos nucleicos da regiao ITS-1 em uma sequencia de nucleotfdeos de SEQ ID NO: 31, SEQ ID NO: 32, SEQ ID NO: 33, SEQ ID NO: 34, e/ou SEQ ID NO: 43. O isolado de Eimeria 6 identificado como E. meleagrimitis 2 quando a sequencia completa de acidos nucleicos da regiao ITS-1 do genoma do isolado de Eimeria exibe mais de 87 % de homologia com a sequencia completa de acidos nucleicos da regiao ITS-1 na sequencia ou sequencias de nucleotfdeos que estao sendo comparadas. Em uma outra tai modalidade, o isolado de Eimeria e identificado como E. meleagrimitis 2 quando a sequencia completa de acidos nucleicos da regiao ITS-1 do genoma do isolado de Eimeria exibe mais de 95 % de homologia com a sequencia completa de acidos nucleicos da regiao ITS-1, que esta na sequencia ou sequencias de nucleotfdeos que estao sendo comparadas. Ainda em uma outra modalidade deste metodo, o isolado de Eimeria e identificado como E. meleagrimitis 2 quando a sequencia completa de nucleotfdeos da regiao ITS-1 do genoma do isolado de Eimeria exibe 100 % de identidade com a sequencia completa de nucleotfdeos da regiao ITS-1 na sequencia de nucleotfdeos que esta sendo comparada. Os alinhamentos da sequencia de nucleotfdeos podem ser realizados com a metodologia de Clustal W da maneira descrita a seguir.
[0024] A presente invenção tambem fornece acidos nucleicos que compreendem respectivamente a sequencia de nucleotfdeos de SEQ ID NO: 13, ou SEQ ID NO: 14, ou SEQ ID NO: 15, ou SEQ ID NO: 16, ou SEQ ID NO: 17, ou SEQ ID NO: 18, ou SEQ ID NO: 19, ou SEQ ID NO: 20, ou SEQ ID NO: 21, ou SEQ ID NO: 22, ou SEQ ID NO: 23, ou SEQ ID NO: 24, ou SEQ ID NO: 25, ou SEQ ID NO: 26, ou SEQ ID NO: 27, ou SEQ ID NO: 28, ou SEQ ID NO: 29, ou SEQ ID NO: 30, ou SEQ ID NO: 31, ou SEQ ID NO: 32, ou SEQ ID NO: 33, ou SEQ ID NO: 34, ou SEQ ID NO: 35, ou SEQ ID NO: 36, ou SEQ ID NO: 37, ou SEQ ID NO: 38, ou SEQ ID NO: 39, ou SEQ ID NO: 40, ou SEQ ID NO: 41, ou SEQ ID NO: 42, ou SEQ ID NO: 43 ou SEQ ID NO: 44. Em uma modalidade particular, um acido nucleico como este compreende nao mais que 800 pares de bases. Em uma outra modalidade, um acido nucleico como este compreende nao mais que 600 pares de bases. Mesmo em uma outra modalidade, um acido nucleico como este compreende nao mais que 500 pares de base. Em uma modalidade relacionada, o acido nucleico pode compreender adicionalmente uma sequencia heterologa de nucleotfdeos.
[0025] A presente invenção fomece adicionalmente acidos nucleicos que compreendem respectivamente a sequencia de nucleotfdeos de SEQ ID NO: 51, ou SEQ ID NO: 52, ou SEQ ID NO: 53, ou SEQ ID NO: 54, ou SEQ ID NO: 55, ou SEQ ID NO: 56, ou SEQ ID NO: 57, ou SEQ ID NO: 58, ou SEQ ID NO: 59, ou SEQ ID NO: 60, ou SEQ ID NO: 61, ou SEQ ID NO: 62, ou SEQ ID NO: 63, ou SEQ ID NO: 64, ou SEQ ID NO: 65, ou SEQ ID NO: 66, ou SEQ ID NO: 67, ou SEQ ID NO: 68, ou SEQ ID NO: 69, ou SEQ ID NO: 70, ou SEQ ID NO: 71, ou SEQ ID NO: 72, ou SEQ ID NO: 73, ou SEQ ID NO: 74, ou SEQ ID NO: 75, ou SEQ ID NO: 76, ou SEQ ID NO: 77, ou SEQ ID NO: 78, ou SEQ ID NO: 79, ou SEQ ID NO: 80 ou SEQ ID NO: 81. Em uma modalidade particular, um acido nucleico como este compreende nao mais que 800 pares de base. Em uma outra modalidade, um acido nucleico como este compreende nao mais que 600 pares de base. Mesmo em uma outra modalidade, um acido nucleico como este compreende nao mais que 500 pares de base. Em uma modalidade relacionada, o acido nucleico pode compreender adicionalmente uma sequencia heterologa de nucleotfdeos.
[0026] A presente invenção tambem fomece um acido nucleico que compreende a sequencia de nucleotfdeos de SEQ ID NO: 3. Em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 4. Mesmo em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 5. Ainda em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 6. Mesmo em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 7. Ainda em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 8. Mesmo em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 9. Ainda em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 10. Mesmo em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 11. Ainda em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 12. Mesmo em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 45. Ainda em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 46. Mesmo em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 47. Ainda em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 48. Mesmo em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 49. Ainda em uma outra modalidade, o acido nucleico compreende a sequencia de nucleotfdeos de SEQ ID NO: 50.
[0027] Tais acidos nucleicos podem ser usados, inter alia, como sodas de hibridizagao ou, alternativamente, como oligonucleotfdeos iniciadores em amplificagoes da reagao em cadeia da polimerase (PCR) para sintetizar produtos de PCR que correspondem as porgoes e/ou todas as regioes de ITS-1 dos respectivos genomas das especies patogenicas de Eimeria em peru, E. adenoeides, E. meleagrimitis 1, E. dispersa, E. gallopavonis e E. meleagridis 2, tambem conhecida aqui como E. edgari. Em uma modalidade particular, um ou mais dos acidos nucleicos anteriormente mencionados compreendem 50 nucleotfdeos ou menos. Mesmo em uma outra modalidade, um ou mais dos acidos nucleicos anteriormente mencionados compreendem 30 nucleotfdeos ou menos. Mesmo em uma outra modalidade, um ou mais dos acidos nucleicos anteriormente mencionados compreendem apenas o numero de nucleotfdeos incluidos explicitamente na sequencia identificada pelo numero de identificagao da sequencia.
[0028] Quaisquer dos acidos nucleicos da presente invenção tambem podem incluir uma sequencia heterologa de nucleotfdeos. Alem do mais, a presente invenção fornece adicionalmente acidos nucleicos que consistem nas sequencias de nucleotfdeos que sao complementares a quaisquer dos acidos nucleicos aqui fornecidos.
[0029] A presente invenção fornece adicionalmente pares de oligonucleotideo iniciador de PCR para amplificar uma regiao ITS-1 do genoma de uma especie de Eimeria em peru. Em uma tai modalidade, o par de oligonucleotideo iniciador de PCR compreende um primeiro oligonucleotideo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 3„ e um segundo oligonucleotideo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 4. Em uma outra modalidade, o par de oligonucleotideo iniciador de PCR compreende um primeiro oligonucleotideo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 5, e um segundo oligonucleotideo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 6. Ainda em uma outra modalidade, o par de oligonucleotideo iniciador de PCR compreende um primeiro oligonucleotideo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 7, e um segundo oligonucleotideo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 8. Mesmo em uma outra modalidade, o par de oligonucleotfdeo iniciador de PCR compreende um primeiro oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 9, e um segundo oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 10. Ainda em uma outra modalidade, o par de oligonucleotfdeo iniciador de PCR compreende um primeiro oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 11, e um segundo oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 12. Mesmo em uma outra modalidade, o par de oligonucleotfdeo iniciador de PCR compreende um primeiro oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 45, e um segundo oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 46. Ainda em uma outra modalidade, o par de oligonucleotfdeo iniciador de PCR compreende um primeiro oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 47, e um segundo oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 48. Mesmo em uma outra modalidade, o par de oligonucleotfdeo iniciador de PCR compreende um primeiro oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 49, e um segundo oligonucleotfdeo iniciador que compreende uma sequencia de nucleotfdeos de SEQ ID NO: 50.
[0030] A presente invenção fomece adicionalmente estojos de amplificagao de PCR que compreendem um, dois ou mais pares de oligonucleotfdeo iniciador de PCR da presente invenção. Tais estojos podem incluir quaisquer tais combinagoes/permutas. Assim, os estojos alternatives da presente invenção podem compreender um, dois, tres, quatro, cinco ou mais de tais pares de oligonucleotfdeo iniciador de PCR.
[0031] Por exemplo, em um tai estojo, as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotfdeo iniciador de um par compreendem SEQ ID NO: lie SEQ ID NO: 12. Em um outro estojo, as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotideo iniciador de um par compreendem SEQ ID NO: 3 e SEQ ID NO: 4, e as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotideo iniciador de um outro par compreendem SEQ ID NO: lie SEQ ID NO: 12. Ainda em um outro estojo, as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotideo iniciador de um par compreendem SEQ ID NO: 5 e SEQ ID NO: 6, e as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotideo iniciador de um outro par compreendem SEQ ID NO: lie SEQ ID NO: 12.
[0032] Ainda em um outro estojo como este, as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotideo iniciador de um par compreendem SEQ ID NO: 5 e SEQ ID NO: 6, as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotideo iniciador de um outro par compreendem SEQ ID NO: 9 e SEQ ID NO: 10, e as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotideo iniciador ainda de um par adicional compreendem SEQ ID NO: lie SEQ ID NO: 12.
[0033] Em uma modalidade particular, o estojo compreende pares de oligonucleotideo iniciador de PCR que apresentam respectivamente pares de oligonucleotideo iniciador que compreendem a sequencia de nucleotfdeos de SEQ ID NO: 3 e SEQ ID NO: 4, SEQ ID NO: 5 e SEQ ID NO: 6, SEQ ID NO: 7 e SEQ ID NO: 8, SEQ ID NO: 9 e SEQ ID NO: 10, e SEQ ID NO: 11 e SEQ ID NO: 12. Alternativamente, em certos estojos, SEQ ID NO: 45 e SEQ ID NO: 46 podem ser substituidos por SEQ ID NO: 7 e SEQ ID NO: 8; e/ou SEQ ID NO: 47 e SEQ ID NO: 48 substituidos por SEQ ID NO. 5 e SEQ ID NO: 6; e/ou SEQ ID NO. 49 e SEQ ID NO: 50 substituidos por SEQ ID NO. 9 e SEQ ID NO: 10.
[0034] Mesmo em uma outra modalidade, um estojo da presente invenção compreende pares de oligonucleotideo iniciador de PCR que apresentam respectivamente pares de oligonucleotfdeo iniciador que compreendem a sequencia de nucleotfdeos de SEQ ID NO: 3 e SEQ ID NO: 4, SEQ ID NO: 5 e SEQ ID NO: 6, SEQ ID NO: 45 e SEQ ID NO: 46, SEQ ID NO: 47 e SEQ ID NO: 48, e SEQ ID NO: 49 e SEQ ID NO: 50.
[0035] A presente invenção fomece adicionalmente metodos de empregar um ou mais pares de oligonucleotfdeos iniciadores de PCR para identificar uma ou mais especies patogenicas de Eimeria em pern em uma amostra biologica. Um metodo como este pode ser usado para identificar E. meleagrimitis 2 em uma amostra biologica. Uma modalidade particular deste metodo compreende determinar acidos nucleicos contidos em uma amostra biologica e amplifica-los por PCR na presenga de um par de oligonucleotfdeo iniciador de PCR especifico para E. meleagrimitis 2 em condigoes que produzirao um produto de PCR quando os acidos nucleicos de E. meleagrimitis 2 estiverem contidos na amostra biologica. A smtese do produto de PCR e monitorada e, quando o produto de PCR e deletado, E. meleagrimitis 2 e identificado como presente na amostra biologica. Em uma modalidade particular deste tipo, as respectivas sequencias de nucleotfdeos do primeiro e segundo oligonucleotfdeo iniciador do par de oligonucleotfdeo iniciador de PCR empregado compreendem SEQ ID NO: lie SEQ ID NO: 12, respectivamente. Ainda em uma outra modalidade, o(s) produto(s) de PCR sintetizado(s) e(sao) sequenciado(s), e quando observa-se que apresentam mais de 87 % de homologia com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 31, 32, 33, 34, 43, e/ou 44, E. meleagrimitis 2 e identificado como presente na amostra.
[0036] Mesmo em uma outra modalidade, o(s) produto(s) de PCR sintetizado(s) e(sao) sequenciado(s) e quando observa-se que apresentam mais de 95 % de homologia com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 31, 32, 33, 34, 43, e/ou 44, E. meleagrimitis 2 € identificado como presente na amostra. Ainda em uma outra modalidade, o(s) produto(s) de PCR sintetizado(s) e(sao) sequenciado(s) e quando observa-se que apresentam 100 % de identidade com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 31, 32, 33, 34, 43, e/ou 44, E. meleagrimitis 2 e identificado como presente na amostra.
[0037] Em uma outra modalidade, um metodo de identificar Eimeria patogenica no peru presente em uma amostra biologica compreende determinar acidos nucleicos contidos na amostra biologica e amplificar os acidos nucleicos determinados por PCR na presenga de um conjunto completo de oligonucleotfdeos iniciadores para as cinco novas especies patogenicas conhecidas de Eimeria em peru, em condigoes que produzirao o(s) produto(s) correspondente(s) de PCR quando os acidos nucleicos correspondentes da Eimeria patogenica no peru estiverem contidos na amostra biologica. O(s) produto(s) de PCR e(sao) monitorado(s), e quando qualquer do(s) produto(s) de PCR e(sao) deletado(s) durante o monitoramento, Eimeria patogenica no peru e identificada como presente na amostra biologica.
[0038] Em uma modalidade relacionada, um metodo de identificar as especies de Eimeria patogenica no peru presentes em uma amostra biologica compreende determinar acidos nucleicos contidos em uma amostra biologica e amplificar os acidos nucleicos determinados por PCR na presenga de um conjunto completo de oligonucleotfdeos iniciadores para as especies patogenicas de Eimeria em peru, em condigoes que produzirao o(s) produto(s) correspondente(s) de PCR quando os acidos nucleicos correspondentes da Eimeria patogenica no peru estiverem contidos na amostra biologica. O(s) produto(s) de PCR e(sao) detetado(s) e as especies da Eimeria patogenica no peru sao associadas a cada produto de PCR detectado e determinado. A determinagao pode identificar assim cada especie de Eimeria patogenica no peru presente na amostra biologica.
[0039] Em modalidades particulares, a(s) sequencia(s) de nucleotfdeos do(s) produto(s) de PCR produzido(s) e(sao) determinada(s). Quando uma sequencia de nucleotfdeos como esta apresenta mais de 87 % de homologia com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 31, 32, 33, 34, 43, e/ou 44, E. meleagrimitis 2 e identificado como presente na amostra. De maneira similar, quando a sequencia de nucleotfdeos de um produto de PCR sintetizado apresenta mais de 90 % de homologia com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 24, 25, 26, 27, 28, 29 e/ou 30, E. meleagrimits 1 e identificado como presente na amostra. Quando a sequencia de nucleotfdeos de um produto de PCR sintetizado apresenta mais de 90 % de homologia com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 18, 19, 20, e/ou 21, E. adenoeides e identificado como presente na amostra. Quando a sequencia de nucleotfdeos de um produto de PCR sintetizado apresenta mais de 90 % de homologia com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 13, 14, 15, 16, 17, 36, 39, 40, e/ou 41, E. gallopavonis e identificado como presente na amostra. Finalmente, quando a sequencia de nucleotfdeos de um produto de PCR sintetizado apresenta mais de 90 % de homologia com a sequencia de nucleotfdeos correspondente contida em SEQ ID NOs: 22, 23, e/ou 42, E. dispersa e identificado como presente na amostra. Em modalidades relacionadas, o percentual de homologia exigido pode ser ajustado para mais de 95 %, e ainda para 100 % de identidade para as especies selecionadas quando desejado.
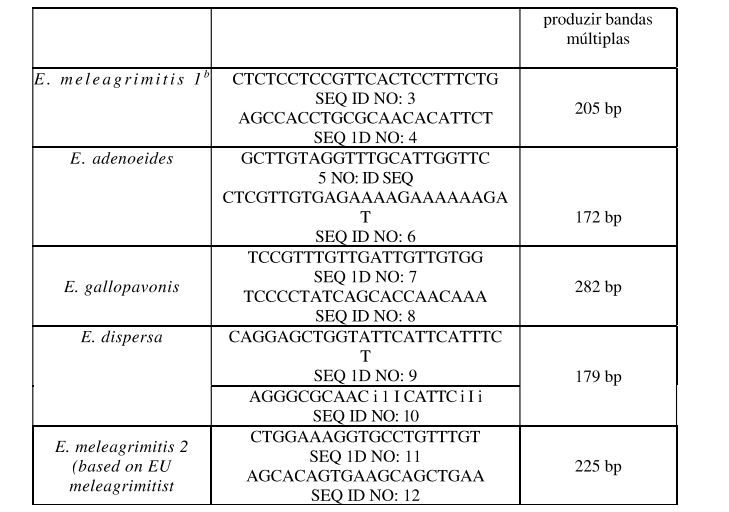
[0040] Em uma modalidade particular, o par de oligonucleotideo iniciador de PCR especifico para E. meleagrimitis 2 compreende as sequencias de nucleotfdeos de SEQ ID NO: 11 e SEQ ID NO: 12, respectivamente; o par de oligonucleotideo iniciador de PCR especifico para E. meleagrimitis 1 compreende as sequencias de nucleotfdeos de SEQ ID NO: 3 e SEQ ID NO: 4, respectivamente; o par de oligonucleotideo iniciador de PCR especifico para E. adenoeides compreende as sequencias de nucleotfdeos de SEQ ID NO: 5 e SEQ ID NO: 6 respectivamente; o par de oligonucleotfdeo iniciador de PCR especifico para E gallopavonis compreende as sequencias de nucleotfdeos de SEQ ID NO: 7 e SEQ ID NO: 8, respectivamente; e o par de oligonucleotfdeo iniciador de PCR especifico para E. dispersa compreende as sequencias de nucleotfdeos de SEQ ID NO: 9 e SEQ ID NO: 10, respectivamente.
[0041] Em uma outra modalidade relacionada, um metodo de identificar as especies de Eimeria patogenica no peru presentes em uma amostra biologica compreende isolar um ou mais isolados de Eimeria em peru da amostra biologica e verificar uma ou mais propriedades da Eimeria patogenica no peru isolada. Estas propriedades incluem, mas sem limitagao, a patologia, a patogenicidade, a imunidade cruzada e/ou a morfometria dos isolados de Eimeria em peru. Em uma modalidade particular deste tipo, o metodo inclui adicionalmente empregar uma ou mais analises geneticas (por exemplo, PCR) junto com a verificagao de uma ou mais propriedades da Eimeria patogenica no peru. Quando mais de um metodo de identificar as especies de Eimeria patogenica no peru presentes em uma amostra biologica e realizado, tais metodos pode ser ocorrer em qualquer ordem, incluindo simultaneamente, se viavel.
[0042] Estes e outros aspectos da presente invencao serao melhor interpretados por referenda a descrito detalhada, figuras e exemplos.
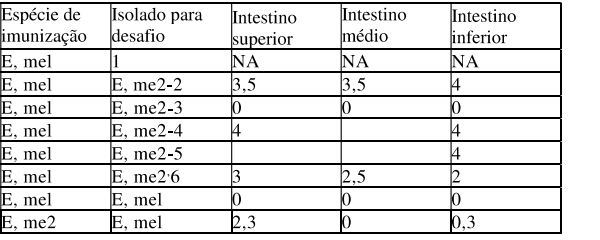
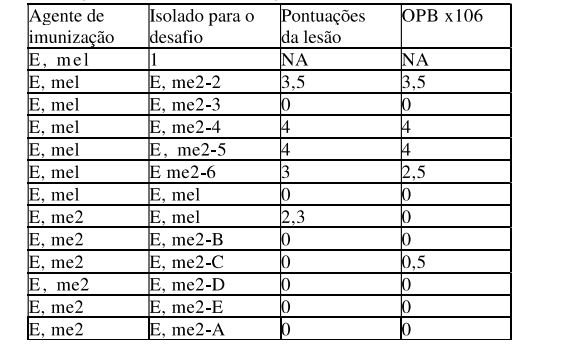
[0043] A figura 1 mostra lesoes espessas tipicas observadas com E. meleagrimitis 1 ou E. meleagrimitis 2 no duodeno.
[0044] A figura 2 mostra lesoes espessas tipicas observadas com E. meleagrimitis 1 ou E. meleagrimitis 2 no jejuno. As fezes dos animais infectados sao aquosas, mucoides e sanguinolentas. Os parasitas invadem as celulas epiteliais do duodeno ate o reto e ocasionalmente sao observados no ceco.
[0045] A figura 3A mostra a localizagao dos oligonucleotideos iniciadores de PCR ITS-1. A figura 3B mostra a localizagao dos oligonucleotfdeos iniciadores intemos especie-especificos.
[0046] A figura 4 mostra uma arvore filogenetica construfda nos termos da presente invenção.
[0047] Em um aspecto, a presente invenção fornece uma especie patogenica de Eimeria recentemente identificada, que foi denominada E. meleagrimitis 2 (ou, alternativamente, E. edgari). Da maneira aqui fornecida adicionalmente, E. meleagrimitis 2 foi caracterizada suficientemente para permitir sua identificagao inequivoca. Em um aspecto relacionado, a presente invenção fornece novas vacinas que protegem contra estas especies patogenicas de Eimeria recentemente identificadas. Ainda em um outro aspecto, a presente invenção fornece estojos que podem ser usados para identificar e distinguir facilmente as cinco especies patogenicas de Eimeria em peru agora conhecidas.
[0048] E. meleagrimitis 2 foi isolada de epidemias de coccidiose cllnica em operagoes de peru comercial a partir de varios estados em todos dos Estados Unidos, e de perus selvagens que vivem na regiao de Delmarva. E meleagrimitis 2 (Eme2) afeta a mesma regiao do intestino assim como E meleagrimitis 1, entretanto, Eme2 pode ser diferenciada por morfologia de oocistos, imunidade conferida (estudos de protegao cruzada) e por sequencia de DNA.
[0049] Ate o momento, nao existem vacinas que fomecem protegao tanto contra E. meleagrimitis 2 quanto contra E. meleagrimitis 1. Portanto, em um aspecto chave, a presente invenção fornece vacinas que protegem tanto contra E. meleagrimitis 2 quanto contra E. meleagrimitis 1. Em uma tai modalidade, a vacina compreende tanto E meleagrimitis 2 quanto E. meleagrimitis 7. Em um aspecto relacionado, sao fornecidos metodos de administrar as vacinas da presente invenção.
[0050] Alem do mais, a presente invenção fomece analise de sequencias da regiao espagadora transcrita interna um (ITS-1) localizadas entre os genes de RNA ribossomal 18S e 5,8S no genoma de Eimeria para cada uma das especies patogenicas de Eimeria'. E meleagrimitis 1, E. adenoeides, E. gallopavonis, E. dispersa, e E meleagrimitis 2. Portanto, ainda em um outro aspecto chave, a presente invenção fomece acidos nucleicos que compreendem sequencias de nucleotfdeos que identificam exclusivamente estas cinco especies patogenicas de Eimeria.
[0051] A presente invenção fomece adicionalmente estojos diagnosticos e metodos relacionados que empregam conjuntos de oligonucleotideo iniciador da reagao em cadeia da polimerase (PCR) capazes de identificar cada uma destas cinco especies patogenicas de Eimeria. Em uma modalidade particular, tais oligonucleotfdeos iniciadores, e/ou conjuntos de oligonucleotideo iniciador sets e/ou sequencias exclusivas de nucleotfdeos aqui fornecidos, podem ser usados para distinguir E meleagrimitis, E. adenoeides, E. gallopavonis, E. dispersa, e/ou E meleagrimitis 2 umas das outras.
[0052] Nao pretende-se de maneira alguma que o uso de termos singulares para conveniencia na descrigao seja assim limitante. Assim, por exemplo, a referenda a uma composigao que compreende "uma quantidade" inclui referenda a uma ou mais de tais quantidades. Alem do mais, a referenda a um "oocisto" inclui referenda a uma pluralidade de tais oocistos, a menos que de outra forma indicada.
[0053] Todas as sequencias de acidos nucleicos aqui fomecidas, a menos que de outra forma indicada, sao escritas 5' a 3'.
[0054] Da maneira aqui usada, os termos a seguir podem ter as definigoes apresentadas a seguir:
[0055] A palavra "peru", da maneira aqui usada, e a menos que de outra forma indicada, inclui todos os elementos do genero Meleagris, incluindo as especies gallopavo e ocellata. Quase todos os perus pertencem a especie gallopavo.
[0056] O termo "amostra biologica", da maneira aqui usada, e qualquer amostra obtida de um animal, por exemplo, peru, ou dos ambientes do animal (por exemplo, detrito, e/ou area geografica e/ou campo onde os animais residem) que contem e/ou sao suspeitos de conter Eimeria, e/ou acidos nucleicos de Eimeria e/ou derivados destes. Exemplos de amostras biologicas incluem, mas sem limitagao: amostras fecais, amostras de detrito e amostras gastrointestinais.
[0057] Da maneira aqui usada, o termo "acidos nucleicos acessiveis" contido em uma amostra biologica significa assegurar que os acidos nucleicos da amostra biologica estao dispomveis para funcionar como um molde durante PCR. No caso mais, acessar os acidos nucleicos implica em colocar uma amostra biologica no tubo de reagao de PCR. Entretanto, este termo tambem pode incluir uma ou mais manipulates de uma amostra biologica, por exemplo, rompimento/lise celular, etapas de purificagao, etc., que auxiliam no prepare dos acidos nucleicos contidos na amostra biologica dispomveis para funcionar como um molde durante PCR.
[0058] O termo "Eimeria", da maneira aqui usada, a menos que de outra forma indicada, significa uma ou mais especies do genero Eimeria que infectam passaros domesticos. As especies de Eimeria incluem aquelas que sao observadas em galinhas e incluem, por exemplo, E. tenella, E. acervulina, E. maxima, E. necatrix, E. mitis, E. praecox, E. mivati, E. hagani e E brunetti, e tambem aquelas que sao observadas em perus, incluindo E. meleagrimitis 1, E. adenoeides, E. gallopavonis, E. dispersa, E. meleagridis, E. innocua, e E. subrotunda. Da maneira aqui usada, uma "Eimeria em peru" refere-se a Eimeria que infecta perus. O termo "Eimeria" tambem inclui todas as cepas das especies anteriormente mencionadas de Eimeria, incluindo, mas sem limitagao, cepas precoces e cepas atenuadas, que tambem incluem cepas que foram irradiadas, ou tratadas de outra maneira, de maneira tai que nao consigam completar o desenvolvimento. O termo Eimeria inclui adicionalmente quaisquer cepas ou especies recem descobertas de Eimeria que infecta passaros domesticos da maneira definida anteriormente, tai como E. meleagrimitis 2, da maneira aqui revelada.
[0059] Da maneira aqui usada, o termo "E. MAD" significa uma mistura de E. meleagrimitis 1, E. adenoeides e E. dispersa.
[0060] Da maneira aqui usada, uma cepa "atenuada" de uma especie de um genero Coccidia (tai como uma "Eimeria atenuada") e uma cepa que foi selecionada por sua patogenicidade reduzida no hospedeiro. Uma atenuagao como esta pode ser atingida por inumeros meios, incluindo metodos de passagem seriada (tai como passagem embrionaria seriada), mutagenese qufmica ou de irradiagao.
[0061] Da maneira aqui usada, uma cepa "precoce" de uma especie do genero Coccidia (tai como uma "Eimeria precoce") e uma cepa que apresenta um menor periodo pre-patente com relagao a cepa nao atenuada da mesma especie. Uma cepa precoce tambem pode ser uma cepa atenuada.
[0062] Da maneira aqui usada, uma cepa "tipo selvagem" de uma especie do genero Coccidia (tai como uma "Eimeria tipo selvagem") e um isolado de campo que nao foi alterado por passagem de atenuagao ou qualquer outro tratamento incluindo selegao de: isolamento de oocisto simples, tolerancia imune ou outro processo segregative.
[0063] Da maneira aqui usada, uma cepa “nao atenuada” de uma especie do genero Coccidia (tai como "Eimeria nao atenuada") e uma cepa que nao apresenta nem um menor periodo pre-patente nem patogenicidade reduzida no hospedeiro com relagao a cepa tipo selvagem da mesma especie, mas foi mantida no laboratorio por um periodo maior.
[0064] Da maneira aqui usada, uma "cepa" de uma especie do genero Coccidia (por exemplo, uma especie de Eimeria) e uma sub-populagao das especies do genero Coccidia que pode ser diferenciada da populagao geral destas especies por uma ou mais das caracteristicas a seguir: morfometria, patogenicidade, imunogenicidade, periodo pre-patente, e/ou uma populagao resultante da expansao de um oocisto simples.
[0065] Da maneira declarada anteriormente, o tempo a partir da ingestao pelo hospedeiro dos oocistos esporulados ate o surgimento dos oocistos nao esporulados nas fezes e denominado o periodo pre-patente. O termo "periodo pre-patente assfncrono" refere-se a periodos pre-patentes de duas ou mais especies do genero Coccidia e/ou duas ou mais cepas de uma especie do genero Coccidia que diferem em 10 % ou mais. Em uma modalidade particular, duas ou mais especies do genero Coccidia e/ou duas ou mais cepas de uma unica especie do genero Coccidia apresentam periodos pre-patentes assincronos que diferem em 20 % ou mais. Mesmo em uma outra modalidade, duas ou mais especies do genero Coccidia e/ou duas ou mais cepas de uma unica especie do genero Coccidia apresentam periodos pre-patentes assincronos que diferem em 25 % ou mais.
[0066] Com relagao aos periodos pre-patentes assincronos para cepas precoces e/ou atenuadas com cepas nao atenuadas que diferem em um percentual (%) de tempo, o percentual baseia-se no periodo de tempo prepatente da cepa nao atenuada. Assim, quando uma cepa nao atenuada do genero Coccidia apresenta um periodo pre-patente de 120 horas e uma cepa precoce da mesma especie do genero Coccidia apresenta um periodo prepatente de 108 horas, as duas cepas apresentam periodos pre-patentes assincronos que diferem em 10 %.
[0067] Da maneira aqui usada, um "material homologo" e uma composigao e/ou aliquota de: organismos que apresentam propriedades biologicas uniformes, e/ou sao derivados de organismos da mesma especie, e/ou mostram um grau de similaridade de propriedades que indica uma origem comum.
[0068] Da maneira aqui usada, um "material heterologo" e uma composigao e/ou aliquota de: organismos que apresentam diferentes propriedades biologicas, e/ou sao derivados de organismos de especies diferentes, e/ou mostram um grau de dissimilaridade de propriedades que indicam diferentes origens.
[0069] As palavras "oocistos", "merozoitas" e "esporozoftas", da maneira aqui usada, e a menos que de outra forma indicada, significam oocistos, merozoitas e esporozoftas de Eimeria em peru que podem ser tanto mortas, atenuadas quanto nao atenuadas.
[0070] A palavra "esporocisto" refere-se a capsula que retem os esporozoftas no oocisto.
[0071] A palavra "encistado" significa o estagio de oocisto do parasita protozoario.
[0072] Da maneira aqui usada, as palavras "imunizar" e "vacinar" sao sinonimos e sao usadas indiferentemente. O termo "dose de imunizagao efetiva", da maneira aqui usada, a menos que de outra forma indicada, significa o numero de esporozoarios em qualquer estagio em seu ciclo de vida incluindo misturas de um ou mais, ou ainda todos os estagios de seus ciclos de vida, por exemplo, esporozoftas, oocistos e/ou merozoitas ou, quando misturados, por exemplo, o numero de esporozoftas, oocistos e merozoitas, suficiente para obter uma reagao imune em animais assim vacinados, por exemplo, obter um aumento nos titulos do anticorpo correspondente e/ou uma ativagao de imunidade mediada por celula. Preferivelmente, a reagao imune que e obtida fornece imunidade protetora que limita ou reduz os sinais de doenga clfnica, perda de peso, morbidade, menos utilizagao do alimento, e/ou mortalidade nos animais vacinados (por exemplo, aves) quando desafiados com uma dose virulenta do esporozoario (por exemplo, Eimeria ou Cryptosporidia).
[0073] O termo "imunidade sólida" é aqui usado indiferentemente com o termo "imunidade total" e o termo "hiper-imunidade" e denota um grau de imunidade outorgado em um grupo de animais vacinados (por exemplo, um grupo de passaros vacinados) que fomece protegao contra um desafio homologo de maneira tai que os animais vacinados sao estatisticamente similares aos controles nao desafiados (e/ou estatisticamente dissimilares aos controles desafiados nao vacinados) na saude e desempenho, da maneira medida em, por exemplo, conversao da ragao, ganho de peso e/ou lesoes (grandes ou microscopicas) da coccidiose.
[0074] Os termos "adjuvante" e "estimulante imune" sao aqui usados indiferentemente, e sao definidos como uma ou mais substancias que causam estfmulo do sistema imune. Os adjuvantes sao agentes que aumentam de maneira nao especifica uma resposta imune a um antfgeno particular, reduzindo assim a quantidade de antfgeno necessario em qualquer vacina fornecida, e/ou a frequencia de injegao necessaria a fim de gerar uma resposta imune adequada ao antfgeno de interesse. Neste contexto, um adjuvante e usado para melhorar uma resposta imune em uma ou mais antfgenos/isolados da vacina. Um adjuvante pode ser administrado ao animal alvo antes, em combinagao com, ou apos a administragao da vacina.
[0075] Da maneira aqui usada uma "sequencia heterologa de nucleotfdeos" e uma sequencia de nucleotfdeos que e adicionada a uma sequencia de nucleotfdeos da presente invenção por metodos recombinantes para formar um acido nucleico que nao e naturalmente sintetizado na natureza. Tais acidos nucleicos podem codificar os acidos nucleicos de fusao (por exemplo, quimericos). Em uma modalidade particular, a sequencia heterologa de nucleotfdeos pode funcionar como um meio de detectar uma sequencia de nucleotfdeos da presente invenção. Em uma outra modalidade, uma sequencia heterologa de nucleotfdeos com esta pode funcionar para facilitar o uso do acido nucleico em uma reagao de PCR.
[0076] Da maneira aqui usada o termo "aproximadamente" é usado indiferentemente com o termo "cerca de" e significa que um valor e cinquenta por cento do valor indicado, isto e, uma composigao que contem "aproximadamente" 100 oocistos, contem de 50 a 150 oocistos.
[0077] O termo "estatisticamente similar", da maneira aqui usada, denota que uma comparagao estatfstica de dois grupos ou populagoes de animais resultaria na aceitagao da hipotese nula (ou hipotese de nenhuma diferenga) em um nivel de significancia de < 0,1.
[0078] O termo "estatisticamente dissimilar", da maneira aqui usada, denota que uma comparagao estatfstica de dois grupos ou populagoes de animais resultaria na rejeigao da hipotese nula (ou hipotese de nenhuma diferenga) em um nivel de significancia de < 0,1.
[0079] Da maneira aqui usada, quando uma serie de sequencias de nucleotfdeos sao fomecidas em uma lista de SEQ ID NOs., por exemplo, SEQ ID NOs: 31, 32, 33, 34, e/ou 43 (ou SEQ ID NO:31, SEQ ID NO:32, SEQ ID NO:33, SEQ ID NO:34, e/ou SEQ ID NO:43), pretende-se que o "e/ou" modifique a relagao entre todas as SEQ ID NOs. listadas na serie. Portanto, uma comparagao/identificagao que baseia-se em uma serie de sequencias de nucleotfdeos como esta pode ser realizada com referenda a qualquer uma das sequencias individuais de nucleotfdeos listadas sozinhas, ou a qualquer combinagao das sequencias individuais de nucleotfdeos listadas, incluindo todas as sequencias de nucleotfdeos listadas na serie.
[0080] Os alinhamento de sequencia de nucleotfdeos sao realizados usando a metodologia de Clustal W J. D. Thompson et al., [Nucleic Acid Research 22:4673-4680 (1994)], no programa de alinhamento Megalign™ do software de analise de dados DNASTAR (Windows 32 Megalign 5.06. 19932203 DNASTAR Inc.) usando ajustes padroes em todos. Caracterizacao de E. meleagrimitis 2
[0081] E. meleagrimitis 2 invade as mesmas regioes intestinais como E. meleagrimitis 1 e E. dispersa, mas os oocistos de E. meleagrimitis 2 sao relativamente menores que aqueles destas duas especies. Observou-se que os oocistos esporulados examinados sao subesfericos, medindo 17,824 x 16,444 microns (16,915-19,549 x 14,585-18,314 microns) com um fndice de forma de 1,0839.
[0082] O parasitismo com E. meleagrimitis 2 e acompanhado por grave hiperemia e produgao excessiva de muco na metade superior do intestino delgado, com hemorragia de mucosa moderada a grave que se estende do duodeno para o fleo a medida que a infecgao progride (ver, figuras 1 e 2).
[0083] A especie de Eimeria recem identificada, E. meleagrimitis 2, pode ser identificada inequivocamente por sua sequencia exclusiva de nucleotfdeos na regiao espagadora transcrita interna um (regiao ITS-1, ver, figura 3B), localizada entre os genes ribossomais 18S e 5,8S no genoma de Eimeria. Dessa maneira, a presente invenção fornece sequencias individuais de nucleotfdeos da regiao ITS-1 de quatro isolados de E. meleagrimitis 2, SEQ ID NOs: 31, 32, 33 e 39. Estas sequencias compartilham mais de 96 % (e ate 100 %) de homologia uma com a outra. A presente invenção fornece adicionalmente uma sequencia consensual para a regiao ITS-1 de E. meleagrimitis 2 com uma sequencia de nucleotfdeos de SEQ ID NO: 44.
[0084] Alem do mais, conjuntos de oligonucleotideo iniciador de PCR, com base na sequencia da regiao ITS-1 de cada especie, foram desenhados para uso em ensaios de identidade a base de PCR. Um conjunto completo de tais oligonucleotfdeos iniciadores esta presente no grupo de pares de sequencias de nucleotfdeos de SEQ ID NOs: 3 e 4, para E. meleagrimitis 1; SEQ ID NOs: 5 e 6, para E. adenoeides', SEQ ID NOs: 7 e 8, para E. gallopavonis', SEQ ID NOs: 9 e 10, para E. dispersa', SEQ ID NOs: 11 e 12, para E. meleagrimitis 2.
[0085] O animal a ser tratado e preferivelmente um elemento do genero Meleagris, isto e, um peru. Em uma modalidade particular, o peru e do genero gallopavo, isto e, um peru domestico. Em uma outra modalidade, o peru e do genero ocellata. Em geral, a administragao da vacina e realizada em perus jovens, muitas vezes, no dia do nascimento do peru jovem.
[0086] Os oocistos tipo selvagem sao obtidos das fezes ou tecido dos animais infectados; ragao ou agua contaminados; solo; detritos das penas ou de local de repouso ou uma variedade de outras fontes. Os metodos para o isolamento de esporocistos e oocistos sao conhecidos. Os procedimentos exatos usados para separar os oocistos variarao com o material dos quais os oocistos sao obtidos e serao facilmente interpretados pelos versados na tecnica. Os merozoitas podem crescer na culture pelos metodos revelados em U.S. 7.250.286 B2, cujos conteudos sao aqui incorporados pela referenda na sua Integra.
[0087] Uma abordagem disponivel para isolar organismos de amostras ambientais brutas e da maneira a seguir: A etapa inicial e a separagao dos esporocistos e/ou oocistos a partir de material estranho. O solo, ou excregoes, e em geral processado formando uma lama com solugao de salina saturada e separando os esporocistos e/ou oocistos da lama. Por exemplo, o material a ser processado e misturado com um mmimo de 2 volumes (p/v) de NaCl aquoso saturado para formar uma lama. Se necessario, a lama pode ser processada em um misturador ou liquidificador ate que uma consistencia homogenea foi atingida. A lama e centrifugada em cerca de 800 x g por 10 minutos a 4 °C. O sobrenadante e coletado vertendo atraves de uma camada dupla de gaze ondulada 24 x 24. Outros metodos para purificar oocistos das amostras que sao comumente usados incluem a flotagao de sacarose do tipo Sheather e flotagao de zinco-sulfato, [por exemplo, ver LR Ash e TC Orihel, Parasites: A Guide to Laboratory Procedures and Identification. ASCP Press © 1991, aqui incorporado pela referenda].
[0088] O sobrenadante filtrado e diluido com dois volumes de agua potavel e centrifugado a cerca de 1.600 x g por 10 minutos a 4 °C. Os oocistos precipitados sao lavados com agua e precipitados por centrifugagao, da maneira descrita, por mais tres vezes. Os oocistos sao entao lavados tres vezes em dicromato de potassio 2,5 % usando o mesmo procedimento usado para as lavagens em agua. Apos a lavagem final, os oocistos podem ser armazenados em dicromato de potassio 2,5 % a 4 °C ou transferidos para um recipiente para esporulagao.
[0089] Altemativamente, a filtragao sequential pode ser usada para isolar os oocistos com base no peso. Se a filtragao for usada, os oocistos srao lavados com agua e dicromato de potassio 2,5 %, da maneira previamente descrita.
[0090] Linhagens nao atenuadas que originaram dos isolados de campo tipo selvagem foram mantidas em ajustes de laboratorio por passagem seriada por muitos anos e sao bem caracterizadas como baixas a moderadas em patogenicidade, com moderada a alta fecundidade, perfodos pre-patentes definidos e padroes de mudanga conhecidos a partir do hospedeiro.
[0091] A parte das linhagens precoces existentes de Eimeria, as linhagens precoces tambem podem ser obtidas a partir das cepas maes tipo selvagem virulentas ou cepas nao atenuadas apos a passagem seriada em perus. Em cada um destes casos, os oocistos sao coletados das fezes apenas durante as primeiras poucas horas apos a patencia. Desta maneira, o penodo de tempo pre-patente pode ser progressivamente reduzido. Este tipo de passagem e denominado uma passagem de selegao. Altemativamente, a fim de aumentar os numeros de oocistos dispomveis para a coleta, pode ser vantajoso coletar oocistos em um penodo entre o initio da patencia e o penodo de tempo pre-patente aproximado da cepa mae. Este tipo de passagem e denominado uma passagem neutra. Finalmente, no processo conhecido como passagem relaxada, virtualmente todos os oocistos sao coletados, incluindo aqueles produzidos posteriormente ao penodo de tempo pre-patente da cepa mae.
[0092] As vacinas da presente invenção podem ser preparadas por muitos procedimentos, um dos quais e fomecido apenas como um exemplo.
[0093] Seis especies de Eimeria em peru foram isoladas e entao propagadas por passagem atraves dos perus. Proporgoes (Oocisto viavel ou unidade por 1.000 doses). Especies Oocistos E. adenoeides 1 xlO41 xlO6 E. dispersa IxlO4IxlO6 E. gallops vonis 1 xlO41 x 106 E. meleagridis 1 xlO41 xlO6 E meleagrimitis 1 xlO41 xlO6 E. meleagrimitis 1 xlO41 xlO6
[0094] • Metodo de Identificagao: Os Coccidia sao identificados por exame microscopio e medigoes de comprimento e largura. A area de infecgao (mudangas patologicas) e tambem um criterio para distinguir especies de Eimeria. Como cada especie e antigenicamente distinta, os estudos imunologicos cruzados em passaros susceptfveis e nao imunizados tambem podem ser usados como um meio de identificagao de culturas.
[0095] • Os artigos de vidro e utensilios usados em laboratorios de produgao sao lavados cuidadosamente apos o uso e permanecem em sua sala especie-especffica. Se tais itens forem usados para crescer uma especie diferente de Eimeria no mesmo hospedeiro, eles sao submetidos a autoclavagao a 121 °C por 30 minutos e/ou tratamento termico em mais de 37,78 °C (100 °F) por 72 horas ou mais de 65,55 °C (150 °F) por 48 horas.
[0096] • Virulencia e pureza das culturas: a pureza de culturas semeadas pode ser obtida por isolamento da celula unica. Um oocisto viavel, medido com um micrometro ocular, e fomecido oralmente a passaros de 3 a 10 dias sem Coccidios. Como o periodo pre-patente e conhecido para cada especie, o passaro e sacrificado durante a produgao de oocisto e os intestinos e/ou bolsas cecais sao lavados com agua esteril, dicromato de potassio 2,5 % e adicionado e aerado por 24-72 horas a fim de permitir que os oocistos contidos na suspensao se tomem esporulados e por meio disso, infectivos. Estes sao passados por um outro passaro sem Coccidia e o processo e repetido ate que numeros suficientes de oocistos fossem obtidos, os quais serao usados como semente para a produgao.
[0097] Todos os oocistos, obtidos em cultures puras da maneira descrita anteriormente, sao reproduzidos em animais nascidos vivos, quarentenados e mantidos sem infecgao coccidial. Os passaros variam em idade de 3-28 dias para a produgao da semente e de 3-8 semanas para a produgao da vacina. Os passaros sao conferidos quanto a ausencia de infecgao pelo metodo de flotagao do sugar agucar semanalmente e exatamente antes de periodo de inoculagao.
[0098] As cultures de semente sao armazenadas em temperature de refrigeragao. Os oocistos para inoculagao sao suspenses em agua de tomeira fria.
[0099] Os passaros individuals sao inoculados com 1,0 mL da suspensao inserindo uma pipeta ou seringa calibradas contendo a suspensao de oocisto no cultivo. O numero de oocistos por 1,0 mL varia com cada especie: Especie Oocistos viaveis/mL E. adenoeides 1 xlO35xl05 E. disperse 1 xlO35xl05 Propagacao e coleta de oocistos:
[00100] • Cada especie e propagada no intestino de perus vivos. Apos um penodo pre-patente apropriado, ver anteriormente, oocistos nao esporulados sao depositados nos excrementos. Os excrementos podem ser coletados diariamente a partir do quarto ao decimo primeiro dia apos a inoculagao. Os oocistos sao examinados microscopicamente e podem obedecer ao tamanho e forma dos oocistos usados na inoculagao. Outros tipos nao podem estar presentes, que de outra forma indicam que uma especie contaminante foi introduzida de maneira inadequada. Passaros aleatorios podem ser sacrificados e observados quanto as lesoes caracteristicas nas segoes apropriadas do intestino. Nenhuma coleta e realizada se existir qualquer evidencia de lesoes causadas por doenga estranha ou outra especie de Coccidia.
[00101] Os passaros usados para a produgao de cada especie de Coccidia sao criados em baterias e mantidos em quarentena ate a necessidade de produgao. Eles sao transferidos em um quarto designado para a produgao de uma especie, e cada passaro e infectado oralmente com uma suspensao de uma cultura de semente pura de oocistos. Os passaros sao cuidados por tecnicos treinados durante o penodo pre-patente.
[00102] • O penodo pre-patente varia com cada especie.
[00103] • Os excrementos de passaros infectados sao coletados em bandejas contendo papel que e trocado diariamente. Os excrementos sao transferidos para um bequer limpo e misturados com agua de tomeira para render uma consistencia encharcada. Uma diluigao 1 :10 desta suspensao e realizada em agua de tomeira e os oocistos sao contados em um hemocitometro. Se as contagens parecem suficientemente altas, os oocistos sao lavados dos excrementos.
[00104] Se os excrementos forem ricos na contagem de oocistos, uma diluigao 1:5 (aproximada) e realizada na suspensao encharcada em dicromato de potassio 2,5 % e a suspensao e vigorosamente agitada. As particulas estranhas mais pesadas assentam rapidamente e os oocistos permanecem suspenses no sobrenadante. Este sobrenadante passa por uma peneira de tela 100 para remover quaisquer particulas grandes de flotagao grandes. Este procedimento e repetido lavando o sedimento varias vezes a fim de remover a maioria dos oocistos. O agrupamento de sobrenadante e transferido para frascos e aerado borbulhando ar atraves deste. A aeragao continua por 24-72 horas ate que a esporulagao maxima fosse obtida.
[00105] Apos a aeragao, os oocistos sao mantidos em temperatura ambiente ate que eles tenharn se sedimentado. O sedimento e lavado com dicromato 2,5 % ate que nenhum oocisto possa ser observado no sedimento. A sedimentagao e o descarte do sobrenadante e repetido ate que os oocistos estejam contidos em um volume que seria aproximadamente a metade do sedimento e a metade do dicromato limpo. A suspensao e resfriada a aproximadamente 4 °C, e a seguir beta-propiolactona fria e adicionada em uma concentragao final de 0,1-0,2 % e colocada no refrigerador. Alternativamente, os excrementos sao dihridos com agua de tomeira e passados por uma peneira de malha 100. Este procedimento e repetido varias vezes para remover a maioria dos oocistos. O sobrenadante e concentrado permitindo-o assentar ate que os oocistos sedimentem ou por centrifugagao de fluxo contmuo a 2.000 RPM. O sedimento e entao misturado com uma solugao saturada de agucar e centrifugada com o efluente retido.
[00106] O efluente e diluido com agua de tomeira fria e re-centrifugado com o sedimento contendo os oocistos que sao retidos. Os oocistos sao ressuspensos com dicromato de potassio 2,5 % e aerados por 24-72 horas. Beta-propiolactona e adicionada em concentrado final a 0,1-0,2 % e colocada em um refrigerador.
[00107] Cada suspensao de especie e cultivada para esterilizagao. Um mL de cada suspensao e inoculada em cada um dos seguintes: agar cerebro coragao, desoxicolato, SS e de dextrose de Sabouraud. Nenhum patogeno pode estar presente.
[00108] As aliquotas de cada especie com um numero ideal de oocistos sao inoculadas oralmente em um grupo de tres passaros de 2-8 semanas. Estes passaros sao sacrificados durante o periodo de infecgao para verificar se as lesoes produzidas foram causadas pelas especies pretendidas. Cada lote tem que conter apenas a especie pretendida.
[00109] Todo o material descartado e manipulado de acordo com V.S. Memo 800.56. Os materiais solidos sao colocados em sacolas de polietileno e queimados ou incinerados. Os liquidos sao tratados com lixivia (50 mL por 1.000 mL de fluidos para fornecer aproximadamente cloro 600 ppm) e mantidos a temperatura ambiente por pelo menos 15 minutos antes da eliminagao por meio do esgoto sanitario.
[00110] • As gaiolas ou baterias de passaros sao lavadas sob pressao e descontaminadas com calor seco (65,55 °C (150 °F) por 48 horas ou 37,78 °C (100 °F) por 72 horas).
[00111] • Exemplo de conjunto de lote: (Lote medio 80.000 mL) Numero mmimo de oocistos esporulados em solucao de dicromato de potassio 2,5 % Species DOSE 1.000 DOSE 5.000 E. adenoeides 4 X 109 8 X 109 E. dispersa 8 X 109 1,6 X IO10 E. gallopavonis 4 X 109 8 X 109 E. meleagrimitis 1 4X 109 8X 109 E. meleagrimitis 2 4X 109 8X 109 • Volume do lote medio: 80.000 mL • Volume de lote maximo: 160.000 mL Volume da carga: (O volume da carga e verificado periodicamente durante o carregamento.)
[00112] • 4,2+0,2 mL em um frasco esteril de 10 mL para 1.000 doses
[00113] • 10,5±0,5 ml em um frasco esteril de 20 mL para 5.000 doses
[00114] • A vacina granulada e agitada durante o carregamento e dispensadas nos recipientes finais por meio de uma maquina de pipetagem. As seringas de carregamento e tubos sao esterilizadas em uma autoclave antes do uso. Os recipientes finais sao esterilizados em fomo em panelas cobertas e resfriados naturalmente antes do carregamento. As rolhas de borracha, esterilizadas no autoclave, sao colocadas nos fiascos e um selo de alumfnio e aplicado. Os fiascos preenchidos sao armazenados em um refrigerador a 37°C.
[00115] Em certas circunstancias, as composigoes da vacina da presente invenção tambem podem incluir um adjuvante farmaceuticamente aceitavel. Os adjuvantes da presente invenção podem ser obtidos de quaisquer de inumeras fontes, incluindo de fontes naturais, fontes recombinantes, e/ou serem quimicamente sintetizados, etc. Os adjuvantes adequados para a vacinagao de animais incluem, mas sem limitagao, Adjuvante 65 (contendo oleo de amendoim, mono-oleato de manida e monoestearato de alumfnio); adjuvante completo ou incompleto de Freund; geis minerais, compostos de alumfnio, tais como hidroxido de alumfnio, fosfato de alumfnio e alumem; agentes tensoativos, tais como hexadecilamina, octadecilamina, lisolecitina, brometo de dimetildioctadecilamonio, N,N-dioctadecil-N',N'-bis (2hidroximetil) propanediamina, metoxi-hexadecilglicerol e poliois pluronicos; polianions, tais como pirana, sulfato de dextrano, poli IC, acido poliacrilico; peptfdeos, tais como muramil dipeptldeo, dimetilglicina e tuftsina e emulsoes oleosas. A informagao relacionada aos adjuvantes e revelada, por exemplo, na serie por P. Tijssen [Practice and Theory of Enzyme Immunoassays, 3a edigao, Elsevier, Nova lorque, (1987), aqui incorporado na sua Integra pela referenda].
[00116] Outros adjuvantes potenciais incluem, mas sem limitagao, oleos metabolizaveis e nao metabolizaveis, pollmeros bloco, ISCOM's (complexes de imunoestimulagao), vitaminas e minerais (incluindo, mas sem limitagao: vitamina E, vitamina A, selenio e vitamina B12), Quil A (saponinas), pollmeros de acido acrflico reticulado com eteres de polialquenila ou divinil glicol, vendido com o nome comercial CARBOPOL® (por exemplo, CARBOPOL® 941 ), e gotas de oleo de tamanho micro disperses uniformemente em emulsao aquosa (por exemplo, da maneira vendida com o nome comercial Emulsigen®).
[00117] Exemplos adicionais de adjuvantes, que algumas vezes sao referidos especificamente como estimulantes imunes, incluem componentes de parede celular bacteriana e fungica (por exemplo, lipopolisaccandeos, lipoprotelnas, glicoprotelnas, muramilpeptldeos, beta-2,3/1,6-glucanas), varios carboidratos complexos derivados de plantas (por exemplo, glicanas, acemanana), varias protelnas e peptfdeos derivados de animais (por exemplo, hormonios, citocinas, fatores co-estimulatorios) e acidos nucleicos ineditos derivados de virus e outras fontes (por exemplo, RNA de dupla fita, CpG). Alem do mais, qualquer numero de combinagoes das substancias anteriormente mencionadas pode fornecer um efeito adjuvante e, portanto, pode formar um adjuvante da presente invenção.
[00118] Uma vacina da presente invenção e facilmente administrada por qualquer via padrao, incluindo vacinagao por aspersao, intravenosa, intramuscular, subcutanea, oral (incluindo na ragao e/ou agua de beber), intranasal, intradermica e/ou intraperitonial. Os versados na tecnica entenderao que a composigao da vacina e preferivelmente formulada de maneira apropriada para cada tipo de recipiente animal e via de administragao.
[00119] Da maneira aqui demonstrada, E. meleagrimitis 2 (E. edgari) e uma nova especie patogenica de Coccidia para perus. Os passaros imunizados com uma combinagao de E. adenoeides, E. meleagrimitis 1, E. dispersa e E. gallopavonis (Coccivac-T) ou E. adenoeides e E. meleagrimitis (Immucox) ou E.meleagrimitis 1, como entidades unicas, nao foram protegidos contra E. meleagrimitis 2. E. meleagrimitis 2 foi isolada de operagoes de peru comercial de varios estados em todo os Estados Unidos e perus selvagens da regiao de Delmarva. Animais jovens hiper-imunizados por varias semanas com E. meleagrimitis 1, E. adenoeides e E. dispersa (E. MAD) e desafiados com os organismos suspeitos (E. meleagrimitis 2) exibiram sinais clmicos de parasitismo grave (depressao, falta de apetite e letargia) por 6,5 dias apos o desafio. A imunidade desenvolvida em animal jovem apos varios graus baixos de exposigoes, e imunidade, foi apenas com relagao a E. meleagrimitis 2.
[00120] E. meleagrimitis 2 invade as mesmas regioes intestinais as E. meleagrimitis 1 e E. dispersa, mas os oocistos de E. meleagrimitis 2 sao menores que aqueles destas duas outras especies. Os passaros imunizados com E. MAD nao foram protegidos contra E. meleagrimitis 2 e os passaros imunizados com E. meleagrimitis 2 nao foram protegidos contra E. meleagrimitis 1, E. adenoeides ou E. dispersa. E. meleagrimitis 2 parece ser relativamente prevalente nos Estados Unidos, sendo presentes em muitas das areas de crescimento de peru nos Estados Unidos. De fato, estima-se que a prevalencia de E. meleagrimitis 2 seja mais de 40 %, com estes organismos que sao identificados em amostras fecais da California, Iowa, Dakota do Norte e do Sul, Minessota, Pensilvania, Virginia, Wisconsin, Delaware e Maryland.
[00121] Fonte de Coccidia: Amostras fecais, amostras de detrito e ou amostras gastrointestinais foram avaliadas em virtude das epidemias da coccidiose em grupos comerciais de peru. Os organismos recuperados foram originalmente caracterizados como E. meleagrimitis tipo-1 com base na morfologia, regiao do trato gastrointestinal parasitado e sua patologia. As amostras foram obtidas de fazendas comercial de peru a partir dos seguintes estados: California, Iowa, Dakotas do Norte de do Sul, Pensilvania, Minessota e Virginia. Amostras fecais tambem foram obtidas de perus selvagens de Delaware e Maryland.
[00122] Patogenicidade e Patologia. O parasitism© com E. meleagrimitis 2 e acompanhado por produgao grave de muco na metade superior dos intestinos delgados e hemorragia moderada a grave ocorrendo do duodeno ao fleo a medida que a infecgao progride. As lesoes grandes apresentam hiperemia, muco em excesso no duodeno e jejuno, seguido por hemorragia na mucosa nos intestinos delgados. As fezes dos animais infectados sao aquosas, mucoides e sanguinolentas. Os parasitas invadem as celulas epiteliais do duodeno ate o reto e sao ocasionalmente observados no ceco.
[00123] Testes conduzidos: Teste de sensibilidade anticoccidial (AST): Amostras de Coccidia foram expandidas em perus jovens e os testes foram conduzidos para determianr a efetividade de anticoccidiais especificos contra varios dos isolados. Os isolados das fazendas comerciais mostraram tolerancia ou resistencia a CLINACOX® e AMPROL®. Nos casos de Iowa, California e Minnesota, foram relatadas falhas de CLINACOX® durante o periodo de uso. Como e agora sabido, os organismos predominantes foram E. meleagrimitis tipo 1, que foram aqui revelados e identificados como E. meleagrimitis 2. Os isolados de peru selvagem de Delaware e Maryland foram testados contra anticoccidiais especfficos, tais como CLINACOX® e AMPROL®. Os achados foram similares, os medicamentos demonstram pouca eficiencia contra os isolados do peru selvagem, tabela 1. E. meleagrimitis 1 de Coccivac®-T demonstrou tolerancia moderada a CLINACOX®, mas menos pronunciada do que a resposta de meleagrimitis 2.
[00124] Aos perus jovens crescidos em gaiolas foram dadas inoculagoes multiplas por varias semanas tanto com Coccivac™-T, uma combinagao de E adenoeides, E. dispersa e E. meleagrimitis 1 (Coccivac®-T) ou E. meleagrimitis 1, quanto com uma combinagao de E.adenoides e E. meleagrimitis 2 (Immucox™), ou E. meleagrimitis 2.
[00125] Os animais jovens form inicialmente inoculados nos primeiros sete dias de idade, e entao varias vezes nas proximas semanas. A inoculagao initial foi realizada por meio de gavagem e as inoculagoes subsequentes foram por meio de ragao. Cada dose subsequente foi duas vezes a dose previa. Desafio/Inoculacao de oocistos:
[00126] Em aproximadamente 28 dias, os passaros saudaveis foram selecionados e separados aleatoriamente em gaiolas de desafio. A cada passaro desafiado foi dado 1 mL de um material homologo ou heterologo. Lesao grande e classificacao microscopica.
[00127] Em 6 dias apos o desafio, todos os passaros foram eutanizados e os intestinos classificados por lesoes usando um sistema de 0 a 4. Os esfregagos foram montados umidos e preparados de seis areas de cada intestino, 1) duodeno, 2) jejuno, 3) divertfculo do saco vitelino (YSD), 4) ileo, 5) bolsa cecal (CP) e, 6) reto, para determinagao da carga do parasita usando um sistema 0 a 4+ (0 = sem parasitismo e 4 = parasitismo grave).
[00128] Os passaros imunizados com E. MAD e desafiados com um de varios materiais heterologos mostraram que os passaros nao foram protegidos contra o organismos desconhecido, aqui referido como E. meleagrimitis 2. O mvel de parasitismo variou de moderamente grave a grave (ver, tabela 1).
[00129] Nfvejs parasitismo em animais jovens hiper-imunizados com E. MAD e desafiados com isolado de campos de E. meleagrimitis 2A AIsolados de campos foram caracterizados por PCR como contendo E. meleagrimitis 2, bem como outra Eimeria em alguns casos. YSD = divertfculo do saco vitelino; CP = bolsa cecal; E. me2 = E. meleagrimitis 2
[00130] Imunizagao com E. meleagrimitis 1: Os passaros imunizados com E. meleagrimitis 1 e desafiados com um dos isolados de campo mostram que os passaros nao foram protegidos contra o organismo que e aqui revelado e definido como E. meleagrimitis 2. O mvel de parasitismo variou de moderadamente grave a grave (ver, tabela 2). Entretanto, os animais jovens desafiados com material homologo nao mostraram nenhuma lesoes grandes ou carga de parasita, (ver, tabela 2).
[00131] Nfveis je parasitismo em animais jovens hiper-imunizados com E. meleagrimitis 1 desafiados com isolados de campo de E. meleagrimitis 2A
AIsolados de campos foram caracterizados por PCR como contendo E. meleagrimitis 2, bem como outra Eimeria em alguns casos. YSD = divertfculo do saco vitelino; CP = bolsa cecal; E. me2 = E. meleagrimitis 2
[00132] Os passaros imunizados com IMMUCOX® e desafiados com um dos varios materials heterologos, incluindo Coccivac®-T, ou materiais homologos, mostraram que os passaros nao foram protegidos contra Coccivac®-T, mas fomeceram resultados mistos contra os organismos desconhecidos, aqui definidos como E meleagrimitis 2. O nivel de parasitismo variou de nenhuma a raras celulas parasitarias para E meleagrimitis 2 ate parasitismo grave para os organismos Coccivac®-T (ver, tabela 3).
[00133] Niveis de Parasitismo em animais jovens hiper-imunizados com IMMUCOX® desafiados com isolados de campo de E. meleagrimitis 2A ou E. MAD AIsolados de campos foram caracterizados por PCR como contendo E. meleagrimitis 2, bem como outra Eimeria em alguns casos. YSD = divertfculo do saco vitelino; CP = bolsa cecal; E. me2 = E. meleagrimitis 2
[00134] Imunizagao com E. meleagrimitis 2. Os passaros imunizados com E. meleagrimitis 2 e desafiados com um dos varios isolados de campo de E meleagrimitis 2 mostraram que os passaros foram protegidos. O mvel de parasitismo variou de nenhum a parasitismo leve, mas os passaros desafiados com E meleagrimitis 1 nao mostraram protegao medida pela carga do parasita no intestino delgado superior (ver, tabela 4).
[00135] Niveis de parasitismo em animais jovens hiper-himunizados com E. meleagrimitis 2 e desafiados com isolados de campos de E meleagrimitis 2A AIsolados de campos foram caracterizados por PCR como contendo E. meleagrimitis 2, bem como outra Eimeria em alguns casos. YSD = divertfculo do saco vitelino; CP = bolsa cecal; E. me2 = E. meleagrimitis 2
[00136] Patogenicidade e patologia. O parasitismo com esta especie e acompanhado por produgao grave de muco na metade superior dos intestinos delgados, com hemorragia moderada a grave ocorrendo do duodeno ao fleo a medida que a infecgao progride. As lesoes grandes apresentam hiperemia, muco em excesso no duodeno e jejuno, seguido por hemorragia na mucosa nos intestinos delgados, (ver, tabelas 5 e 6, figuras 1 e 2).
[00137] A gravidade de lesoes grandes e regioes intestinais afetadas por E. meleagrimitis 2 em animais hiper-imunizados contra E. meleagrimitis 1 ou E. meleagrimitis 2
E. mel = E. meleagrimitis 1; E. me2= E. meleagrimitis 2 ; NA = nao aplicavel
[00138] Gravidade das lesoes grandes e produgao de oocistos por passaro (OPB) em milhoes de animais jovens hiper-imunizados contra E. meleagrimitis 1 ou E. meleagrimitis 2 e desafiados com E. meleagrimitis 2 E. mel = E. meleagrimitis 1; E. me2= E. meleagrimitis 2 ; NA = nao aplicavel
[00139] Os dados dos estudos de imunizagao e imunizagao cruzada com Coccidia de diferentes fontes, as especies heterologas e homologas mostraram que animais jovens imunizados com E. meleagrimitis 1, E. adenoeides e E. dispersa (E. MAD) e desafiados com E. meleagrimitis 2 nao foram protegidos contra este desafio. Os animais jovens imunizados contra E. meleagrimitis 2 e desafiados com E. meleagrimitis 2 mostraram um alto grau de protegao, mas nao quando desafiados com E. meleagrimitis 1.
[00140] Eimeria meleagrimitis 2 (E. edgari sp.n.) da maneira aqui revelada. Os oocistos esporulados sao subesfericos, medindo 17,82 x 16,44 microns (16,92-19,55 x 14,5918,31 microns) com um mdice de forma de 1,084.
[00141] E. mealeagrimitis 1. Os oocistos esporulados sao subesfericos, medindo 21,47 x 19,19 microns (18,90-25,93 x 16,36-21,78 microns) comum mdice de forma de 1,119. Eimeria meleagrimitis 1, referenciada em nas doengas de Aves: Os oocistos esporulados sao subesfericos, medindo 19,2 x 16,3 microns com um mdice de forma de 1,178.
[00142] Materiais e Metodos. Quarenta perus comerciais jovens de 4 dias foram hiper-imunizados por um periodo de 28 dias com um estoque puro de E meleagrimitis 1 (E. me080121). Quarenta aves de quatro dias (chocadas juntas) foram mantidas sem Coccidia por alimentagao com AMPROL® a 125 ppm durante o periodo de crescimento. O AMPROL® foi removido 96 horas antes do desafio. Os passaros dos grupos hiper-imunizados e controle foram separados aleatoriamente em cinco grupos e desafiados com um dos cinco tratamentos, da maneira mostrada na tabela 1. Haviam sete passaros por grupo. Os perus foram considerados prontos para o desafio quando nenhum oocisto foi excretado nas fezes 5 a 6 dias apos a exposigao. O desafio foi realizado por gavagem oral e as galinhas foram eutanizadas e classificadas de acordo com as lesoes grandes da coccidiose em uma escala de 0 a 4 (sem lesoes a lesoes graves) no dia 6 apos o desafio. As classificagoes de lesao grande cumulativa do duodeno, intestino medio, ileo e ceco foram tabuladas (grandes). O intestino foi examinado por parasitemia microscopica (Micros) a 100X e classificado em uma escala de 0 a 4. Oocisto excretado foi determinado por coleta de fezes coletadas de cada passaro por um periodo de 48 horas do dia 4 aos dia 6. Os oocistos foram contados e tabulados por grama, por passaro (OPB). Ver tabela 1 para resultados. O ganho foi calculado como a diferenga no peso corporal do dia do desafio e dia 6.
[00143] Estudo de protegao cruzada em perus imunizados contra EMEI e desafiados com varios isolados medidos por ganho de peso e carga do parasitaE.mel -080121 = stock E. meleagrimitis 1 ; E.mel -071690 = stock E meleagrimitis 1 ; E.me2-WPC = isolado de campo de E meleagrimitis 2 = E. edgari', E.me2-Sundale = isolado de campo de E. meleagrimitis 2 = E. edgari', E.me2-UK = E meleagrimitis 2 estoque Resultados e Conclusoes
[00144] Os passaros imunizados com E.mel -080121 ficaram solidamente imunes quando desafiados com E. mel -080121, sem nenhuma lesao grande, nenhum oocisto excretado e nenhum parasita observado in situ. As galinhas imunizadas com E.me2-080121 mostraram imunidade solida quando desafiadas com E.mel -071690, sem nenhuma lesao, nenhum oocisto excretado e nenhum parasitas observado in situ', mas os parasitas E adenoeides foram observados no tecido cecal. As galinhas imunizadas com E.mel -080121 e desafiadas tanto com E.me2-UK, E.me2-WPC quanto E.me2-Sundale nao foram protegidas do desafio com E.mel, da maneira demonstrada por depressao de crescimento, lesoes grandes, parasitemia microscopica e oocisto excretado. Todos os isolados de E.me2 demonstraram patogenicidade em animais jovens naive com Coccidia. Patologias agressivas foram similares entre os isolados E.me2. E.mel e E.me2 nao foram similares.
[00145] Quatro cepas referencia de Eimeria em peru previamente classificadas pelos exame de sua patologia em passaros foram obtidas da Universidade da Georgia. A analise de sequencias de DNA foi realizada em fragmentos clonados amplificados por PCR da regiao ITS-1 (espa^adora transcrita interna um do agrupamento de DNA ribossomal 18S-5,8S-28S) de cada cepa, e as relagoes filogeneticas foram estabelecidas. Ao passo que, analises analogas foram realizadas para identificar diferentes isolados de Eimeria em galinhas, ate o momento, nenhuma analise como esta foi realizada em perus.
[00146] Os presentes resultados identificam as quatro especies de peru previamente classificadas, e inesperadamente identificam uma especie adicional de Eimeria em peru, que foi previamente agrupada com E. meleagrimitis 1 (ver, exemplo 1 anterior). A especie adicional, aqui revelada, caracterizada e descrita, foi denominada E meleagrimitis 2. Alem de classificar os varios isolados de peru dos Estados Unidos, os conjuntos de oligonucleotideo iniciador de PCR capazes de identificar cada uma das cinco especies sao tambem aqui revelados. Estes conjuntos de oligonucleotideo iniciador de PCR provaram, inter alia, serem uteis como ferramentas de diagnostico.
[00147] Uma vacina que foi usada por muito tempo para auxiliar na prevengao de coccidiose em peru, Coccivac-T®, contem oocistos vivos de quatro especies de Eimeria em peru: E. adenoeides, E. meleagrimitis (aqui identificada como E meleagrimitis 1), E. gallopavonis, e E dispersa. Previamente, a sequencia de nucleotfdeos da regiao ITS-1, localizada entre os genes ribossomais 18S e 5,8S no genoma de Eimeria, foi usada para estabelecer relagoes filogeneticas entre diferentes especies de Eimeria que infectam galinhas. O Genbank contem varios depositos desta regiao para varios isolados de galinha que auxiliam seu uso em isolados de especiagao, mas nao existem depositos comparaveis para especies de peru nesta regiao especifica.
[00148] Da maneira aqui revelada, os estoques de referenda de cada especie conhecida de Eimeria em peru foram obtidos de uma fonte bem respeitada e a sequencia ITS-1 foi entao determinada para cada um dos isolados obtidos. Uma comparagao foi realizada entre as sequencias dos estoque de referenda stocks e aqueles contidos em CoccivacT®. Alem do mais, uma analise da arvore filogenetica foi realizada. As analises de sequencia tambem foram usadas para determinam se os conjuntos de oligonucleotfdeo iniciador baseados nas quatro especies de peru previamente classificadas podem identificar inequivocamente todos os varios isolados. Materials e Metodos Estojos e geis comerciais: ver tabela 1 TABELA 1
[00149] Amostras de referenda de Eimeria (ver tabela 2) foram obtidas da Universidade da Georgia, em Atenas (UGA). Todos os isolados UGA de Eimeria foram previamente caracterizados pela patologia. Algumas das amostras foram isoladas do campo e, portanto, continham potencialmente especies multiplas. O DNA tambem foi isolado das especies na na vacina Coccivac-T® de peru contra Eimeria, which contem isolados de E. adenoeides, E. meleagrimitis, E. dispersa e E. gallopavonis. Alem do mais, o DNA e a informagao da sequencia das tres amostras europeias de Eimeria em peru foram obtidas. Estas amostras foram caracterizadas pela patologia e foram marcadas como E. adenoeides-EU, E. dispersa-EE e E. meleagrimitis 1-EU. Protocolo: • DNA foi isolado das amostras referencia UGA de Eimeria em peru (ver tabela 2). • A(s) regiao(s) ITS-1 de cada cepa referencia foram amplificadas por PCR usando conjunto de oligonucleotideo iniciador WWl/WW3r para amplificagao de ITS-1, e entao purificadas [ver tabela 5 para sequencia de oligonucleotideo iniciador, e figura 3A para seu local no genoma; Woods et al/. Electrophoresis 21 :3558-3563 (2000)]. • Cada fragmento de PCR foi clonado em um vetor plasmfdeo, pCR2.1 -TOPO, e o fragmento e sequenciado. • Os dados da sequencia foram analisados por um programa dispomvel comercialmente, [software de analise DNASTAR, Seqman, Editseq, Mapdraw, Megalign] e as relagoes filogeneticas de cepas referencia para cepas intemas foram determinadas (ver figura 4). • As discrepancias foram avaliadas entre as determinagaoes de especies obtidas pela patologia e por analise de sequencias usando amplificagao de PCR que emprega conjuntos de oligonucleotideo iniciador de especie de ITS-1 interna (ver tabela 5 para sequencias de oligonucleotideo iniciador, figura 3B para local no genoma e tabela 7). Procedimentos experimentais • Purificagao de oocistos por sacarose RDP 7416.0-01 (Manual/escala pequena). • Excistagao de esporocistos RDP 7423.0-01. • Oocistos suspensos 1 x 10e5 a 1 x 10e6 em 1 mL de PBS, usando um microtubo para centnfuga com tampa de 1,5 mL e adicionado um grama de vidro balllotini (esteril) [SIGMA 710-1,180 pm (peneira 16-25 U.S.)] ao tubo. Fechar a tampa. • Vortexar no maior ajuste por 1 minuto, e entao transferir a suspensao de esporocisto pipetando em um microtubo de centrifuga de 2 mL, e rinsar as microesferas com mais PBS ate q.s. em 2 mL • Centrifugar a suspensao de esporocisto (12.000 r.p.m. por 15 segundos em uma microcentiifuga), remover o sobrenadante, e ressuspender os esporocistos liberados em 200 pL de PBS. • A extragao do DNA de esporocistos liberados e realizada da maneira descrita no mini estojo Qiagen QIAamp DNA (protocolo de centrifugagao de sangue e fluido corporal): • Pipetar 20 pL de proteinase K no fundo de um microtubo de 1,5 mL. • Adicionar 200 pL de amostra no tubo, adicionar em 200 pL de tampao AL a amostra, misturar vortexando por pulso por 15 segundos. • Incubar a 56 °C por 10 minutos. • Centrifugar rapidamente para remover gotas de dentro da tampa, adicionar 200 pL de etanol e mistura novamente por 15 segundos. Centrifugar rapidamente para remover gotas de dentro da tapa. • Transferir a mistura a coluna de centrifugagao QIAamp, tampar e centrifugar a 8.000 rpm por 1 minuto, transferir a coluna para um tubo limpo de 2 mL, descartar o sobrenadante. • Adicionar 500 pL de tampao AW1, tampar e centrifugar a 8.000 rpm por 1 minuto, transferir a coluna para um tubo limpo de 2 mL, descartar o sobrenadante. • Adicionar 500 pL de tampao AW2, tampar e centrifugar a 14.000 rpm por 3 minutos, transferir a coluna para um tubo limpo de 1,5 mL, descartar o sobrenadante. • Adicionar 200 pL de tampao AE, tampar, incubar em temperatura ambiente por 1 minuto, e centrifugar a 8.000 rpm por 1 minuto para coletar o DNA elufdo. • Amplificagao por PCR de ITS-1 • Realizar as reagbes de PCR contendo 10 pL DNA molde, 1 pM de cada um dos oligonucleotfdeos iniciadores Woods ITS-1 sentido e anti-sentido (WW1 e WW3r), mistura master lx HotStar Taq, e agua sem RNase em um volume final de 50 pL. As condigbes do ciclo foram da maneira a seguir: 1 ciclo de 95 °C por 15 minutos; 35 ciclos de 95 °C por 30 segundos, 55 °C por 30 segundos, 72 °C por 30 segundos; e entao 1 ciclo de 72 °C por 7 minutos, seguido por uma espera a 4 °C. Um DNA molde controle positivo e um controle negative de agua (sem molde) foram incluidos para cada conjunto de oligonucleotfdeo iniciador. • Eletroforese de produtos de PCR RDP 7605.0-03 • Apos a amplificagao, 10 pL de cada reagao foram colocados em um E-Gel de agarose a 2 %, e a corrente foi aplicada por 15-30 minutos. A descrigao completa do uso de E-Geis e descrita no manual tecnico de E-Gel da Invitrogen. Estes geis contem brometo de etidio que se liga a quaisquer fragmentos de DNA, e permite que sejam visualizados e fotografados quando expostos a luz UV. Um DNA lider de 1-kb foi corrido em cada gel para comparagao de tamanho do fragmento de PCR. • Para purificar os fragmentos de PCR, um gel de agarose 2 % foi preparado em uma solugao de tampao TAE IX e 0,5 pg/mL de brometo de etfdio, seguindo as diretrizes descritas em RDP 7605.0-03. A mistura restante da reagao de PCR, ~40 pL, foi misturada com corante de peso Bluejuice lOx em uma concentragao final de lx, e entao colocada nos pogos do gel, e a corrente foi aplicada e eletroforizada ate que a boa separagao de todos os fragmentos foi obtida (85V por 60 minutos, seguido por 75V por 50 minutos.) Novamente, um DNA lider de 1-kb foi colocado como uma referenda de tamanho. O gel foi exposto a luz UV para visualizar os fragmentos de DNA. • Purificagao do gel dos produtos de PC • Uma vez que cada fragmento de PCR foi separado por eletroforese em agarose 2 %, um bisturi foi usado para cortar um bloco de gel de agarose contendo o fragmento de PCR, e o bloco de gel foi transferido para um microtubo pesado. • O volume do bloco de gel foi determinado por peso (1 miligrama igual a 1 pL de gel fundido). • O DNA foi extrafdo usando um estojo de extragao de gel da Qiagen, seguindo as instrugoes do fabricante, e o DNA foi eluido em um volume final de 200 pL. • Clonagem dos produtos de PCR em vetor de clonagem de pCR2.1-TOPO, e transformagao de plasmfdeo em E. coli. • Para clonar cada fragmento de PCR purificado, seguir as instrugoes dos fabricantes forecidas no estojo de clonagem TOPO TA, incluindo a transformagao de celulas de E.coli Top 10 competentes. • Plaquear celulas transformadas em placas de agar imMedia Amp, espalhadas com 40 pL de uma solugao 40 mg/mL de X-Gal e incubar a 37 °C por toda a noite. • Crescimento, extragao de DNA e analise de restrigao de Clones • Apos 20 -24 horas de crescimento bacteriano nas placas de transformagao, as colonias bacterianas de cor azul e brancas white e blue estao visfveis. • Duas colonias "brancas" de cada transformagao foram escolhidas para crescimento e analise. Cada colonia foi escolhida com um palito de dente esteril e inoculada em 3 mL de caldo Luria contendo 100 pg/mL de antibiotico carbenicilina. Cada tubo da culture foi entao aerado em 200 rpm em uma temperature de 37 °C for aproximadamente 16-20 horas. • O DNA foi extrafdo de 1,5 mL de cada culture por toda a noite usando um estojo Qiagen QIAprep Spin Miniprep. As instrugoes do fabricante foram seguidas, e o DNA foi eluido em um volume final de 50 pL. • A digestao por restrigao de cada preparado de DNA foi realizada com enzima EcoRI, e o material digerido colocado em um gel de agarose 1,5 % em tampao TAE IX e 0,5 pg/mL de brometo de etfdio. Cda reagao de digestao continha 5pL de DNA miniprep, 100 pg/mL de BSA, tampao de enzima EcoRI lx, 10 U de enzima e agua em um volume final de 20 pL. As misturas da reagao foram incubadas por mais de 2 horas a 37 °C, e entao o corante de peso foi adicionado em uma concentragao final de 1 %. A seguir, a mistura foi colocada no gel e eletroforizada a 95V por 41 minutos. A luz UV foi usada para visualizar os produtos de digestao. O DNA digerido a partir dos clones bacterianos contendo o fragmento de PCR desejado foi liberado do fragmento restante do plasmfdeo e pode ser identificado por comparagao com um padrao de tamanho de DNA. • Analise de sequencias de produtos de PCR clonados • O DNA purificado de cada clone contendo o fragmento de PCR desejado foi enviado para SeqWright DNA Technologies para reagoes de sequencia de corante grande usando oligonucleotfdeos iniciadores de sequenciamento que anelam-se ao vetor plasmfdeo, e lido no fragmento de PCR clonado. • Teste de identidade de PCR usando ITS-1 baseado nos conjuntos de oligonucleotideo iniciador • Reagoes realizadas de PCR contendo 10 pL de DNA molde, 1 pM de cada um dos oligonucleotfdeos iniciadores especie-especfficos sentido e anti-sentido, mistura master lx HotStar Taq, e aguas sem RNase em um volume final de 50 pL. As condigoes do cilco foram as seguintes: 1 ciclo de 95 °C por 15 minutos; 35 ciclos de 94 °C por 30 segundos, temperature de anelamento variavel (5565 °C) por 30 segundos, 72 °C por 30 segundos; a seguir 1 ciclo de 72 °C por 7 minutos, seguido por uma espera a 4 °C. As reagoes contendo conjuntos de oligonucleotideo iniciador para E. adenoeides ou E. meleagrimitis 2 usaram uma temperatura de anelamento de 60 °C. As reagoes contendo conjuntos de oligonucleotfdeo iniciador de E. dispersa ou E gallopavonis usaram uma temperatura de anelamento de 65 °C, e as reagoes contendo o conjunto de oligonucleotfdeo iniciador de E. meleagrimitis 1 usaram uma temperatura anelamento de 55 °C. Um molde de DNA controle positivo e um cotrole negativo com agua (sem molde) foram incluidos para cada conjunto de oligonucleotfdeo iniciador, e os resultados visualizados da maneira descrita anteriormente.
[00150] Criterios de validade e aceitabilidade do teste: o(s) produto(s) da regiao ITS-1 de PCR foi(m) amplificado(s) para todos os isolados. O numero e a sequencia da(s) regiao(s) ITS-1 para cada isolado puro foi(m) agrupado(s) em famflias. Os isolados contendo especies multiplas foram identificados com base na analise de PCR com conjuntos de oligonucleotfdeo iniciador especieespecifico.
[00151] O DNA foi extrafdo satisfatoriamente de todos os isolados UGA de Eimeria em peru. A amplificagao por PCR da(s) regiao(s) ITS-1 foi realizada em cada isolado de UGA, junto com os outros isolados dos Estados Unidos (exceto E. dispersa), e os fragmentos resultantes foram clonados em um plasmfdeo comercial para facilitar o sequenciamento. A regiao ITS-1 do isolado interno de E. dispersa foi amplificada, mas nao foi clonada ou sequenciada, ja que foi identificada usando oligonucleotfdeos iniciadores baseados na sequencia de E. dispersa-EU. Um unico clone para cada fragmento clonado de ITS-1 foi enviado para uma companhia de sequenciamento comercial [SeqWright DNA Technology Services of Houston, Texas] para realizar o sequenciamento por extensao do oligonucleotfdeo iniciador BigDye. Tanto as fitas sentido quanto anti-sentido foram sequenciadas para cada fragmento, e os dados brutos foram entao analisados usando software DNASTAR. A analise demonstrou sequencias nao ambiguas para todos os clones. Tabela 2 TABELA 3 TABELA 4 TABELA 5
Fonte da sequencia: SPAH US para E. meleagrimitis 1, E. adenoeides, E. gallopavonis, e E. dispersa c Fonte da sequencia: SPAH UK
[00152] Uma vez que a sequencia de cada fragmento ITS-1 foi determinada, o alinhamento e a analise filogenetica foram realizados nestas sequencias, bem como nas sequencias dos isolados europeus. Os resultados da analise filogenetica sao mostrados na figura 4. O alinhamento da analise da sequencia agrupou os vinte e cinco isolados nas cinco "especies". Os moldes de E. adenoeides amplificam um produto unicos de PCR de 419 base pares (bp) usando o conjunto de oligonucleotideo iniciador Woods ITS-1. Os moldes de E. dispersa rendem um produto unicos de ITS-Ide 409 bp. Todos os moldes de E. gallopavonis produzem dois produtos, de 534 bp e 392 bp em tamanho. O DNA dos isolados caracterizado originalmente como E. meleagrimitis amplifica um produto unico com os oligonucleotfdeos iniciadores Woods mas, surpreendentemente, os isolados sao segregados em duas famflias distintas. Os fragmentos de ITS-1 produzidos a partir destas duas famflias apresentam tamanhos diferentes e compartilham apenas 10,6 % de homologia. Uma famflia amplificou um produto de 405 bp, ao passo que a segunda, designada E. meleagrimitis 2, amplificou um produto de 500 bp. As sequencias dos fragmentos ITS-1 em cada grupo compartilham entre 96 % a 100 % de homologia, mas entre grupo compartilham apenas 10,6 % a 49,7 % de homologia. TABELA 6
[00153] Com poucas excegoes importantes, os agrupamentos baseados em sequencia das cepas referenda UGA combinaram com os agrupamentos baseados na patologia. Da maneira entendida na tecnica, nem todos os isolados estudados foram puros, e examinando a sequencia de um unico fragmento clonado por isolado, permaneceu a possibilidade de que alguns estoques continham multiplas especies, e que um clone de um contaminante de Eimeria tem que ser retirado de um estoque caracterizado. Para determinar se este e o caso onde um conflito existe entre a informagao da sequencia e a caracterizagao baseada na patologia, uma analise de PCR foi realizada usando os oligonucleotfdeos iniciadores especie-especificos.
[00154] Finalmente, os oligonucleotfdeos iniciadores de PCR que foram desenhados com base na sequencia segregaram EU E. meleagrimitis, da maneira aqui revelada como E. meleagrimitis 2, assim, estes oligonucleotfdeos iniciadores foram sintetizados e usados em um ensaio de PCR igualmente (ver tabela 5).
[00155] A analise de PCR com os oligonucleotfdeos iniciadores especieespecificos fomeceu os seguintes resultados: isolado UGA E. adenoeides 544066A foi positive tanto com oligonucleotfdeos iniciadores de E adenoeides quanto de E. meleagrimitis 2. Isolado UGA E adenoeides 544-066C foi positivo tanto com oligonucleotfdeos iniciadores de E adenoeides quanto de E. gallopavonis. Isolado de UGA E dispersa 544064A foi positivo tanto com oligonucleotfdeos iniciadores E. dispersa quanto com E. meleagrimitis 1. TABELA 7
[00156] Os isolados de Eimeria em peru foram estudados para aumentar o entendimento das relagoes filogeneticas entre as especies existentes, e para validar um teste de identificagao a base de PCR para os isolados de peru. As amostras referencia de todas as cepas Eimeria em peru conhecidas nos Estados Unidos foram obtidas de uma colegao da Universidade de Georgia, em Atenas (UGA), e seu DNA foi extrafdo. Este DNA foi entao submetido a amplificagao por PCR usando conjunto de oligonucleotideo iniciador da regiao Woods ITS-1, e os fragmentos resultantes foram clonados e sequenciados. A analise filogenetica das sequencias foi entao realizada, e os resultados comparados com isolados intemos de Eimeria em peru, e tres isolados europeus. Destas analises, uma quinta especie distinta foi identificada. Quatro especies de peru foram previamente reconhecidas com base na patologia da lesao, mas a presente analise de sequencias indica que uma das quatro, E. meleagrimitis, pode ser subdividida adicionalmente em duas especies separadas, E. meleagrimitis 1 e E. meleagrimitis 2. Adendo
[00157] Oligonucleotfdeos iniciadores de PCR adicionais tambem foram criados com base na sua sequencia ITS-1 dos isolados EU Eimeria em peru, e em uma sequencia ITS-1 "desconhecida" amplificada orginalmente de Coccivac-T®. A identidade destes estoques foi verificada no experimente descrito anteriormente. Estes oligonucleotfdeos iniciadores adicionais foram usados para identificar os estoques descritos a seguir. TABELA 8
[00158] O DNA de oito isolados de campo de Eimeria em peru foi isolado e suas regioes ITS-1, localizadas entre os genes ribossomais 18S e 5,8S, foram amplificados por PCR e clonados em um vetor E. coli. Ate cinco clones de cada isolado (a ate e) foram selecionados e sequenciados. As sequencias das regioes ITS-1 de cada clone foram entao comparadas com as sequencias referenda de E. meleagrimitis 2 do isolado EU-E.me2 e quatro isolados UGA-E. me2. Cada sequencia extende-se da primeira base apos o gene de RNA robossomal 18S ate o gene de RNA ribossomal 5,8S. Uma arvore filogenetica foi desenvolvida. As sequencias foram analisadas por similaridade e uma sequencia consensual foi gerada (SEQ ID NO: 44, ver a seguir). A sequencia inclui "N's" onde existem substitutes, insergoes ou delegoes. O tamanho que varia para as sequencias ITS-1 entre os oito isolados e 394-398 bases. A sequencia consensual, SEQ ID NO: 44, compartilha 87,2 88,5 % de homologia com os clones sequenciados Eme2 ITS1, comparado com a homologia de sequencia das oito sequencias umas com as outras, que mostram 93,8 100 % de homologia.
[00159] SEQ ID NOs. 13-44 referem-se as sequencias de nucleotfdeos das respectivas regioes ITS-1 e sao denotadas em letras maiusculas. SEQ ID NOs. 51-81 referem-se a sequencia completa de nucleotfdeos apresentados.
[00160] As sequencias mostradas a seguir nao incluem todas as sequencias 18S e 5,8S que preparam os fragmentos de PCR gerados pelos conjuntos de oligonucleotfdeo iniciador Woods WWl/WW3r.
[00161] O texto em negrito e a regiao 18S (oligonucleotfdeo iniciador WW1 e sublinhado)
[00162] O texto em italico e a regiao 5,8S (oligonucleotfdeo iniciador WW3R e sublinhado)
[00163] 544-065B: Grande fragmento 5’-> 3’ (534 bp) SEQ ID NO.: 51 [SEQ ID NO.: 13 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqKqcqjlaaataqaqccctctaaaqqatqcaaaaqtoqtaacacqgtttccgtaggtgaacctgcggaaqgaicattcACACGTAAAG CATGAAAGCAGGGAAAGATACTTTTTGATCTTATCCGTTTGTTGATTGTTGTGGGACAGTCAGCTTGCATG AGGGTTGGGTCACGAGTQTGTGCTGCTGTTCAGGCTTATCCGGGTGGGACAAAGATTAACAAOAAGCTGT AAATCTGTnTmCFCACAACGAGTTTTCTTTTTTTrGCCGAAAAAGTCTTTTTGCTGCTTCACTGTGTAGT. GCGGTGTGGQTGTGGCGGGAGGTGTTGTGATCTCCATAACTCCCCTCCCATGCA7CATCATGACCAGTG TTGGGTACTGGTrTGTTGGT<3CTGATAGGGGAACGrrATGTAGAGGACCCATAGCCGTTACAGAACGTTT CCGGCCTCAGTGTATTGCAGGGACTFTATTCTGTATATACTAACAGAATGTATATATGAAGCCAAAaaaiK® caacaataaatatctta
[00164] 544-065B: Grande fragmento 5’-> 3’ (392 bp) SEQ ID NO.: 52 [SEQ ID NO.: 14e a regiao ITS-1, mostrada em Letras Maiusculas] aagttqcqtaaataqaqgcctctaaa ggatg caaaagtcgtaacacggtttccgtaggtgaacctgcggaa ggatcattc AC AGGTAT A A AGCAfGAAAGCAGGAAGAGACATATTTCrrrTATTTQATCTCCTCCTATATCCTTCTTGAGAGATCTGCGTT TACGCGGG’n’GATCAAGTTTGGTGGrGGTTGGTCAATAGAAGAGGTGTCTTTrrGACTGGTCTTVT'CAGG CTTATTATGGGATAATATTCAACCGCAACCTG7AAATCTCTTTTTCCTCTCTCACAACAAGGAGTmCTGT AGATrGCAATTGATGCAAGTGTATTCTGTACGCTACAGAATATAAAGGTACAAAAAGAAAAAAaaaaefflease aatqgargtcrtQ
[00165]544-065C: Grande fragmento 5’-> 3’ (518 bp sequenciado) SEQ ID NO.: 53 [SEQ ID NO.: 15 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacgqtttccgtaqqtqaacctqcqqaaqqatcattcACACGTAAAG CATGAAAGCAGGGAAAGATACTTrnGATCTTATCCGTTTGTTGATTGTTGTGGGACAGICAGCTTGCATG CGGGTTGGGTCACGAGTGTCTGGTGCTGTTCAGGCTIATCCGGGTGGGACAAAGATTAACAACAACCTGT AAATCTGTTTTTTTCTCACAACGAGrrTrCTTTTTTTrGCCGAAAAAGTCTnTrGCTGCtTCACTGTGTAGT GCGGTGTGGGTGTGGCGGCAGGTGTTGTGATCTCCATAACTCCCCTCCCATGCATCATCATGACCAGTG TTGGGTACTGGTTTGTTGGTGCTGATAGGGGAACGTTATGTAGAGGACCCATAGCCGTTACACAACGTTT CCGGCCTCAGTGTArTGCAGGGACTTTATTCTGTATATACTAACAGAATGTATATATGAAGCCAAAaaaaG® c
[00166] 544-065C: Grande fragmento 5’-> 3’ (3928 bp) SEQ ID NO.: 54 [SEQ ID NO.: 16 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacgqtttccgtagqtgaacctgc.qgaagqatcattcACACGTATAA AGCATGAAAGCAGGAAGAGACATATrrCTTTTATTTGATCTCCTCCTATATCCTTCTTGAGAGATCIGCGTT TACGCGGCTTGATCAAGTTTGGTGGTGGTTGGTCAATAGAAGAGGTGTCTTTTrGACTGGTCTrTTCAGG CTTATTATGGGAYAATATTCAACCGCAACCTGTAAATCrCTTnTCCTCTCTCACAACAACGAGTrTTCTGT AGATTGCAATTGATGCAAGTGTATTCTGTACGCTACAGAA TATAAAGGTGCAAAAAGAAAAAAaaaaK^gs aataqatgicttg
[00167] 544-065C: Grande fragmento 5’-> 3’ (532 bp) SEQ ID NO.: 55 [SEQ ID NO.: 17 e a regiao ITS-1, mostrada em Letras Maiusculas] aatqcqtaaa’taqaniyctctaaaqcatccaaaaqtcqtaacacqqtttccqtagqlqaacctqcggF.aqgatcattcACACGTAAAGCATGAA AGCAGGGAAAGAfACTTITrGATCTTATCCGnTGTTGATTGTTGTGGGACAGTCAGCTTGCATGCGGGTT GGGTCACGAATGTCTGCTGCTGTTCAGGCTTATCCGGGTGGGACAAAGATTAACAACAACCTGTAAATCT GTTrnTrCTCACAACGAGTTTTCTTTiTTTTGCCGAAAAAGTCTTTTTGClGCT'rCACTGTGTAGTGCGGT GTGQGTGTGGCGGCAGGTGTTGTGATGTGCATAACTCCCCTCCCATGCATCATCATGACCAGTQTTGGGT ACTGGT nGTTOGTGCTGATAGGGGAACGn ATGTAGAGGACCCAIAGCCGTTACAGAAGGTTTCCGGCC TCAGTGTA'nGCAGGGACmATTCTGTATATACTAACAGAATGTATATATGAAGCCAAAaaaactttcaqcaalqq atqtcttq
[00168] 544-066A: Pequeno Grande fragmento 5’—> 3’ (417 bp) SEQ ID NO.: 56 [SEQ ID NO.: 18 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaaiaqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccgtaqqtgaacctgcggaaggatcattcACACGTGAAG CATGAAGGCAGAGAAAGGATGCTTTTGATCAGATATATCTGCTTTGCTTGTAGGTTTGCATTGGTTCTTGQ TAACAAGTCGCCAAGCAGA7TTGCATGCATGCAGTTTTGTGATCATTATTTATAGCGTCACTTTCTTTGACT GCTGTTTATGCTTTTGTTATGGATTGGACACACATTACAAAATCTGTAAATCTTTnTCTTTTCTCACAACGA GTTTTCTCTTTGAAATTTCTGGAAAGAAAGAATATAGATTGCTGGCTGTGTATGTACCAGCAGAATGTGTA G AAT GAAA AAGTT GA aaaactttcaqc.aatqqaf(]tcfta
[00169]544-066C: 'Pequeno fragmento 5’-> 3’ (417 bp) SEQ ID NO.: 57 [SEQ ID NO.: 19 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqgatqcaaaagtcgtaacacggtttccgtaggtqaacctgcggaaggatcattcACACGTGAAG CATGAAGGCAGAGAAAQGATGCTTTTGATCAGATATATCTGCTTTGCTTGTAGGTTTGCATTGGTTCTTGG TAACAAGTCGCCAAGCAGATTTGCATGCATGCAGTTTTGTGATCATTATTTATAGCGTCACTTTCTTTGGCT GCTGTTTATGCTTTTGTTATGGATTGGACACACATTACAAAATCTGTAAATCTTmTCTTTTCTCACAACGA GTrTTCTCTTTGAAATTTCTGGAAAGAAAGAATATAGATTGCTGGCTGTGTATGTACCAGCAGAATGTGTA GAATGAAAAAGTTGAaaaactttaffocaatgqafc?ta/tq
[00170] 544-066D: 5’-> 3’ (417 bp) SEQ ID NO.: 58 [SEQ ID NO.:20 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaaiaqaqccctctaaagqatqcaaaaqtcataacacqqtttccgtaqqtqaacctqcqqaaqqatcattcACACGTGAAG CATGAATGCAGAGAAAGGATGCTTTTGATCAGATATATCTGCTTTGCTFGTAGGTTTGCATTGGTTCTTGG TAACAAGTCGCCAAGCAGATTTGCATGCATGCAGTTTAGTGATCATTATTTATAGCGTCTCTTTCTTTGACT GCTGTTTATGCTTTTGTTATGGATTGGACACACATTACAAAATCTGTAAATCTTTTTTCTTTTCTCACAACGA GTTTTCTCTTTGAAATTTCTGGAAAGAAAGAATATAGATTGCTGGCTGTGTATGTACCAGCAGAATGTGTA
[00171] 544-066E 5’-> 3’ (416 bp) SEQ ID NO.: 59 [SEQ ID NO.:21 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqteacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACGTGAAG CATGAATGCAGAGAAAGGATGCTTTTGATCAGATATATCTGCTTTGCTTGTAGGTTTGCATTGGTTCTTGG TAACAAGTCGCCAAGCAGATTTGCATGCATGCAGTrrTGTGATCATTATTTATAGCGTCTCTTTCTTTGACT GCTGTTTATGCTTTTGTTATGGGTTGGACACACATTACAAAATCTGTAAATCTTTTTTCTTTTCTCACAACGA GTTTrCTCTTTGAAATTTCTGGAAAGAAAGAATATAGATTGCTGGCTGTGTATGTACCAGCAGAATGTGTA GAATGAAAAAGTTGAaaaacWca.acaafggafqtett
[00172] 544-064B 5’-> 3’ (409 bp) SEQ ID NO.: 60 [SEQ ID NO.:22 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaatagaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACATTCTG TCCAACAGGAGCTGGTATTCATTCATTTCTGTGTGAAATGGCATAGATGGGTGTTGCAAGCTTCCTGTCTT GGGCGGCTGAGTATTGAACCTTTTTATCCCTCCCACAACCTTTGAATCGGTTTGTTGAGTTTTCTTTCCAC GACGAGTTTTCTTAATATTTAAAAGAATGAAAGTTGCGCCCTTGCTGGCCACTCATTGAGAGCCGCATTTG TAACTGCTCTCGTGAGCAGTGGAAGCGGGGCTTTTTCAGTGAGTGGCTGCATGCGCGCATGCGTAATATT TATC AGCTCTT aaaacmcaqcaatqqatqM'.q
[00173] 544-064C 5’-> 3’ (409 bp) SEQ ID NO.: 61 [SEQ ID NO.:23 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttgcgtaaataqagccctctaaaggatqcaaaaqtcqtaacacggtttccqtagqtqaacctqcggaaggatcattcACACATTCTG fcCAACAGGAGCTGGTATTCATTCATTTCTGTGTGAAATGGCACAGATGGGTGTTGCAAGCTTCCTGTCTT GGGCGGCTGAGTATTGAACCTTTTTATCCCTCCCACAACCTTTGAATCGGTTTGTTGAGTTTTCTnCCAC GACGAGTTTTCTTAAAATTTAAAAGAATGAAAGTTGCGCCCTTGCTGGTCACTCATTGAGAGCCGCATTTQ TAACTGCTCTCGAGAGCAGAGGAAGCGGGGGTTTTTAGGTGAGTGGCTGCATGCGCGCATGCGTAATAT TTAT CAGCTCTT aaaactttcagcaatggatgtcttq
[00174] 544-067C 5’-> 3’ (405 bp) SEQ ID NO.: 62 [SEQ ID NO.:24 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaantaqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcAGACA i I i IC GGTCGCGCGAACAAAAGGAGCCTCTCTCTCCTCCGrrCACTCCTTTCTGCTGCAATTCAGTGGAATGTGG GGTGTGCAGATGGTCGTGTGTGACGGCTTTTTGTCTTGTTGGCCGACTGGAATCCTTTTTGAACCTTTTTA ATTCCTCCCAACCTTTGAATCGGTTAAGAGTTTTCTTCCCACGACGAGTTTTCTTTGAGAATAAAAGAGAAT GTGTTGCGCAGGTGGCTGCTTGCTCGTTGAGAGTGGCTGGGCTGCATGCGCGCATGCGAAGAGAGAAA AAAGGACCCaaaacfflcaqcaafqqatqCTq
[00175] 544-067D 5’-> 3’ (405 bp) SEQ ID NO.: 63 [SEQ ID NO.:25 e a regiao ITS-1, mostrada em Letras Maiusculas] aaattqcqtaaataqsQCCctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatoattcACACA I I I ICGGTCG CGCGAACAAAAGGAGCCTCTCTCTCCTCTGTTCACTCCTTTCTGCTGCAATTCAGTGGAATGTGGGGTGT GCAGATGGTCGTGTGTGACGGCTnTTGTCTTGTTGGCCGACTGGAATCCTTTTTGAACCTTTTTAATTCC TCCCAACCTTTGAATCGGTTAAGAGTTTTCTTCCCACGACGAGTTTTCTTTGAGAATAAAAGAGAATGTGTT GCGCAGGTGGCTGCTCGCTCGTTGAGAGTGGCTGGGCTGCATGCGCGCATGCGAAGAGAGAAAAAAGG ACCCaaaactftcaqcaatqqatatcttq
[00176] 544-067E 5’-> 3’ (404 bp) SEQ ID NO.: 64 [SEQ ID NO.:26 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcgtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccgtaqqtqaacctqcqqaagqatcattcACACAI 11 iC GGTCGCGCGAACAAAAGGAGCCTCTCTCTCCTCCGTTCACTCCTTTCTGCTGCAATTCAGTGGAATGTGG GGTGTGCAGATGGTCGTGTGTGACGGCTTTTTGTCTTGTTGGCTGACTGGAATCCTTTTTGAACCTTTTTA ATTCCTCCCAACCTTTGAATCGGTTAAGAGTTTTCTTCCCACGACGAGTTTTCTTTGAGAATAAAAGAGAAT GTGTTGCGCAGGTGGCTGCTCGCTCGTTGAGAGTGGCTGGGCTGCATGCGCGCATGCGAAGCGAGAAA AAAGGACCCaaaactticaqcaaiqqafotctt
[00177] 544-067F 5’-> 3’ (405 bp) SEQ ID NO.: 65 [SEQ ID NO.:27 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACATTTTC GGTCGCGCGAACAAAAGGAGCCTCTCTCTCCTCCGTTCACTCCTTTCTGCTGCAATTCAGTGGAATGTGG GGTGTGCAGATGGTCGTGTGTGACGGCTTTTTGTCTTGTTGGCCGACTGGAATCCTTTTTGAACCTTTTTA ATTCCTCCCAACCTTTGAATCGGTTAAGAGnTrCTTCCCACGACGAGTTTTCTTTGAGAATAAAAGAGAAT GTGTTGCGCAGGTGGCTGCTCGCTCGTTGAGAGTGGCTGGGCTGCATACGCGCATGCGAAGCGAGAAA AAAGGACCCaaaacfflcaqcaatfl,<?a*qtaffa
[00178] 544-067G 5’-> 3’ (407 bp) SEQ ID NO.: 66 [SEQ ID NO.:28 e a regiao ITS-1, mostrada em Letras Maiusculas]
[00179] 544-064A 5’ÿ 3’ (405 bp) SEQ ID NO.: 67 aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaaGctqcqqaaqqatcattcACACAi J11C GGTCGCGCGAACAAAAGGAGCCTCTCTCTCCTCCGTTCACTCCTTTCTGCTGCAATTCAGTGGAATGTQG GGTGTGCAGATGGTCGTGTGTGACGGCTTTTTGTCTTGTTGGCCGACTGGAATCCTTTTTGAACCTrTTTA ATTCCTCCCAACC’TTTGAATCGGTTAAGAGTTTTCTTCCGACGACGAGTTTTCTTTGAGAATAAAAGAGATG TGTTGCGCAGGTGGCTGCTCGCTCGTTGAGAGTGGCTGGGCTGCATGCTGCGCGCATGCGAAGAGAGA AAAAAGGACCCaaaacfflcaqcaaftwa/qtoffc? [SEQ ID NO.:29 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqBaqqatcattcACACArnTC GGTCGCGCGAACAAAAGGAGCCTCTCTCTCCTCCGTTCACTCCTTTCTGCTGCAATTCAGTGGAATGTGG QGTGTGCAGATGGTCGTGTGTGACGGCTTTTTGTCTTGTTGGCCGACTGGAATCCTTTTTGAACCTTTTTA ATTCCTCCCAACCTTTGAATCGGTTAAGAGTnTCTTCCCACGACGAGTTTTCTTTGAGAATAAAAGAGAAT GTGTTGCGCAGGTGGCTGCTCGCTCGTTGAGAGTGGCTGGGCTGCATGCGCGCATGCGAAGAGAGAAA AAAGGACCCaaaacfflcaqcaatoqaMcftg
[00180] 544-065A5’^ 3’ (405 bp) SEQ ID NO.: 68 [SEQ ID NO.:30 e a regiao ITS-1, mostrada em Letras Maiusculas] Isolados de UGA E. meleagrimitis
[00181] 544-066A Grandes fragmentos 5’-> 3’ (500 bp) SEQ ID NO.: 69 [SEQ ID NO.:31 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqlaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACATTTTC GGTCGCGCGAACAAAAGGAGCCTCTCTCTCCTCCGTTCACTCCTTTCTGCTGCAATTCAGTGGAATGTGG GGTGTGCAGATGGTCGTGTGTGACGGCTTTTTGTCTTGTTGGCCGACTGGAATCGTTTTTGAACCTTTTTA ATTCCTCCCAACCTTTGAATCGGTTAAGAGTTTTCTTCCCACGACGAGTTTTCTTTGAGAATAAAAGAGAAT GTGTTGCGCAGGTGGCTGCTCGCTCGTTGAGAGTGGCTGGGGTGCATGCGCGCATGCGAAGAGAGAAA AAAGGACCCaaaacfflcagcaatoqafqfcffq
[00182] 544-067A 5’-> 3’ (502bp) SEQ ID NO.: 70 [SEQ ID NO.:32 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACGTGATG CATGCAGCAAGCTGGAAAGGTGCCTGTTTGTATGTGGGAAGTGCATTTATTATGCACACCTGCATTCATG CGAGGTTACTGTCAATCCGGCGACTGCATGTATGGCTTCTTGGACCGCAATAACAACCTGTAAATCTCTTT TCTTCTCCACAACGGTTTTrCTTTTGTTTAGGGTACTTTATTTGTGTACCACAACTATAAGTTGTTGGGGTTT TCAGCTGCTTCACTGTGCTACTGGATGATAGGCTAGCTGCATTTGTTTTGCCGGTCGGGGTTGTTGTTCG GCAGGCACAGCATGGCAGCAGGGCTGTCGGCAGTGGCAGGTGTTTGCAGTTGTGTACCATTTAATTCTG CTAAAGAGCAGAATGAI I iGTTIACAAAAAAAaaaacfttcaqcaafqqatateftq
[00183] 544-067B 5’-> 3’ (503 bp) SEQ ID NO.: 71 [SEQ ID NO.:33 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACGTGATG CATGCAGCAAGCTGGAAAGGTGCCTGTTTGTATGTGGGAAGTGCATTTCTTATGCACACCTGCATGCATG TGAGGTTACTGTCAAGCCGGCGACTGCATGTATGGCTTCTTGGACCGCAATAACAACAACCTGTAAATCT CTTTTCCTCTCCACAACGGTTTTTCTTTTGTTTACGGTACTTTATrTGTGTACCACAACTATAAGTTCTTGGG GTTTTCAGCTGCTTCACTGTGCTACTGGATGATAGGCTAGCTGCATTTGTTrrGCCAGTCGGGGTTGCTGT TTGGCAGGCACAGCATGGCAGCAGGGGTGTTGGCAGTTGCAGTGTTTGCAGTTGTATACCATTTAATTCT GCTGAAGAGCAGAATGTTTTGTTTACAAAAAAAaaaacfflcaqcaafqqafofctta
[00184] 544-068A 5’-> 3’ (501 bp) SEQ ID NO.: 72 [SEQ ID NO.34 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACJACGTGATG CATGCAGCAAGCTGGAAAGGTGCCTGTTTGTATGTGGGAAGTGCATTTCTTATGCACACCTGCATGCATG TGAGGTTACTGTCAAGCCGGCGACTGCATGTATGGCTTCTTGGACCGCAATAACAACAACCTGTAAATCT CTTTTCCTCTCCACAACGGTTTTTCTTTTGTTTACGGTACTTTATTTGTGTACCACAACTATAAGTTCTTGGG GTTTTCAGCTGCTTCACTGTGCTACTGGATGATAGGCTAGCTGCATTTGTTTTGCCAGTCGGGGTTGCTGT TTGGCAGGCACAGCATGGCAGCAGGGGTGTTGGCAGTTGCAGTGTTTGCAGTTGTATACCATTTAATTCT GCTGAAGAGCAGAATGI T n GT FTAGAAAAAAAAaaaacfffgaacagtqqatqfcffq
[00185] E.adenoeides SPAH-US (CAD) 5’ÿ 3’ (417 bp) SEQ ID NO.: [SEQ ID NO.37 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaflccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacclqcqqaaqqatcattcACACGTGATG CATGCAGCAAGCTGGAAAGGTGCCTGTTTGTATGTGGGAAGTGCATTTCTTATGCACACCTGCATGCATG TGGGGTTACTGTCAATCCGGCGACTGCATGTATGGCTTCTTGGACCGCAATAACAACAACCTGTAAATCT CTTTTCTTCTCCACAACGGTTTTTCCTtTGTTTACGGTGCTTTATTTGTGTACCACAACTATAAGTTGTTGG GGTTTTCAGCTGCTTCACTGTGCTACTGGATGACCGGCTAGCTGCATrTATrn'GCCAGTCGGGGTTGCT GTTCGGCAGGCACAGCATGGCAGCAGGGCTGTCGGCAGTGGCAGGTGTTTGCAGTTGTATACCATrrAA TTCT GCTGA AGAGCAGAAT GTTTT GTTT AC AAAAAaaaacfflcaqcaatgqafafcfta
[00186] E.meleagrimitis SPAH-US (Erne) 5’-> 3’ (403 bp) SEQ ID NO.: 76 [SEQ ID NO.38 e a regiao ITS-1, mostrada em Letras Maiusculas] aaBttqcqtaaataqaqccctctaaaqqatqcaaaaqtoqtaacacqqtttccqtaqgtqaacctqcqqaaqqatcattcACACGTGAAG CATGAAKGCAGAGAAAGGATGCTTTTGATCAGATATATCTGCTTTGCTTGTAGGTTTGCATTGGTTCTTGG TAACAAGTCGCCAAGCAGATTTGCATGCATGCAGTTTTGTGATCATTATTTATAGCGTCTCTTTCTTTGACT GCTGTTTATGCTTTTGTTATGGATTGGACACACATTACAAAATCTGTAAATCTrTTTTCTTTTCTCACAACGA GTTTTCTCTTTGAAATTrCTGGAAAGAAAGAATATAGATTGCTGGCTGTGTATGTACCAGCAGAATGTGTA GAAT GAAA AAGTT GAAaaacfflcaqcaafcrqatatottq
[00187] E.gallopavonis SPAH-US (Ega) Grande fragmento 5’—> 3’ (538 bp) SEQ ID NO.: 77 [SEQ ID NO.39 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACATTTTC GGTCGCGCGAACAAAAGGAGCCTCTCTCTCCTCCGTTCACTCCmCTGCTGCAATTCAGTGGAATGTGG GGTGTGCAGATGGTCGTGTGTGACGGCTTTTTGTCTTGTTGGCCGACTGGAATCCTTTTTGAAC.CTmTA ATTCCTCCCAACCTTTGAATCGGTTAAGAGT1TTCTTCCCACGACGAGTTTTCTTTGAGAATAAAAGAGAAT GTGTTGCGCAGGTGGCTGCTCGCTCGTTGAGAGTGGCTGGGCTGCATGCGCGCATGCGAAGAGAGAAA AAAGGACCCAaaacfflcaqca.a/qqafqtef
[00188] E.gallopavonis SPAH-US (Ega) Pequeno fragmento 5’-> 3’ (392 bp) SEQ ID NO.: 78 [SEQ ID NO.40 e a regiao ITS-1, mostrada em Letras Maiusculas] taaqttqcqqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACGTAAA GCATGAAAGCAGGGAAAGATACTTTTTGATCTTATCCGTTTGTTGATTGTTGTGGGACAGTCAGCTrGCAT GCGGGTTGGGTCACGAGTGTCTGCTGCTGTTCAGGCTTATCCGGGTGGGACAAAGATTAACAACAACCT GTAAATCTGTTTTTTTCTCACAACGAGTTTTCTTTTTTTTGCCGAAAAAGTCTTTTTGCTGCTTCACTGTGTA GTGCGGTGTGGGTGTGGCGGCAGGTGTTGTGATCTCCATAACTCCCCTCCCATGCATCATCATGACCAG TGTTGGGTACTGGTTTGTTGGTGCTGATAGGGGAACGTTATGTAGAGGACCCATAGCCGTTACACAACGT TTCCGGCCTCAGTGTATTGCAGGGACTTTATTCTGTATATACTAACAGAATGTATATATGAAGCCAAAAaaa ctffcaqcaafqqaafqtcftqa Isolados de Referenda EU
[00189] E.meleagrimitis5’-> 3’ (4753 bp) SEQ ID NO.: 73 [SEQ ID NO.35 e a regiao ITS-1, mostrada em Letras Maiusculas] aaqttqcqtaaataqaqccctctaaaqqatqcaaaaqtcqtaacacqqtttccqtaqqtqaacctqcqqaaqqatcattcACACGTATAA AGCATGAAAGCAGGAAGAGACATATTTCTTTTATTTGATCTCCTCCTATATCCTTCTTGAGAGATGTGCGTT TACGCGGCTTGATCAAGTTTGGTGGTGGTTGGTCAATAGAAGAGGTGTCTTTTTGACTGGTCTTTTCAGG CTTATTATGGGATAATATTCAACCACAACCTGTAAATCTCTTTTTCCTCTCTCACAACAACGAGTTTrCTGTA GATTGCAATTGATGCAAGTGTATTCTGTACGCTACAGAATATAAAGGTACAAAAAGAAAAAAAaaaacrrtragc
[00190] E.gallopavonis Grande fragmento 5’—> 3’ (506 bp) SEQ ID NO.: 74 [SEQ ID NO.36 e a regiao ITS-1, mostrada em Letras Maiusculas] gcatgcagtcgtacacggtttccgtaggtgaacctgcggaaggatcattcACACGTGATGCATGCAGCAAGCTGGAAAGGTG CCTGTTTGTATGTGGGAAGTGCATTTCTTATGCACACCTGCATTCATGCGAGGTTACTGTCAATCCGGCGA CTGCATGTATGGCTTCTTGGACCGCAATAACAACAACCTGTAAATCTCTTTTCCTCTCCACAACGGTTTTTC TTTTGTTTACGGTACTTTATTTGTGTACCACAACTATAAGTTGTTGGGGTTTTCAGCTGCTTCACTGTGCTA CTGGATGATAGGCTAGCTGCATTTGTTTTGCCGGTCGGGGTTGTTGTTCGGCAGGCACAGCATGGCAGC AGGGCTGTCGGCAGTGGCAGGTGTTTGCAGTTGTATACCATTTAATTCTGCTAAAAAGCAAAATGTTTTGT TTACAAAAAAAAAATTTTTCAACGGTGGTTTTGAGGAA
[00191] E.gallopavonis Pequeno fragmento 5’—> 3’ (355 bp) SEQ ID NO.: 79 [SEQ ID NO.41 e a regiao ITS-1, mostrada em Letras Maiusculas] gtcgtcaagtcgtacacggtttccgtaggtgaacctgcggaaggatcattcACACGTAAAGCATGAAAGCAGGGAAAGATACT TTTTGATCTTATC.CGTTTGTTGATTGTTGTGGGACAGTCAGCTTGCATGCGGGTTGGGTCACGAGTGTCTG CTGCTGTTCAGGCTTATCCGGGTGGGACAAAGATTAACAACAACCTGTAAATCTGTTTTnTCTCACAACG AGTTTTCTTTTTTTTGCCGAAAAAGTCTTTTTGCTGCTTCACTGTGTAGTGCGGTGTGGGTGTGGCGGCAG GTGTTGTGATCTCCATAACTCCCCTCCCATGCATCATCATGACCAGTGTTGGGTACTGGTrrGTTGGTGCT GATAGGGGAACGTTATGTAGAGGACCCATAGCCGTTACACAACGTTTCCGGCCTCAGTGTATTGCAGGGA CTTTATTCTGTATATACTAACAGAATGTATATATGAAGCCAAAAaaacfficaqcaatqoafqfoffqa
[00192] E. dispersa 5’-> 3’ (373 bp) SEQ ID NO.: 80 [SEQ ID NO.42 e a regiao ITS-1, mostrada em Letras Maiusculas] gtaatcagtcgtacacggtttccgtaggtgaacctgcggaaggatcatteACACGTATAAAGCATGAAAGCAGGAAGAGACAT ATTTCTTTTATTTGATCTCCTCCTATATCCTTCTTGAGAGATCTGCGTTTACGCGGCTTGATCAAGTTTGGT GGTGGTTGGTCAATAGAAGAGGTGTCTTTTTGACTGGTCTTTTGAGGCTTATTATGGGATAATATTCAACC GCAACCTGTAAATCTCTTTTTCCTCTCTCACAACAACGAGT7TTCTGTAGATTGCAATTGATGCAAGTGTAT TCTGTACGCTACAGA ATATAAAGGTACAAAAAGAAAAAA aaaacWcaqcaaqqqa
[00193] E.meleagrimitis -2 SPAH-UK 5’-> 3’ (268 bp) SEQ ID NO.: 81 [SEQ ID NO.43 e a regiao ITS-1, mostrada em Letras Maiusculas] cggtttecgtaggtgaacctgcggaaggatcattcACACGTGATGCATGCAGCAAGCTGGAAAGGTGCCTGTTTGTATGTG GGAAGTGCATTTCTTATGCACACCTGCATGCATGTGAGGTTACTGTCAATCCGGCGACTGCATGTATGGC TTCTTGGACCGCAATAACAACAACCTGTAAATCTCTTTTCCTCTCCACAACGGTTTTTCTTTTGTTTACGGT ACTTTATTTGTGTACCACAACTATAAGTTGTTGGGGTTTTCAGCT Sequencia de consenso E.meleagrimitis -2
[00194] Sequencia de consenso E.meleagrimitis -2 5’-» 3’ (409 bp) SEQ ID NO.: 44 ACACGTGANGCATGCANNNAGCTGGAAANNTNGCCTGTTTGTATGTGGGAAGTGCATTTNTTATGCACAC CTGCATNCATGNGNGGTTACTGTCAANCCGGCGANCTGCATGTATGGCTTCTTGGACCGCAATAACANNN ACCTGTAAATCNCTTTTNNTCTCCACAACGGTTTTTCNTTTGTTTACGGTNCTTTATTTGTGTACCACAACT ATAAGTTNTTGGGGTTTTCNGCTGCTTCACTGTGCTACTGGNTGANNNNNNGGCTAGCTGCATTTNTTTTG CCNGTCGGGGTTGNTGTTNGGCAGGCNCAGCATGGCAGCAGGGNTGTNGGCAGTNGCAGNNGTTTGCA GTTGNNTACNATTTANTTCTGCTNAANAGCANNATGNTTTGTTTACAAAAAAAANNNN (5.8S end) Onde “N” pode ser qualquer nucleotfdeo ou nenhum nucleotfdeo
[00195] Entende-se que esta invenção nao e limitada a configuragoes, etapas do processo e materials particulares aqui revelados, tais como configuragoes, etapas do processo e materials, que podem variar um pouco. Entende-se tambem que a terminologia aqui empregada e usada com o proposito apenas de descrever modalidades particulares e nao pretende-se que sejam limitantes, uma vez que o escopo da presente invenção sera limitado apenas as reivindicaçoes em anexo e equivalentes destas.
Claims (15)
1. Composiçao de vacina, caracterizada pelo fato de que compreende E. meleagrimitis 2 eE. meleagrimitis 1.
2. Composiçao de vacina de acordo com a reivindicação 1, caracterizada pelo fato de que compreende adicionalmente uma ou mais especies adicionais de Eimeria selecionadas do grupo que consiste em E. adenoeides, E. gallopavonis, E. dispersa, E. innocua e E. subrotunda.
3. Composiçao de vacina de acordo com a reivindicação 2, caracterizada pelo fato de que a especie adicional de Eimeria Q E. adenoeides.
4. Composiçao de vacina de acordo com a reivindicação 3, caracterizada pelo fato de que compreende adicionalmente E. meleagridis.
5. Composiçao de vacina de acordo com a reivindicação 3, caracterizada pelo fato de que compreende adicionalmente E. dispersa.
6. Composiçao de vacina de acordo com a reivindicação 1, caracterizada pelo fato de que compreende adicionalmente um parasita do genero Coccidia selecionado do grupo que consiste em Isospora, Cystoisospora, e Cryptosporidium.
7. Composiçao de vacina de acordo com a reivindicação 1, caracterizada pelo fato de que E. meleagrimitis 2 e uma cepa nao atenuada.
8. Composiçao de vacina de acordo com a reivindicação 7, caracterizada pelo fato de que E. meleagrimitis 1 e uma cepa nao atenuada.
9. Composiçao de vacina de acordo com a reivindicação 8, caracterizada pelo fato de que compreende de cerca de 10 a cerca de 1000 oocistos de cada E. meleagrimitis 2eE. meleagrimitis 1.
10. Composiçao de vacina de acordo com a reivindicação 1, caracterizada pelo fato de que E. meleagrimitis 2 & uma cepa atenuada.
11. Composiçao de vacina de acordo com a reivindicação 10, caracterizada pelo fato de que E. meleagrimitis 1 e uma cepa atenuada.
12. Composiçao de vacina de acordo com a reivindicação 11, caracterizada pelo fato de que a quantidade de oocistos e de cerca de 100 a cerca de 10000 oocistos de cada E. meleagrimitis 2 QE. meleagrimitis 1.
13. Composiçao de vacina de acordo com a reivindicação 1 caracterizado pelo fato de que compreende merozoitas.
14. Uso de uma composiçao como definida em qualquer uma das reivindicaçoes 1 a 13, caracterizado pelo fato de ser na manufatura de um medicamento para imunizar um peru contra a coccidiose.
15. Uso de uma composiçao contra E meleagrimitis 2 que compreende uma quantidade imunologicamente efetiva E. meleagrimitis 2, caracterizado pelo fato de ser na manufatura de um medicamento para imunizar um peru contra a coccidiose.
Applications Claiming Priority (3)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| US11420808P | 2008-11-13 | 2008-11-13 | |
| US61/114,208 | 2008-11-13 | ||
| PCT/US2009/063977 WO2010056709A2 (en) | 2008-11-13 | 2009-11-11 | Eimeria vaccine for turkeys |
Publications (2)
| Publication Number | Publication Date |
|---|---|
| BRPI0921843A2 BRPI0921843A2 (pt) | 2018-10-09 |
| BRPI0921843B1 true BRPI0921843B1 (pt) | 2020-11-24 |
Family
ID=41786412
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| BRPI0921843-2A BRPI0921843B1 (pt) | 2008-11-13 | 2009-11-11 | composição de vacina, e, uso de uma composição de vacina |
Country Status (8)
| Country | Link |
|---|---|
| US (1) | US8252292B2 (pt) |
| EP (1) | EP2355844A2 (pt) |
| AU (1) | AU2009314192A1 (pt) |
| BR (1) | BRPI0921843B1 (pt) |
| CA (1) | CA2743262C (pt) |
| CL (1) | CL2011001097A1 (pt) |
| MX (1) | MX2011005133A (pt) |
| WO (1) | WO2010056709A2 (pt) |
Families Citing this family (4)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| CA2725361C (en) * | 2008-05-29 | 2017-05-16 | Intervet International B.V. | Coccidiosis vaccines |
| US9603915B2 (en) | 2013-02-14 | 2017-03-28 | The Board of Trustees of the University of Akansas | Compositions and methods of enhancing immune responses to Eimeria or limiting Eimeria infection |
| BE1028702B1 (nl) * | 2020-10-13 | 2022-05-16 | Poulpharm Bvba | Biobank en werkwijze voor het in stand houden van deze biobank |
| CN115927691B (zh) * | 2022-08-01 | 2026-03-17 | 山西农业大学 | 一种检测鸡球虫的四重pcr引物组、试剂盒 |
Family Cites Families (29)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| JPS5649323A (en) * | 1979-09-29 | 1981-05-02 | Nisshin Flour Milling Co Ltd | Coccidiostat |
| JPS5780325A (en) * | 1980-09-05 | 1982-05-19 | Nat Res Dev | Coccidial disease vaccine |
| GB8326633D0 (en) | 1983-08-04 | 1983-11-09 | Unilever Plc | Compositions |
| JP3020226B2 (ja) * | 1986-08-18 | 2000-03-15 | ブリティッシュ・テクノロジー・グループ・リミテッド | ワクチン |
| US4935007A (en) * | 1986-08-28 | 1990-06-19 | Eli Lilly And Company | Anticoccidial method |
| KR960003379B1 (ko) | 1986-08-28 | 1996-03-09 | 일라이 릴리 앤드 캄파니 | 개선된 콕시듐증 예방법 |
| GB8711256D0 (en) * | 1987-05-13 | 1987-06-17 | Unilever Plc | Protection |
| ZA954785B (en) * | 1994-06-16 | 1996-02-08 | Yamanouchi Pharma Co Ltd | Crude drug-containing feed |
| FI974439A7 (fi) * | 1995-06-07 | 1998-01-27 | Pfizer | In ovo-rokotus kokkidioosista vastaan |
| MX9709870A (es) * | 1995-06-07 | 1998-03-31 | Pfizer | Uso de esporocistos u occistos para preparar una vacuna contra coccidiosis. |
| CA2213385A1 (en) | 1997-08-20 | 1999-02-20 | Eng-Hong Lee | Method of protecting against coccidiosis infections in poultry |
| CA2214233A1 (en) * | 1997-08-29 | 1999-02-28 | Eng-Hong Lee | Method for assessing viability of live microbial therapeutic agents |
| AUPP268398A0 (en) * | 1998-03-30 | 1998-04-23 | Eimeria Pty Limited | Vaccination modalitites |
| DE19828322A1 (de) | 1998-06-25 | 1999-12-30 | Hoechst Roussel Vet Gmbh | Coccidienvakzine, Verfahren zu ihrer Herstellung und ihre Verwendung |
| US7247309B2 (en) * | 1999-12-21 | 2007-07-24 | Intervet International B.V. | Coccidiosis vaccines |
| AUPQ622900A0 (en) | 2000-03-15 | 2000-04-06 | University Of Melbourne, The | Pcr-based identification of eimeria species and strains |
| US6432646B1 (en) * | 2000-03-16 | 2002-08-13 | The University Of Melbourne | PCR-based identification of Eimeria species and strains |
| CA2428110A1 (en) | 2000-11-08 | 2002-05-16 | Novus International, Inc. | Methods and compositions for the control of coccidiosis |
| US6969602B1 (en) * | 2001-04-20 | 2005-11-29 | The United States Of America As Represented By The Secretary Of The Agriculture | Production of an immunovariant strain of Eimeria maxima contributes to strain cross-protection with other Eimeria maximas |
| WO2003020917A1 (en) * | 2001-08-30 | 2003-03-13 | Embrex, Inc. | Improved methods for producing oocysts |
| TWI348376B (en) | 2002-02-26 | 2011-09-11 | Wyeth Corp | Selection of poultry eimeria strains through extra-intestinal sporozites |
| US7250286B2 (en) * | 2002-05-21 | 2007-07-31 | Schering-Plough Corporation | Methods for the in vitro culture of Sporozoea sp. and uses thereof |
| BR0313994A (pt) | 2002-09-20 | 2005-07-19 | Akzo Nobel Nv | Parasita vivo atenuado, vacina para combater infecção parasìtica, uso de um parasita vivo atenuado, método para a produção de uma vacina, e, fragmento de dna |
| ATE483471T1 (de) * | 2002-12-09 | 2010-10-15 | Univ Georgia | Kokzidioseimpfstoff sowie verfahren zu seiner herstellung und verwendung |
| US7354593B2 (en) | 2002-12-09 | 2008-04-08 | Merial Limited | Coccidial vaccine and methods of making and using same |
| DK1742656T3 (da) | 2004-03-12 | 2010-07-19 | Univ Georgia | Hidtil ukendt jordnøddeskindekstrakt som adjuvansvaccine |
| CA2464522C (en) * | 2004-04-15 | 2011-11-15 | Eng-Hong Lee | Soft gel delivery system for treating poultry |
| US20080131463A1 (en) * | 2006-11-30 | 2008-06-05 | Perdue Holdings, Inc. | Vaccination method for controlling coccidiosis in fowl |
| CA2725361C (en) | 2008-05-29 | 2017-05-16 | Intervet International B.V. | Coccidiosis vaccines |
-
2009
- 2009-11-11 EP EP20090752084 patent/EP2355844A2/en not_active Withdrawn
- 2009-11-11 CA CA2743262A patent/CA2743262C/en active Active
- 2009-11-11 BR BRPI0921843-2A patent/BRPI0921843B1/pt active IP Right Grant
- 2009-11-11 MX MX2011005133A patent/MX2011005133A/es active IP Right Grant
- 2009-11-11 US US12/616,341 patent/US8252292B2/en active Active
- 2009-11-11 AU AU2009314192A patent/AU2009314192A1/en not_active Abandoned
- 2009-11-11 WO PCT/US2009/063977 patent/WO2010056709A2/en not_active Ceased
-
2011
- 2011-05-13 CL CL2011001097A patent/CL2011001097A1/es unknown
Also Published As
| Publication number | Publication date |
|---|---|
| WO2010056709A2 (en) | 2010-05-20 |
| AU2009314192A1 (en) | 2010-05-20 |
| CA2743262A1 (en) | 2010-05-20 |
| MX2011005133A (es) | 2011-08-04 |
| EP2355844A2 (en) | 2011-08-17 |
| US20100166803A1 (en) | 2010-07-01 |
| CL2011001097A1 (es) | 2012-07-20 |
| CA2743262C (en) | 2021-11-02 |
| AU2009314192A2 (en) | 2011-06-23 |
| BRPI0921843A2 (pt) | 2018-10-09 |
| WO2010056709A3 (en) | 2010-07-01 |
| US8252292B2 (en) | 2012-08-28 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| ES2351299T3 (es) | Procedimientos mejorados para la producción de ooquistes. | |
| BRPI0921843B1 (pt) | composição de vacina, e, uso de uma composição de vacina | |
| Sinski et al. | Biological characterisation of Cryptosporidium parvum isolates of wildliferodents in Poland. | |
| EP2912198B1 (en) | Immunogenic composition against aeromonas hydrophila | |
| JP2546581B2 (ja) | エイメリアネカトリクスdnaプローブ | |
| JP2546577B2 (ja) | エイメリア・ブルネッティdnaプローブ | |
| CN116121224B (zh) | 弓形虫gra5基因敲除虫株的构建方法及其应用 | |
| EP1963482B1 (en) | Avirulent isolate of neospora caninum and its uses | |
| CN112899167A (zh) | 一种模拟田间快速诱导抗球虫药耐药株的方法及其分离鉴定方法 | |
| JP2546578B2 (ja) | エイメリア・マキシマdnaプローブ | |
| KR101827767B1 (ko) | 닭 전염성 후두기관염 바이러스 약독화주 및 이를 포함하는 백신 조성물 | |
| Gong et al. | Biological characteristics of a precocious line of Eimeria tenella | |
| Argamjav et al. | New coccidian Eimeria iyoensis n. sp.(Apicomplexa: Eucoccidiorida: Eimeriidae) in farmed ring-necked pheasants (Phasianus colchicus L.) in Ehime, Japan | |
| JP2546580B2 (ja) | エイメリアミチスdnaプローブ | |
| JP2568789B2 (ja) | エイメリア・アセルブリナdnaプローブ | |
| Balogun et al. | Management of canine parvoviral enteritis: a case report of a 3-month-old Nigerian indigenous puppy in a resource-limited setting. | |
| Kang et al. | Pathogenicity, immunogenicity, and cross-protective efficacy of representative Eimeria brunetti strains in Chinese yellow-feathered broilers: an in vivo evaluation | |
| JP2546579B2 (ja) | エイメリアテネラdnaプローブ | |
| CN121271807A (zh) | 稳定突变的犬细小病毒弱毒株及其应用 | |
| Oliveira et al. | Experimental Neospora caninum infection in chickens (Gallus gallus | |
| Guttormsdóttir | Tail and fin rot bacteria in Icelandic aquaculture. Diversity and genetic analysis | |
| JP2546582B2 (ja) | エイメリア・プラエコックスdnaプローブ | |
| CA3158539A1 (en) | Inactivated piscine orthoreovirus vaccine | |
| CN111187722A (zh) | grx S16和grx C5基因双缺失的新孢子虫弱毒虫株及其构建方法和应用 | |
| JPH06225796A (ja) | エイメリア種の感染力を確認するための種・特異的方法 |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| B07D | Technical examination (opinion) related to article 229 of industrial property law [chapter 7.4 patent gazette] |
Free format text: DE ACORDO COM O ARTIGO 229-C DA LEI NO 10196/2001, QUE MODIFICOU A LEI NO 9279/96, A CONCESSAO DA PATENTE ESTA CONDICIONADA A ANUENCIA PREVIA DA ANVISA. CONSIDERANDO A APROVACAO DOS TERMOS DO PARECER NO 337/PGF/EA/2010, BEM COMO A PORTARIA INTERMINISTERIAL NO 1065 DE 24/05/2012, ENCAMINHA-SE O PRESENTE PEDIDO PARA AS PROVIDENCIAS CABIVEIS. |
|
| B06F | Objections, documents and/or translations needed after an examination request according [chapter 6.6 patent gazette] | ||
| B07G | Grant request does not fulfill article 229-c lpi (prior consent of anvisa) [chapter 7.7 patent gazette] | ||
| B06U | Preliminary requirement: requests with searches performed by other patent offices: procedure suspended [chapter 6.21 patent gazette] | ||
| B09A | Decision: intention to grant [chapter 9.1 patent gazette] | ||
| B16A | Patent or certificate of addition of invention granted [chapter 16.1 patent gazette] |
Free format text: PRAZO DE VALIDADE: 10 (DEZ) ANOS CONTADOS A PARTIR DE 24/11/2020, OBSERVADAS AS CONDICOES LEGAIS. |