ES2786507T3 - Plantas de melón con resistencia al virus asociado al amarilleamiento del melón (MYaV) - Google Patents
Plantas de melón con resistencia al virus asociado al amarilleamiento del melón (MYaV) Download PDFInfo
- Publication number
- ES2786507T3 ES2786507T3 ES13803041T ES13803041T ES2786507T3 ES 2786507 T3 ES2786507 T3 ES 2786507T3 ES 13803041 T ES13803041 T ES 13803041T ES 13803041 T ES13803041 T ES 13803041T ES 2786507 T3 ES2786507 T3 ES 2786507T3
- Authority
- ES
- Spain
- Prior art keywords
- myav
- melon
- plant
- resistance
- seq
- Prior art date
- Legal status (The legal status is an assumption and is not a legal conclusion. Google has not performed a legal analysis and makes no representation as to the accuracy of the status listed.)
- Active
Links
- 235000015510 Cucumis melo subsp melo Nutrition 0.000 title description 105
- FJJCIZWZNKZHII-UHFFFAOYSA-N [4,6-bis(cyanoamino)-1,3,5-triazin-2-yl]cyanamide Chemical compound N#CNC1=NC(NC#N)=NC(NC#N)=N1 FJJCIZWZNKZHII-UHFFFAOYSA-N 0.000 title description 91
- 241000700605 Viruses Species 0.000 title description 17
- 238000004383 yellowing Methods 0.000 title description 12
- 241000219112 Cucumis Species 0.000 title 2
- 241000196324 Embryophyta Species 0.000 claims abstract description 255
- 210000000349 chromosome Anatomy 0.000 claims abstract description 182
- 239000012634 fragment Substances 0.000 claims abstract description 132
- 239000003550 marker Substances 0.000 claims abstract description 95
- 108700028369 Alleles Proteins 0.000 claims abstract description 75
- 238000000034 method Methods 0.000 claims abstract description 57
- 125000003729 nucleotide group Chemical group 0.000 claims abstract description 54
- 239000002773 nucleotide Substances 0.000 claims abstract description 53
- 238000003556 assay Methods 0.000 claims abstract description 44
- 239000003147 molecular marker Substances 0.000 claims abstract description 25
- 239000003795 chemical substances by application Substances 0.000 claims abstract description 18
- 238000012216 screening Methods 0.000 claims abstract description 8
- 235000009831 Citrullus lanatus Nutrition 0.000 claims description 63
- 244000022291 Cucumis melo subsp agrestis Species 0.000 claims description 8
- 244000241257 Cucumis melo Species 0.000 claims description 6
- FWMNVWWHGCHHJJ-SKKKGAJSSA-N 4-amino-1-[(2r)-6-amino-2-[[(2r)-2-[[(2r)-2-[[(2r)-2-amino-3-phenylpropanoyl]amino]-3-phenylpropanoyl]amino]-4-methylpentanoyl]amino]hexanoyl]piperidine-4-carboxylic acid Chemical compound C([C@H](C(=O)N[C@H](CC(C)C)C(=O)N[C@H](CCCCN)C(=O)N1CCC(N)(CC1)C(O)=O)NC(=O)[C@H](N)CC=1C=CC=CC=1)C1=CC=CC=C1 FWMNVWWHGCHHJJ-SKKKGAJSSA-N 0.000 claims description 4
- 244000064895 Cucumis melo subsp melo Species 0.000 abstract description 308
- 241001608711 Melo Species 0.000 abstract description 5
- 241001376324 Melon yellowing-associated virus Species 0.000 description 260
- 244000241235 Citrullus lanatus Species 0.000 description 66
- 210000004027 cell Anatomy 0.000 description 47
- 108090000623 proteins and genes Proteins 0.000 description 28
- 201000010099 disease Diseases 0.000 description 22
- 208000037265 diseases, disorders, signs and symptoms Diseases 0.000 description 22
- 235000013399 edible fruits Nutrition 0.000 description 22
- 230000002068 genetic effect Effects 0.000 description 22
- 210000001519 tissue Anatomy 0.000 description 18
- 238000012360 testing method Methods 0.000 description 15
- 235000009847 Cucumis melo var cantalupensis Nutrition 0.000 description 14
- 208000024891 symptom Diseases 0.000 description 13
- 235000009842 Cucumis melo Nutrition 0.000 description 12
- 238000013507 mapping Methods 0.000 description 11
- 230000009261 transgenic effect Effects 0.000 description 11
- 230000006872 improvement Effects 0.000 description 10
- 150000007523 nucleic acids Chemical group 0.000 description 10
- 241000499507 Cucurbit yellow stunting disorder virus Species 0.000 description 9
- 238000003205 genotyping method Methods 0.000 description 9
- RWQNBRDOKXIBIV-UHFFFAOYSA-N thymine Chemical compound CC1=CNC(=O)NC1=O RWQNBRDOKXIBIV-UHFFFAOYSA-N 0.000 description 9
- 244000024469 Cucumis prophetarum Species 0.000 description 8
- 238000009395 breeding Methods 0.000 description 8
- 230000001488 breeding effect Effects 0.000 description 8
- 238000004519 manufacturing process Methods 0.000 description 8
- 108020004707 nucleic acids Proteins 0.000 description 8
- 102000039446 nucleic acids Human genes 0.000 description 8
- 108020004414 DNA Proteins 0.000 description 7
- 239000000463 material Substances 0.000 description 7
- 108091028043 Nucleic acid sequence Proteins 0.000 description 6
- GFFGJBXGBJISGV-UHFFFAOYSA-N adenyl group Chemical group N1=CN=C2N=CNC2=C1N GFFGJBXGBJISGV-UHFFFAOYSA-N 0.000 description 6
- 238000004113 cell culture Methods 0.000 description 6
- 101710132601 Capsid protein Proteins 0.000 description 5
- 101710094648 Coat protein Proteins 0.000 description 5
- 241000948317 Cowpea mild mottle virus Species 0.000 description 5
- 102100021181 Golgi phosphoprotein 3 Human genes 0.000 description 5
- 101710125418 Major capsid protein Proteins 0.000 description 5
- 101710141454 Nucleoprotein Proteins 0.000 description 5
- 241000422193 Ormyrus Species 0.000 description 5
- 101710083689 Probable capsid protein Proteins 0.000 description 5
- 238000011161 development Methods 0.000 description 5
- 230000018109 developmental process Effects 0.000 description 5
- UYTPUPDQBNUYGX-UHFFFAOYSA-N guanine Chemical class O=C1NC(N)=NC2=C1N=CN2 UYTPUPDQBNUYGX-UHFFFAOYSA-N 0.000 description 5
- 230000008569 process Effects 0.000 description 5
- 230000006798 recombination Effects 0.000 description 5
- 238000005215 recombination Methods 0.000 description 5
- 241000894007 species Species 0.000 description 5
- 235000015001 Cucumis melo var inodorus Nutrition 0.000 description 4
- 240000002495 Cucumis melo var. inodorus Species 0.000 description 4
- 235000010071 Cucumis prophetarum Nutrition 0.000 description 4
- 241000879842 Fusarium oxysporum f. sp. melonis Species 0.000 description 4
- 230000009418 agronomic effect Effects 0.000 description 4
- OPTASPLRGRRNAP-UHFFFAOYSA-N cytosine Chemical compound NC=1C=CNC(=O)N=1 OPTASPLRGRRNAP-UHFFFAOYSA-N 0.000 description 4
- 238000001514 detection method Methods 0.000 description 4
- 235000013305 food Nutrition 0.000 description 4
- 210000001161 mammalian embryo Anatomy 0.000 description 4
- 210000000056 organ Anatomy 0.000 description 4
- 230000001850 reproductive effect Effects 0.000 description 4
- 238000012546 transfer Methods 0.000 description 4
- 230000009466 transformation Effects 0.000 description 4
- 229930024421 Adenine Natural products 0.000 description 3
- 241000269350 Anura Species 0.000 description 3
- 241000710175 Carlavirus Species 0.000 description 3
- 241000258937 Hemiptera Species 0.000 description 3
- 108700026244 Open Reading Frames Proteins 0.000 description 3
- 108020004511 Recombinant DNA Proteins 0.000 description 3
- 108700019146 Transgenes Proteins 0.000 description 3
- 101000872823 Xenopus laevis Probable histone deacetylase 1-A Proteins 0.000 description 3
- 229960000643 adenine Drugs 0.000 description 3
- 238000004458 analytical method Methods 0.000 description 3
- 230000001580 bacterial effect Effects 0.000 description 3
- 238000011156 evaluation Methods 0.000 description 3
- 238000000338 in vitro Methods 0.000 description 3
- 108020004999 messenger RNA Proteins 0.000 description 3
- 210000001938 protoplast Anatomy 0.000 description 3
- 229940113082 thymine Drugs 0.000 description 3
- 238000012795 verification Methods 0.000 description 3
- 101000645498 Alkalihalobacillus pseudofirmus (strain ATCC BAA-2126 / JCM 17055 / OF4) Uncharacterized protein BpOF4_10220 Proteins 0.000 description 2
- 241000894006 Bacteria Species 0.000 description 2
- 241001302798 Bemisia argentifolii Species 0.000 description 2
- 235000011274 Benincasa cerifera Nutrition 0.000 description 2
- 235000005976 Citrus sinensis Nutrition 0.000 description 2
- 240000002319 Citrus sinensis Species 0.000 description 2
- 101001132313 Clostridium pasteurianum 34.2 kDa protein in rubredoxin operon Proteins 0.000 description 2
- 240000001251 Cucumis anguria Species 0.000 description 2
- 241000056715 Cucumis picrocarpus Species 0.000 description 2
- 240000008067 Cucumis sativus Species 0.000 description 2
- 235000010799 Cucumis sativus var sativus Nutrition 0.000 description 2
- 102000053602 DNA Human genes 0.000 description 2
- 208000035240 Disease Resistance Diseases 0.000 description 2
- 101000618325 Enterobacteria phage T4 Uncharacterized 12.4 kDa protein in mobB-Gp55 intergenic region Proteins 0.000 description 2
- 101000653284 Enterobacteria phage T4 Uncharacterized 9.4 kDa protein in Gp31-cd intergenic region Proteins 0.000 description 2
- 101000758676 Pyrococcus woesei Uncharacterized 24.7 kDa protein in gap 5'region Proteins 0.000 description 2
- 244000087991 Silene chilense Species 0.000 description 2
- 206010040925 Skin striae Diseases 0.000 description 2
- 241000607479 Yersinia pestis Species 0.000 description 2
- 210000004436 artificial bacterial chromosome Anatomy 0.000 description 2
- 230000010165 autogamy Effects 0.000 description 2
- 230000002759 chromosomal effect Effects 0.000 description 2
- 235000009508 confectionery Nutrition 0.000 description 2
- 229940104302 cytosine Drugs 0.000 description 2
- 238000007405 data analysis Methods 0.000 description 2
- 238000001493 electron microscopy Methods 0.000 description 2
- 210000002257 embryonic structure Anatomy 0.000 description 2
- 230000007613 environmental effect Effects 0.000 description 2
- 239000000284 extract Substances 0.000 description 2
- 238000002509 fluorescent in situ hybridization Methods 0.000 description 2
- 230000021121 meiosis Effects 0.000 description 2
- 238000010369 molecular cloning Methods 0.000 description 2
- 102000044158 nucleic acid binding protein Human genes 0.000 description 2
- 108700020942 nucleic acid binding protein Proteins 0.000 description 2
- 239000002245 particle Substances 0.000 description 2
- 230000007170 pathology Effects 0.000 description 2
- 210000002706 plastid Anatomy 0.000 description 2
- 230000000644 propagated effect Effects 0.000 description 2
- 102000004169 proteins and genes Human genes 0.000 description 2
- 230000000405 serological effect Effects 0.000 description 2
- 239000007787 solid Substances 0.000 description 2
- UHPMCKVQTMMPCG-UHFFFAOYSA-N 5,8-dihydroxy-2-methoxy-6-methyl-7-(2-oxopropyl)naphthalene-1,4-dione Chemical compound CC1=C(CC(C)=O)C(O)=C2C(=O)C(OC)=CC(=O)C2=C1O UHPMCKVQTMMPCG-UHFFFAOYSA-N 0.000 description 1
- 241000300595 Acalymma trivittatum Species 0.000 description 1
- 241000238876 Acari Species 0.000 description 1
- 241000254032 Acrididae Species 0.000 description 1
- 241000589158 Agrobacterium Species 0.000 description 1
- 101000758020 Alkalihalobacillus pseudofirmus (strain ATCC BAA-2126 / JCM 17055 / OF4) Uncharacterized aminotransferase BpOF4_10225 Proteins 0.000 description 1
- 241000961634 Alphaflexiviridae Species 0.000 description 1
- 241001124076 Aphididae Species 0.000 description 1
- 235000000832 Ayote Nutrition 0.000 description 1
- FGUUSXIOTUKUDN-IBGZPJMESA-N C1(=CC=CC=C1)N1C2=C(NC([C@H](C1)NC=1OC(=NN=1)C1=CC=CC=C1)=O)C=CC=C2 Chemical compound C1(=CC=CC=C1)N1C2=C(NC([C@H](C1)NC=1OC(=NN=1)C1=CC=CC=C1)=O)C=CC=C2 FGUUSXIOTUKUDN-IBGZPJMESA-N 0.000 description 1
- 235000012828 Citrullus lanatus var citroides Nutrition 0.000 description 1
- 101000744710 Clostridium pasteurianum Uncharacterized glutaredoxin-like 8.6 kDa protein in rubredoxin operon Proteins 0.000 description 1
- 241001505951 Coconut cadang-cadang viroid Species 0.000 description 1
- 240000003370 Cucumis africanus Species 0.000 description 1
- 235000009075 Cucumis anguria Nutrition 0.000 description 1
- 241000890154 Cucumis ficifolius Species 0.000 description 1
- 241000911418 Cucumis hystrix Species 0.000 description 1
- 241001609709 Cucumis meeusei Species 0.000 description 1
- 235000010084 Cucumis melo subsp agrestis Nutrition 0.000 description 1
- 244000241200 Cucumis melo var. cantalupensis Species 0.000 description 1
- 244000243496 Cucumis melo var. texanus Species 0.000 description 1
- 241000882804 Cucumis metulifer Species 0.000 description 1
- 241000056262 Cucumis queenslandicus Species 0.000 description 1
- 241000882811 Cucumis zeyherii Species 0.000 description 1
- 240000004244 Cucurbita moschata Species 0.000 description 1
- 235000009854 Cucurbita moschata Nutrition 0.000 description 1
- 235000009804 Cucurbita pepo subsp pepo Nutrition 0.000 description 1
- 235000000784 Cyclanthera pedata Nutrition 0.000 description 1
- 238000001712 DNA sequencing Methods 0.000 description 1
- 241001529600 Diabrotica balteata Species 0.000 description 1
- 241000489973 Diabrotica undecimpunctata Species 0.000 description 1
- 241001000394 Diaphania hyalinata Species 0.000 description 1
- 206010013883 Dwarfism Diseases 0.000 description 1
- 101000653283 Enterobacteria phage T4 Uncharacterized 11.5 kDa protein in Gp31-cd intergenic region Proteins 0.000 description 1
- 101000618324 Enterobacteria phage T4 Uncharacterized 7.9 kDa protein in mobB-Gp55 intergenic region Proteins 0.000 description 1
- 241000221785 Erysiphales Species 0.000 description 1
- 241000233866 Fungi Species 0.000 description 1
- 241000223218 Fusarium Species 0.000 description 1
- 101000947178 Homo sapiens Platelet basic protein Proteins 0.000 description 1
- 206010020649 Hyperkeratosis Diseases 0.000 description 1
- 241000227653 Lycopersicon Species 0.000 description 1
- 235000007688 Lycopersicon esculentum Nutrition 0.000 description 1
- 241001465754 Metazoa Species 0.000 description 1
- 241000244206 Nematoda Species 0.000 description 1
- 241000233679 Peronosporaceae Species 0.000 description 1
- 102100036154 Platelet basic protein Human genes 0.000 description 1
- 241000353135 Psenopsis anomala Species 0.000 description 1
- 101000961876 Pyrococcus woesei Uncharacterized protein in gap 3'region Proteins 0.000 description 1
- 101001056915 Saccharopolyspora erythraea 6-deoxyerythronolide-B synthase EryA2, modules 3 and 4 Proteins 0.000 description 1
- 101000819248 Staphylococcus aureus Uncharacterized protein in ileS 5'region Proteins 0.000 description 1
- 235000001231 Streptopus amplexifolius Nutrition 0.000 description 1
- NINIDFKCEFEMDL-UHFFFAOYSA-N Sulfur Chemical compound [S] NINIDFKCEFEMDL-UHFFFAOYSA-N 0.000 description 1
- 208000005652 acute fatty liver of pregnancy Diseases 0.000 description 1
- 238000007844 allele-specific PCR Methods 0.000 description 1
- 125000003275 alpha amino acid group Chemical group 0.000 description 1
- 230000004888 barrier function Effects 0.000 description 1
- 239000012620 biological material Substances 0.000 description 1
- 230000033228 biological regulation Effects 0.000 description 1
- 230000005540 biological transmission Effects 0.000 description 1
- 230000008859 change Effects 0.000 description 1
- 238000009402 cross-breeding Methods 0.000 description 1
- 238000005520 cutting process Methods 0.000 description 1
- 230000001419 dependent effect Effects 0.000 description 1
- 238000013461 design Methods 0.000 description 1
- 210000001840 diploid cell Anatomy 0.000 description 1
- 230000004927 fusion Effects 0.000 description 1
- 238000012239 gene modification Methods 0.000 description 1
- 230000005017 genetic modification Effects 0.000 description 1
- 230000001295 genetical effect Effects 0.000 description 1
- 235000013617 genetically modified food Nutrition 0.000 description 1
- 230000035784 germination Effects 0.000 description 1
- PCHJSUWPFVWCPO-UHFFFAOYSA-N gold Chemical compound [Au] PCHJSUWPFVWCPO-UHFFFAOYSA-N 0.000 description 1
- 239000010931 gold Substances 0.000 description 1
- 229910052737 gold Inorganic materials 0.000 description 1
- 230000012010 growth Effects 0.000 description 1
- 238000003306 harvesting Methods 0.000 description 1
- 238000003384 imaging method Methods 0.000 description 1
- 238000012606 in vitro cell culture Methods 0.000 description 1
- 210000003000 inclusion body Anatomy 0.000 description 1
- 208000015181 infectious disease Diseases 0.000 description 1
- JEIPFZHSYJVQDO-UHFFFAOYSA-N iron(III) oxide Inorganic materials O=[Fe]O[Fe]=O JEIPFZHSYJVQDO-UHFFFAOYSA-N 0.000 description 1
- 230000014759 maintenance of location Effects 0.000 description 1
- 230000001404 mediated effect Effects 0.000 description 1
- 230000000442 meristematic effect Effects 0.000 description 1
- 244000005700 microbiome Species 0.000 description 1
- 238000009448 modified atmosphere packaging Methods 0.000 description 1
- 230000000869 mutational effect Effects 0.000 description 1
- 239000004745 nonwoven fabric Substances 0.000 description 1
- 208000030212 nutrition disease Diseases 0.000 description 1
- 208000019180 nutritional disease Diseases 0.000 description 1
- 210000001672 ovary Anatomy 0.000 description 1
- 230000001717 pathogenic effect Effects 0.000 description 1
- 238000012247 phenotypical assay Methods 0.000 description 1
- 238000003976 plant breeding Methods 0.000 description 1
- 238000012545 processing Methods 0.000 description 1
- 235000015136 pumpkin Nutrition 0.000 description 1
- 230000008929 regeneration Effects 0.000 description 1
- 238000011069 regeneration method Methods 0.000 description 1
- 230000001105 regulatory effect Effects 0.000 description 1
- 230000003362 replicative effect Effects 0.000 description 1
- 238000007894 restriction fragment length polymorphism technique Methods 0.000 description 1
- 230000010153 self-pollination Effects 0.000 description 1
- 238000000528 statistical test Methods 0.000 description 1
- 238000003860 storage Methods 0.000 description 1
- 229910052717 sulfur Inorganic materials 0.000 description 1
- 239000011593 sulfur Substances 0.000 description 1
- 235000019605 sweet taste sensations Nutrition 0.000 description 1
- 238000010998 test method Methods 0.000 description 1
- 238000011144 upstream manufacturing Methods 0.000 description 1
- 230000009417 vegetative reproduction Effects 0.000 description 1
- 238000013466 vegetative reproduction Methods 0.000 description 1
- 230000017260 vegetative to reproductive phase transition of meristem Effects 0.000 description 1
Classifications
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12N—MICROORGANISMS OR ENZYMES; COMPOSITIONS THEREOF; PROPAGATING, PRESERVING, OR MAINTAINING MICROORGANISMS; MUTATION OR GENETIC ENGINEERING; CULTURE MEDIA
- C12N15/00—Mutation or genetic engineering; DNA or RNA concerning genetic engineering, vectors, e.g. plasmids, or their isolation, preparation or purification; Use of hosts therefor
- C12N15/09—Recombinant DNA-technology
- C12N15/63—Introduction of foreign genetic material using vectors; Vectors; Use of hosts therefor; Regulation of expression
- C12N15/79—Vectors or expression systems specially adapted for eukaryotic hosts
- C12N15/82—Vectors or expression systems specially adapted for eukaryotic hosts for plant cells, e.g. plant artificial chromosomes (PACs)
- C12N15/8241—Phenotypically and genetically modified plants via recombinant DNA technology
- C12N15/8261—Phenotypically and genetically modified plants via recombinant DNA technology with agronomic (input) traits, e.g. crop yield
- C12N15/8271—Phenotypically and genetically modified plants via recombinant DNA technology with agronomic (input) traits, e.g. crop yield for stress resistance, e.g. heavy metal resistance
- C12N15/8279—Phenotypically and genetically modified plants via recombinant DNA technology with agronomic (input) traits, e.g. crop yield for stress resistance, e.g. heavy metal resistance for biotic stress resistance, pathogen resistance, disease resistance
- C12N15/8283—Phenotypically and genetically modified plants via recombinant DNA technology with agronomic (input) traits, e.g. crop yield for stress resistance, e.g. heavy metal resistance for biotic stress resistance, pathogen resistance, disease resistance for virus resistance
-
- A—HUMAN NECESSITIES
- A01—AGRICULTURE; FORESTRY; ANIMAL HUSBANDRY; HUNTING; TRAPPING; FISHING
- A01H—NEW PLANTS OR NON-TRANSGENIC PROCESSES FOR OBTAINING THEM; PLANT REPRODUCTION BY TISSUE CULTURE TECHNIQUES
- A01H5/00—Angiosperms, i.e. flowering plants, characterised by their plant parts; Angiosperms characterised otherwise than by their botanic taxonomy
- A01H5/08—Fruits
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q1/00—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions
- C12Q1/68—Measuring or testing processes involving enzymes, nucleic acids or microorganisms; Compositions therefor; Processes of preparing such compositions involving nucleic acids
- C12Q1/6876—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes
- C12Q1/6888—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for detection or identification of organisms
- C12Q1/6895—Nucleic acid products used in the analysis of nucleic acids, e.g. primers or probes for detection or identification of organisms for plants, fungi or algae
-
- C—CHEMISTRY; METALLURGY
- C12—BIOCHEMISTRY; BEER; SPIRITS; WINE; VINEGAR; MICROBIOLOGY; ENZYMOLOGY; MUTATION OR GENETIC ENGINEERING
- C12Q—MEASURING OR TESTING PROCESSES INVOLVING ENZYMES, NUCLEIC ACIDS OR MICROORGANISMS; COMPOSITIONS OR TEST PAPERS THEREFOR; PROCESSES OF PREPARING SUCH COMPOSITIONS; CONDITION-RESPONSIVE CONTROL IN MICROBIOLOGICAL OR ENZYMOLOGICAL PROCESSES
- C12Q2600/00—Oligonucleotides characterized by their use
- C12Q2600/156—Polymorphic or mutational markers
Landscapes
- Life Sciences & Earth Sciences (AREA)
- Health & Medical Sciences (AREA)
- Chemical & Material Sciences (AREA)
- Genetics & Genomics (AREA)
- Engineering & Computer Science (AREA)
- Organic Chemistry (AREA)
- Zoology (AREA)
- Biotechnology (AREA)
- Wood Science & Technology (AREA)
- Analytical Chemistry (AREA)
- Proteomics, Peptides & Aminoacids (AREA)
- General Engineering & Computer Science (AREA)
- Bioinformatics & Cheminformatics (AREA)
- Molecular Biology (AREA)
- Botany (AREA)
- General Health & Medical Sciences (AREA)
- Physics & Mathematics (AREA)
- Biochemistry (AREA)
- Microbiology (AREA)
- Biomedical Technology (AREA)
- Biophysics (AREA)
- Environmental Sciences (AREA)
- Developmental Biology & Embryology (AREA)
- Mycology (AREA)
- Physiology (AREA)
- Virology (AREA)
- Cell Biology (AREA)
- Immunology (AREA)
- Plant Pathology (AREA)
- Breeding Of Plants And Reproduction By Means Of Culturing (AREA)
- Measuring Or Testing Involving Enzymes Or Micro-Organisms (AREA)
- Micro-Organisms Or Cultivation Processes Thereof (AREA)
Abstract
Un procedimiento de identificación de una planta de C. melo cultivada que comprende un fragmento de introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV, que comprende: a) proporcionar una población de plantas de C. melo cultivada recombinantes (tal como una población F2, F3, BC1, BC2, BC1S1), b) cribar dicha población utilizando un ensayo de marcadores moleculares que detecta al menos un marcador de SNP seleccionado del grupo que consiste en: marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3; y c) identificar y/o seleccionar una planta que comprende al menos el genotipo CC o AC para el marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y el genotipo AA o AG para el marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3.
Description
DESCRIPCIÓN
Plantas de melón con resistencia al virus asociado al amarilleamiento del melón (MYaV)
Campo de la invención
La presente invención se refiere al campo de la mejora genética vegetal, en particular a la mejora genética de melones. Se desvela el locus genético que confiere resistencia al virus asociado al amarilleamiento del melón (MYaV, forma siglada del inglés: Melon Yellowing associated Virus) como se encuentra en accesiones de melón silvestre o en parientes silvestres del melón, y plantas de melón cultivadas que comprenden dicho locus genético (o una parte que confiere resistencia del mismo), que confiere a dichas plantas resistencia a MYaV. Además, se desvelan semillas a partir de las cuales tales plantas se pueden cultivar, partes de plantas, células, tejidos u órganos de tales plantas, y procedimientos de mejora genética para transferir el locus de resistencia a MYaV, o parte que confiere resistencia del mismo, a otras plantas o células vegetales de melón cultivado, especialmente a plantas de melón susceptibles al MYaV. Se proporcionan marcadores moleculares con los que dicho locus genético puede identificarse en plantas y células vegetales, y/o transferirse a otras plantas o células vegetales de melón. Como la resistencia a MYaV presente en el locus genético es dominante, las plantas y/o células vegetales resistentes al MYaV pueden comprender el locus genético en forma homocigótica o heterocigótica.
Antecedentes de la invención
Desde 1999, se informó que una nueva enfermedad que provoca síntomas descritos como "amarilleamiento de plantas de melón" provocaba daños en el noreste de Brasil, que es la región donde tiene lugar más del 90 % de la producción brasileña de melón. Los síntomas son el moteado y el amarilleamiento de las hojas y se observan principalmente en las hojas más antiguas (Nagata y col. 2003, Plant Pathology 52, 797). El virus que provocó esta enfermedad se denominó tentativamente virus asociado al amarilleamiento del melón (MYaV) (Nagata y col.,2003, citado anteriormente y Nagata y col., 2005, Arch. Virology Vol. 150(2):379-87). En 2007, la detección serológica (utilizando un anticuerpo policlonal desarrollado para la detección de MYaV, (véase Avila y col. 2008 Trop. Plant Pathol. v.33 n.3 Brasilia mayo/jun. de 2008) reveló que un gran porcentaje de plantas de melón sintomáticas estaban infectadas con MYaV (Lima y col. Hortic. Bras. vol. 27 n.° 4 Brasilia oct./dic. de 2009). La región más afectada fue el estado de Rio Grande do Norte, en Mossoro, con el 96,3 % de los melones infectados. De forma interesante, las concentraciones de virus fueron mayores en extractos preparados a partir de tallos de plantas sintomáticas que a partir de hojas.
Los síntomas típicos de la enfermedad aparecen como moteado y amarilleamiento en las hojas, principalmente de las hojas más antiguas, de forma similar a un trastorno nutricional (ver Nagata y col.,2003, citado anteriormente y la Fig. 1 de Nagata y col. 2010, Journal of General Plant Pathology Volumen 76, N.°4, página 268-272). En el tejido foliar infectado que muestra síntomas amarillentos, se pueden observar por microscopía electrónica partículas de virus filamentosas de 600-700 nm de longitud.
El virus que se encuentra en las plantas con los síntomas de amarilleamiento de la enfermedad se transmite de unas plantas de melón a otras mediante la mosca blanca (Bemisia tabaci biotipo B). Además, se puede utilizar el injerto para transmitir el virus a otras plantas de melón o a Cucumis anguria (pepino silvestre). Mediante microscopía electrónica, se observaron en hojas infectadas partículas filamentosas largas de tipo Carlavirus y cuerpos de inclusión, lo que sugirió la presencia de un virus del género Cartavirus (Nagata y col. 2003, Plant Pathol 52:797). Nagata y col.
2005 (citado anteriormente) secuenciaron dos genes, la proteína de la cubierta (ORF-A) y un marco de lectura abierto más (ORF-B), véase el número de referencia de GenBank AY373028. Como el virus del moteado leve del caupí (CPMMV, forma siglada del inglés Cowpea mild mottle virus) era la única especie de carlavirus conocida por ser transmitida por la mosca blanca, se esperaba que las propiedades genéticas y serológicas del MYaV fueran similares a las de CPMMV. Sin embargo, el MYaV no reaccionó de forma cruzada en un ensayo de inmunounión puntual con anticuerpos del CPMMV (Nagata y col. 2003, citado anteriormente), y los datos de secuencia genómica mostraron que la proteína de la cubierta (PC) del CPMMV no estaba estrechamente relacionada con la del MYaV (Nagata y col. 2005, citado anteriormente).
Inicialmente, no estaba claro si incluir al MYaV dentro del género Carlavirus o si debía ser un nuevo género en la familia Flexiviridae (Nagata y col. 2005, citado anteriormente). Sin embargo, en un estudio reciente (Nagata y col.
2010, citado anteriormente), se estima que se clonó y secuenció el 40 % (aproximadamente 3,1 kb) del genoma del MYaV y, basándose en estos datos, los autores sugieren que el virus es una especie nueva dentro del género Carlavirus y sugieren cambiar el nombre de este virus a virus del amarilleamiento del melón (MYV). La secuencia de 3,1 kb contenía 5 marcos de lectura abiertos (ORF), que codifican tres proteínas de bloque génico triple (Triple Gene Block) (TGB1, TGB2 y TGB3), la proteína de la cubierta (PC) y la supuesta proteína de unión a ácido nucleico (NABP, forma siglada de nucleic acid binding protein), véase el número de referencia de GenBank AB510477. La secuencia de la proteína de la cubierta (PC) en este estudio tenía una identidad de secuencia del 93 % con la secuencia de ORF-A (AY373028).
Como no hay disponibles plantas con resistencia contra el virus, una estrategia desarrollada para limitar la infección por MYaV es cubrir todo el campo con una capa de tela no tejida hilada desde la germinación hasta la floración, para prevenir la transmisión del virus por la mosca blanca. Sin embargo, las plantas se volvieron sensibles a los minadores
de hojas (Liriomisa spp.), lo que se convirtió en una producción de fruta muy dañada de forma generalizada (Nagata y col. 2010, citado anteriormente).
En el presente documento se desvelan fuentes de resistencia a MYaV y una región genética que comprende el locus de resistencia o una parte del mismo, que confieren resistencia frente al MYaV. Además, se desvelan plantas de melón cultivadas (Cucumis melo L.) y células, tejidos, frutas y otras partes de tales plantas que comprenden en su genoma un locus que confiere resistencia a MYaV (o una parte que confiere resistencia del mismo), ya sea en forma homocigótica o heterocigótica, mediante lo cual las plantas de melón son resistentes frente al MYaV. Además, se desvelan semillas a partir de las cuales se pueden cultivar plantas de melón resistentes al MYaV.
En un aspecto se proporcionan marcadores moleculares, que pueden utilizarse para detectar la presencia y/o transferir el locus que confiere resistencia a MYaV, o una parte que confiere resistencia del mismo, en/dentro de plantas o células vegetales de Cucumis melo L. Uno o más de los marcadores pueden, por tanto, utilizarse, por ejemplo, para transferir el locus de resistencia, o una parte que confiere resistencia del mismo, a plantas de melón que sean susceptibles al MYaV. En una divulgación, el locus de resistencia, o parte que confiere resistencia del mismo, es el locus en el cromosoma 6 que se encuentra en las semillas depositadas con el número de referencia NCIMB 41966 o NCIMB 41969. En una divulgación adicional en el presente documento, el locus de resistencia o parte que confiere resistencia del mismo es el locus en el cromosoma 6, o una parte que confiere resistencia del mismo, como se encuentra en otras plantas de melón silvestre o parientes silvestres del melón.
Se pueden utilizar también uno o más de los marcadores ligados, o asociados con, el locus de resistencia a MYaV, o parte que confiere resistencia del mismo, para identificar nuevas fuentes de resistencia a MYaV, tal como otras accesiones silvestres de Cucumis melo o parientes silvestres del melón que comprenden un locus de resistencia a MYaV en el cromosoma 6, y para transferir (introgresar) el locus de resistencia, o una parte que confiere resistencia a MYaV del mismo, de tales accesiones a plantas de melón cultivadas. La resistencia a MYaV que confiere el locus del rasgo cuantitativo (QTL, forma siglada de quantitative trait locus) en el cromosoma 6 (equivalente al grupo de ligamiento VI de la ICuGI (forma siglada de International Cucurbit Genomics Initiative: Iniciativa internacional de genómica de cucurbitáceas), o GL VI) fue nombrada MYaV6.1.
El documento EP1962578B1 describe un QTL de resistencia al CYSDV (forma siglada de cucurbit yellow stunting disorder virus: virus del amarilleo y enanismo de las cucurbitáceas) de PI313970 en un grupo de ligamiento, designado arbitrariamente como GL6, y reivindica plantas de melón que comprenden una introgresión de PI313970, cuya introgresión comprende un QTL de resistencia a CYSDV ligado a al menos un marcador ubicado en el cromosoma equivalente al grupo de ligamiento (GL) 6 de la accesión de melón PI313970. Debe tenerse en cuenta que en el documento EP1962578B1, el GL6 nombrado de manera arbitraria es el GL VI de la ICuGI de melón, pero corresponde al Grupo de Ligamiento V (GL V) de la ICuGI. En un aspecto, la planta desvelada en el presente documento, es decir, una planta de Cucumis melo cultivada que comprende una resistencia frente al virus asociado al amarilleamiento del melón (MYaV), en la que dicha resistencia es conferida por un fragmento de introgresión en el cromosoma 6 en forma homocigótica o heterocigótica, y en la que dicho fragmento de introgresión es de una planta silvestre de la especie Cucumis melo, no comprende el QTL de resistencia al CYSDV como se describe en el documento EP1962578B1. En otro aspecto, la planta desvelada en el presente documento, es decir, una planta de Cucumis melo cultivada que comprende una resistencia frente al virus asociado al amarilleamiento del melón (MYaV), en la que dicha resistencia es conferida por un fragmento de introgresión en el cromosoma 6 en forma homocigótica o heterocigótica, y en la que dicho fragmento de introgresión es de una planta silvestre de la especie Cucumis melo, no comprende los marcadores E11/M49-239, como se define en el párrafo [0037] del documento EP 1962578 B1. En otro aspecto más, la planta desvelada en el presente documento no comprende los marcadores E11/M54-156, E14/M54-152, E14/M51-210, E14/M51-083, E11/M49-239, E11/M54-169, E14/M50-262, E11/M57-278, E11/M54-163 y/o E11/M49-072 como se define en el párrafo [0040] del documento EP1962578 B1. En aún otro aspecto, la planta desvelada en el presente documento no comprende los marcadores E11/M54-156, E14/M54-152, E14/M51-210, E14/M51-083, E11/M49-239, E11/M64-169, E14/M60-262, E11/M67-278, E11/M64-163 y/o E11/M49-072 como se define en el párrafo [0013] del documento EP 1962578 B1. Los pasajes citados del documento EP1962578B1 se adjuntan en el presente documento como referencia. En otro aspecto más, las plantas desveladas en el presente documento, es decir, una planta de Cucumis melo cultivada que comprende una resistencia frente al virus asociado al amarilleamiento del melón (MYaV), en la que dicha resistencia es conferida por un fragmento de introgresión en el cromosoma 6 en forma homocigótica o heterocigótica, y en la que dicho fragmento de introgresión es de una planta silvestre de la especie Cucumis melo, no tienen un fenotipo de CYSDV (es decir, no son resistentes al CYSCV).
Definiciones generales
El artículo indefinido "a" o "una" no excluye la posibilidad de que esté presente más de uno de los elementos, a menos que el contexto precise claramente que haya uno y solo uno de los elementos. Por tanto, el artículo indefinido "un" o "una" habitualmente significa "al menos uno o una".
Como se usa en el presente documento, el término "planta" incluye la planta completa o cualquiera de sus partes o derivados de la misma, tales como órganos vegetales (por ejemplo, órganos de almacenamiento cosechados o no cosechados, tubérculos, frutos, hojas, semillas, etc.), células vegetales, protoplastos vegetales, cultivos de células o tejidos vegetales a partir de los que pueden regenerarse plantas, callos de plantas, agrupaciones de células vegetales,
y células vegetales que están intactas en plantas o partes de plantas, tales como los embriones, polen, óvulos, ovarios, frutos (por ejemplo, tejidos u órganos cosechados, tales como melones cosechados o partes de los mismos), flores, hojas, semillas, tubérculos, bulbos, plantas reproducidas de forma clonal, raíces, rizomas, tallos, puntas de raíces y similares. Además, se incluye cualquier fase del desarrollo, tal como las plántulas, inmadura y madura, etc. Cuando se hace referencia a "semillas de una planta", estas se refieren a semillas de las cuales se puede cultivar la planta o a semillas producidas en la planta, después de la autofecundación o la fecundación cruzada.
"Variedad vegetal" es un grupo de plantas dentro del mismo taxón botánico del grado más bajo conocido, que (independientemente de si se cumplen o no las condiciones para el reconocimiento de los derechos del obtentor de plantas) puede definirse en función de la expresión de características que son el resultado de un determinado genotipo o una combinación de genotipos, puede distinguirse de cualquier otro grupo de plantas por la expresión de al menos una de esas características, y puede considerarse como una entidad, debido a que se pueden multiplicar sin ningún cambio. Por lo tanto, la expresión "variedad vegetal" no puede utilizarse para indicar un grupo de plantas, incluso si son del mismo tipo, si todas se caracterizan por la presencia de uno o dos locus o genes (o características fenotípicas debidas a estos locus o genes específicos), pero que de lo contrario pueden diferir enormemente entre sí en lo que respecta a los otros locus o genes.
"F1, F2, F3, etc." se refiere a las generaciones relacionadas consecutivas después de un cruce entre dos plantas parentales o líneas parentales. Las plantas cultivadas a partir de las semillas producidas al cruzar dos plantas o líneas se llama generación F1. La autofecundación de las plantas F1 da como resultado la generación F2, etc.
La planta "híbrida F1" (o semilla híbrida F1) es la generación obtenida al cruzar dos líneas parentales endogámicas. Por tanto, las semillas híbridas F1 son semillas a partir de las cuales crecen las plantas híbridas F1. Los híbridos F1 son más vigorosos y de mayor rendimiento, debido a la heterosis.
El término "alelo (o alelos)" significa cualquiera de una o más formas alternativas de un gen en un locus particular, alelos que se relacionan todos con un rasgo o característica en un locus específico. En una célula diploide de un organismo, los alelos de un gen dado se emplazan en una ubicación específica, o locus (plural, locus) en un cromosoma. En cada cromosoma del par de cromosomas homólogos está presente un alelo. Una especie de planta diploide puede comprender una gran cantidad de alelos distintos en un locus particular. Estos pueden ser alelos idénticos del gen (homocigótico) o dos alelos distintos (heterocigótico). Por tanto, por ejemplo, en el presente documento se puede hacer referencia a un alelo de MYaV del locus de resistencia a MYaV MYaV6.1.
El término "gen" significa una secuencia de ADN (genómica) que comprende una región (región transcrita), que se transcribe en una molécula de ARN mensajero (ARNm) en una célula y una región reguladora unida operativamente (por ejemplo, un promotor). Los distintos alelos de un gen son, por tanto, distintas formas alternativas del gen, que pueden estar en forma de, por ejemplo, diferencias en uno o más nucleótidos de la secuencia de ADN genómico (por ejemplo, en la secuencia del promotor, las secuencias exónicas, la secuencias intrónicas, etc.), de la secuencia del ARNm y/o de aminoácidos de la proteína codificada.
El término "locus" (plural, locus) significa un lugar o lugares específicos o un sitio en un cromosoma donde, por ejemplo, se encuentra un gen o marcador genético. El locus de resistencia a MYaV (o locus que confiere resistencia MYaV) es, por tanto, la ubicación en el genoma del melón, donde se encuentra el gen de resistencia a MYaV. En el melón cultivado, el locus de resistencia a MYaV se encuentra en el cromosoma 6 (utilizando la nomenclatura de la ICuGI para cromosomas o grupos de ligamiento, es decir, el GLVI) y preferentemente introgresa en el genoma del melón cultivado (es decir, en el cromosoma 6 o GLVI) a partir de accesiones de melón silvestre, tales como (pero sin limitación) las dos accesiones de melón silvestre depositadas con los números de referencia NCIMB 41966 y NCIMB41969, o a partir de otros melones silvestres o parientes silvestres del melón que se pueden cruzar con C. melo y de cuyos cruces se puede producir una descendencia fértil.
Un "locus de rasgo cuantitativo" o "QTL" es un locus cromosómico que codifica uno o más alelos que afectan la expresividad de un fenotipo distribuido de forma continua (cuantitativo). La resistencia a MYaV que confiere el locus de rasgo cuantitativo se denomina en el presente documento MYaV6.1.
"ICuGI" (forma siglada del inglés International Cucurbit Genomics Initiative) se refiere a Iniciativa Internacional de los Genomas de las cucurbitáceas, que publica mapas genéticos de, por ejemplo, Cucumis melo (http://www.icugi.org/cgibin/cmap/map_set_info?species_acc=CM). La versión actual del mapa genómico de C. melo es del 4 de marzo de 2012 y el mapa del cromosoma 6 se denomina ICuGI_VI (o GL VI, o Grupo de Ligamiento VI), y contiene 124 marcadores (11 AFLP, 1 ISSR, 19 RAPD, 17 RFLP, 31 Sn P, 45 marcadores SSR) en un grupo de ligamiento que abarca de 0,00 a 98,00 cM. En el presente documento, cromosoma 6 de melón y GL VI se usan indistintamente.
La "distancia genética" entre locus (por ejemplo, entre marcadores moleculares y/o entre marcadores fenotípicos) en el mismo cromosoma se mide por la frecuencia de entrecruzamiento o frecuencia de recombinación (FR) y se indica en centimorgans (cM). Un cM corresponde a una frecuencia de recombinación del 1 %. Si no se pueden encontrar recombinantes, la FR es cero y los locus están extremadamente juntos físicamente o son idénticos. Cuanto más separados están dos locus, mayor es la FR.
La "distancia física" entre locus (por ejemplo, entre marcadores moleculares y/o entre marcadores fenotípicos) en el
mismo cromosoma es la distancia física real expresada en pares de bases (pb), kilo pares de bases (kb) o mega pares de bases (Mb). C. melo tiene un tamaño total del genoma haploide de aproximadamente 450 Mb, dividido en 12 pares de cromosomas, véase Garcia-Mas y col., PNAS 2 de julio de 2012, p1-6 y Gonzales y col. 2010, BMC Genomics 11:339, p1-13.
"Fragmento de introgresión" o "segmento de introgresión" o "región de introgresión" se refiere a un fragmento de cromosoma (o parte o región del cromosoma) que se ha introducido en otra planta de la misma especie o de una especie relacionada mediante técnicas de cruzamiento o técnicas tradicionales de mejora genética, tales como el retrocruzamiento, es decir, el fragmento introgresado es el resultado de procedimientos de mejora genética a los que se hace referencia mediante el verbo "introgresar" (tal como retrocruzamiento). En el melón, las accesiones de melón silvestre o parientes silvestres del melón se utilizan a menudo para introgresar fragmentos del genoma silvestre en el genoma del melón cultivado, Cucumis melo. Dicha planta de melón cultivada tiene, por tanto, un "genoma de C. melo" cultivado, pero comprende en el genoma un fragmento de un melón silvestre o de un pariente silvestre del melón, por ejemplo, un fragmento de introgresión de un genoma de Cucumis silvestre relacionado, tal como Cucumis melo ssp. agrestis, C. melo ssp. melo, C. melo ssp. acidulous, C. callosus, C. trigonus, C. picrocarpus, u otro melón silvestre o pariente silvestre del melón. Se entiende que la expresión "fragmento de introgresión" nunca incluye un cromosoma completo, sino solo una parte de un cromosoma. El fragmento de introgresión puede ser grande, por ejemplo, incluso la mitad de un cromosoma, pero preferentemente es más pequeño, tal como de aproximadamente 15 Mb o menos, tal como de aproximadamente 10 Mb o menos, de aproximadamente 9 Mb o menos, de aproximadamente 8 Mb o menos, de aproximadamente 7 Mb o menos, de aproximadamente 6 Mb o menos, de aproximadamente 5 Mb o menos, de aproximadamente 4 Mb o menos, de aproximadamente 3 Mb o menos, de aproximadamente 2 Mb o menos, de aproximadamente 1Mb (equivalente a 1.000.000 pares de bases) o menos, o de aproximadamente 0,5 Mb (equivalente a 500.000 pares de bases) o menos, tal como de aproximadamente 200.000 pb (equivalente a 200 kilo pares de bases) o menos, de aproximadamente 100.000 pb (100 kb) o menos, de aproximadamente 50.000 pb (50 kb) o menos, aproximadamente 25.000 pb (25 kb) o menos.
El "alelo de MYaV" se refiere a un alelo que confiere resistencia a MYaV que se encuentra en el locus que confiere resistencia a MYaV MYaV6.1, o en la parte del locus que confiere resistencia, introgresado en el melón cultivado (en el cromosoma 6 de C. melo cultivado), procedente de un melón silvestre o pariente silvestre del melón, por ejemplo, de plantas de las cuales se depositó una muestra representativa de semillas con el número de referencia NCIMB 41966 o NCIMB 41969. La expresión "alelo de MYaV", por tanto, también abarca los alelos de MYaV que se pueden obtener de otras accesiones de Cucumis resistentes a MYaV, tal como alelos ortólogos de MYaV (véase más abajo). Cuando están presentes uno o dos alelos de MYaV en el locus que confiere resistencia a MYaV en el genoma (es decir, en forma heterocigótica u homocigótica), la planta es resistente al MYaV, es decir, tiene un fenotipo de resistencia MYaV. En la planta de melón cultivada que carece del fragmento de introgresión, el alelo de C. melo encontrado en el mismo locus en el cromosoma 6 se denomina en el presente documento alelo "myav" alelo (o alelo susceptible a MYaV). Como la resistencia es dominante, las plantas myav/myav muestran un fenotipo susceptible al MYaV, mientras que las plantas MYaV/myav y las plantas MYaV/MYaV son plantas que poseen el fenotipo resistente al MYaV conferido por el alelo MYaV (es decir, son resistentes al MYaV).
"alelos ortólogos de MYaV u "ortólogos de MYaV', u "ortólogos para M YaV" son alelos de genes de resistencia a MYaV presentes en otros parientes silvestres del melón, en los cromosomas ortólogos 6. Dichos alelos ortólogos pueden, por tanto, encontrarse en el cromosoma 6 ortólogo de parientes silvestres de C. melo, tales como C. callosus, C. trigonus, C. picrocarpus y otros, y son transferibles, por introgresión, al cromosoma 6 de C. melo.
Un "fenotipo de resistencia MYaV" o "resistencia a MYaV", o "plantas resistentes al MYaV", se refiere a la resistencia frente al MYaV conferida por el alelo MYaV(o por el alelo ortólogo de MaYV) cuando está presente en el genoma de C. melo en dos copias (en forma homocigótica). El fenotipo de resistencia MYaV y la presencia del alelo M YaVy/u ortólogos de MYaV puede analizarse utilizando el "ensayo de resistencia MYaV" y/o ensayos de marcadores de MYaV.
Un "ensayo de resistencia a MYaV" puede llevarse a cabo de distintas maneras, ya sea por injerto o, preferentemente, como prueba de campo, como también se describe en otra parte en el presente documento. Preferentemente, se utiliza un ensayo de campo una zona de alta incidencia natural de Bemisia tabaci biotipo B, que porta el MYaV, tal como el noreste de Brasil u otras zonas donde hay una alta incidencia de enfermedad por el MYaV (es decir, un área infestada por MYaV). Una planta de un genotipo particular se considera resistente al MYaV si la puntuación promedio de resistencia a la enfermedad de una pluralidad de plantas (al menos 4, 5, 6, 7, 8, 9, 10 o más, preferentemente en al menos dos o tres repeticiones) de ese genotipo es significativamente mayor en comparación con los controles susceptibles (plantas que carecen de un fragmento de introgresión que comprende un alelo MYaV o un ortólogo de MYaV, tales como las variedades de melón Galia Amaregal F1 (Nunhems) o Glory (Origene Seeds); o las variedades de melón Piel de Sapo Medellín (Nunhems) o Sancho (Syngenta)), cuando se cultiva en el mismo entorno. Por tanto, por ejemplo, las plantas de melón de una línea que comprende la introgresión del locus que confiere resistencia a MYaV, o una parte que confiere resistencia del mismo, en forma heterocigótica u homocigota, se pueden cultivar junto con plantas de melón de control adecuadas (especialmente plantas de melón susceptibles a MYaV) en un campo abierto en el noreste de Brasil y, cuando todas las plantas de los controles susceptibles muestren síntomas claros de amarilleamiento (véase la Figura 2) todas las plantas se fenotipan en una escala de resistencia a la enfermedad de 1 (hojas totalmente amarillas, es decir, las hojas en el primer 1/3 de la planta son el 100% amarillas) a 9 (hojas totalmente verdes; las hojas en el primer 1/3 de la planta son el 100 % verdes), por lo que 2 = aproximadamente el
81 % al 99 % del área foliar en el primer 1/3 de la planta es amarilla, 3 = aproximadamente el 65 % al 80 % del área foliar en el primer 1/3 de la planta es amarilla, 4 = aproximadamente el 49 % al 64 % del área foliar en el primer 1/3 de la planta es amarilla, 5 = aproximadamente el 33 % al 48 % del área foliar en el primer 1/3 de la planta es amarilla, 6 = aproximadamente el 17 % al 32 % del área foliar en el primer 1/3 de la planta es amarilla, 7 = hasta aproximadamente el 17 % del área foliar en el primer 1/3 de la planta es amarilla, 8 = unas pocas hojas en el primer 1/3 de la planta comienzan a mostrar sombras/moteado amarillo. El primer 1/3 de la planta se refiere a las hojas más antiguas en la zona del primer 1/3 de la planta, determinada a partir del sistema principal del tallo/radicular de la planta y como se observa en la Figura 2 (rectángulo negro). Las hojas más jóvenes de las matas, más hacia la punta de las matas, no se fenotipan, dado que estas son generalmente verdes en el momento del fenotipado y se vuelven amarillas, solo en las plantas susceptibles, después de varios días más, por ejemplo, 7-10 días después (aunque ya contengan el virus en el momento del fenotipado). Las plantas con una puntuación promedio de resistencia a la enfermedad que es significativamente más alta que la puntuación promedio de la enfermedad de los controles susceptibles, por ejemplo, una puntuación promedio de al menos 3,0, preferentemente de al menos 4,0, más preferentemente de al menos 5,0, de al menos 6,0, de al menos 7,0, de al menos 8,0, muy preferentemente de 9,0, son en el presente documento plantas resistentes a MYaV o plantas que tienen una resistencia a MYaV.
El "ensayo de marcadores de MYaV" es un ensayo de marcadores moleculares que se puede utilizar para probar si en el cromosoma 6 de C. melo una introgresión de un melón silvestre, o pariente silvestre del melón que comprende el alelo de MYaV está presente en el genoma (o si en el melón silvestre o los parientes silvestres del melón comprenden la región que comprende QTL MYaV6.1 en su genoma), mediante la determinación del genotipo de los marcadores de SNP mME15090 y/o mME12135, y/o cualquier marcador específico del genoma de melón silvestre o pariente silvestre del melón entre los marcadores de SNP mMEmME15090 y mME12135, y opcionalmente también A) de uno o más marcadores seleccionados del grupo mME40332, mME28908, mME36531, mME9692, mME50656, o cualquier marcador específico del genoma de C. melo silvestre o pariente silvestre del melón entre mME1509 y mME50656, o B) de uno o más marcadores seleccionados del grupo mME21377, mME36533, mE13585, o cualquiera específico del genoma de C. melo silvestre o pariente silvestre del melón entre mME21377 y mME13585.
"Melón" o "melón almizcleño" se refiere en el presente documento a plantas de la especie Cucumis melo. Los melones o 'melones almizcleños', Cucumis melo, se pueden clasificar en: C. melo cantalupensis, C. melo inodorous y C. melo reticulatus. Los C. melo cantalupensis también se denominan cantalupos y son principalmente de forma redonda con estrías prominentes y casi sin reticulado. La mayoría tiene una pulpa naranja y dulce, y habitualmente son muy fragantes. En contraste con el melón europeo, el "cantalupo" norteamericano no es de este tipo, pero pertenecen a los melones almizcleños verdaderos. Los C. melo inodorous (o melones de invierno) se pueden subdividir en distintos tipos, tal como el melón Honeydew, Piel de sapo, melón Sugar, melón japonés, etc. C. melo reticulatus es el melón almizcleño verdadero, que tiene una piel reticulada (con forma de red) e incluye melones Galia, melones Sharlyn y el cantalupo norteamericano.
"Melón cultivado" se refiere a plantas de Cucumis melo, es decir, variedades, líneas reproductivas o cultivares de la especie C. melo, cultivados por los seres humanos y que tienen buenas características agronómicas, especialmente, producen frutos comestibles y comercializables de buen tamaño, calidad y uniformidad; preferentemente tales plantas no son "plantas silvestres", es decir, plantas que generalmente tienen rendimientos mucho peores y características agronómicas peores que las plantas cultivadas y, por ejemplo, crecen naturalmente en poblaciones silvestres. Las "plantas silvestres" incluyen, por ejemplo, ecotipos, líneas de PI (forma siglada de Plant Introduction: introducción vegetal), variedades autóctonas o accesiones silvestres o parientes silvestres de una especie.
El melón y los parientes silvestres del melón es/son diploides y tiene/tienen 12 pares de cromosomas homólogos, numerados del 1 al 12. "Cromosoma 6 de melón" se refiere al cromosoma 6 de C. melo, como se conoce en la técnica y como se denomina en la nomenclatura de la ICuGI. El "cromosoma 6 ortólogo" se refiere al cromosoma 6 de parientes silvestres del melón, partes de cual pueden introgresarse en el cromosoma 6 del melón cultivado.
"Melón silvestre" incluye plantas silvestres de la especie Cucumis melo, por ejemplo, C. melo ssp agrestis, C. melo ssp. melo, C. melo var. texanus, C. melo var. acidulous, semillas depositadas con el NCIMB 41966, el NCIMB 41969, y otras accesiones de C. melo silvestre, como, por ejemplo, variedades autóctonas o accesiones PI que se encuentran en http://www.ars-grin.gov u otras colecciones de semillas. Las semillas depositadas con el NCIMB 41966 se obtuvieron de la colección ARS-GRIN y tienen la denominación de origen 'India'. Las semillas depositadas con el NCIMB 41969 se obtuvieron de España y tienen como origen Uzbekistán.
Los "parientes silvestres del melón" incluyen plantas silvestres de otras especies de Cucumis, pero que se pueden cruzar con Cucumis melo para producir descendencia fértil (opcionalmente, con la ayuda de rescate de embriones, potenciación dependiente de temperatura del crecimiento del tubo polínico o técnicas similares para superar las barreras reproductivas) y de las cuales se pueden obtener fragmentos de cromosomas y transferirlos a Cucumis melo (ya sea por cruces interespecíficos con C. melo o a través de cruces con una especie que actúa de puente). Ejemplos de parientes silvestres del melón son C. anguria, C. metuliferus, Cucumis callosus, Cucumis trigonus, Cucumis ficifolius, C. picocarpus, C. zeyheri, C. africanus, C. meeusei, C. prophetarum, C. hystrix, C. queenslandicus, y otras especies de Cucumis (véase, por ejemplo, Sebastian y col. 2010, PNAS Vol. 107, n.° 32, 14269-14273).
"Promedio" se refiere en el presente documento a la media aritmética.
Un "cromosoma recombinante" se refiere a un cromosoma que tiene una nueva composición genética que surge a través del cruce entre cromosomas homólogos, por ejemplo, un "cromosoma 6 recombinante", es decir, un cromosoma 6 que no está presente en ninguna de las plantas parentales y que surgió a través de un raro evento de entrecruzamiento entre cromosomas homólogos de un par de cromosomas 6. En el presente documento, por ejemplo, se proporciona un cromosoma 6 recombinante de melón que comprende un locus que confiere resistencia a MYaV, o una parte que confiere resistencia del mismo (que comprende un alelo de resistencia MYaV).
La expresión "técnicas de mejora genética tradicionales" abarca en el presente documento el cruce, retrocruzamiento, autofecundación, selección, producción de haploides dobles, rescate de embriones, fusión de protoplastos, selección asistida por marcador, mejora genética por mutación, etc., tal como conoce el obtentor de plantas (es decir, procedimientos que no son procedimientos de modificación genética/transformación/transgénicos), mediante los cuales, por ejemplo, se puede obtener, identificar y/o transferir un cromosoma 6 recombinante.
"Retrocruzamiento" se refiere a un procedimiento de mejora genética mediante el cual un rasgo (único), tal como la resistencia a MYaV, puede transferirse desde un acervo genético inferior (por ejemplo, un melón silvestre o un pariente silvestre del melón; también denominado "donante") a un acervo genético superior (también denominado "parental recurrente"), por ejemplo, un melón cultivado. Una descendencia de un cruce (por ejemplo, una planta F1 obtenida cruzando un melón silvestre resistente a MYaV con un melón cultivado susceptible a MYaV; o una planta F2 o una planta F3, etc., obtenida de la autofecundación de F1) se "retrocruza" con el parental con el acervo genético superior, por ejemplo, con el parental cultivado, susceptible a MYaV. Después de repetidos retrocruces, el rasgo del acervo genético inferior se habrá incorporado al acervo genético superior.
La "selección asistida por marcadores" o "SAM" es un procedimiento de uso de la presencia de marcadores moleculares, que están genéticamente ligados a un locus particular o a una región cromosómica particular (por ejemplo, fragmento de introgresión), para seleccionar plantas por la presencia del locus o región específica (fragmento de introgresión). Por ejemplo, un marcador molecular genéticamente ligado a un locus de resistencia a MYaV, puede utilizarse para detectar y/o seleccionar plantas de melón que comprendan el locus de resistencia a MYaV. Cuanto más cerca esté el ligamiento genético del marcador molecular con el locus (por ejemplo, aproximadamente 7 cM, 6 cM, 5 cM, 4 cM, 3 cM, 2 cM, 1 cM, 0,5 cM o menos), menos probable es que el marcador se disocie del locus mediante recombinación meiótica.
La "puntuación LOD" (logaritmo (en base 10) de probabilidades) se refiere a una prueba estadística que se utiliza a menudo para el análisis de ligamiento en poblaciones animales y vegetales. La puntuación LOD compara la probabilidad de obtener los datos de la prueba si los dos locus (locus de marcadores moleculares y/o un locus de un rasgo fenotípico) están en efecto ligados, a la probabilidad de observar los mismos datos al azar. Las puntuaciones LOD positivas favorecen la presencia de un ligamiento y una puntuación LOD mayor a 3,0 se considera prueba de ligamiento. Una puntuación LOD de 3 indica una probabilidad de 1000 a 1 de que el ligamiento observado no se produjo al azar.
"Propagación vegetativa", "reproducción vegetativa" o "propagación clonal" se utilizan indistintamente en el presente documento y significan el procedimiento de tomar parte de una planta y permitir que esa parte de la planta forme al menos raíces, donde parte de la planta, por ejemplo, se define como o se obtiene de (por ejemplo, cortando) la hoja, polen, embrión, cotiledón, hipocótilo, células, protoplastos, célula meristemática, raíz, punta de la raíz, pistilo, antera, flor, punta de brotes, brote, tallo, fruto, pecíolo, etc. Cuando una planta entera se regenera por propagación vegetativa, también se denomina propagación vegetativa.
"Cultivo celular" o "cultivo de tejidos" se refiere al cultivo in vitro de células o tejidos de una planta.
"Regeneración" se refiere al desarrollo de una planta a partir de un cultivo celular o un cultivo de tejidos, o de propagación vegetativa.
"Transgén" o "gen quimérico" se refiere a un locus genético que comprende una secuencia de ADN, tal como un gen recombinante o un cromosoma recombinante o parte del mismo, que se ha introducido en el genoma de una planta de melón por transformación, tal como transformación mediada por Agrobacterium. Una planta que comprende un transgén integrado de manera estable en su genoma se denomina "planta transgénica". Un transgén o una planta transgénica también puede contener un cromosoma recombinante completo o parte de un cromosoma recombinante, por ejemplo, la parte que comprende el alelo de MYaV, introducido en el genoma por transformación.
Una "secuencia de ácido nucleico aislada" o "ADN aislado" se refiere a una secuencia de ácido nucleico que ya no se encuentra en el entorno natural del que se aisló, por ejemplo, la secuencia de ácido nucleico en una célula hospedadora bacteriana o en el genoma nuclear o plastídico de la planta.
Una "célula hospedadora" o una "célula hospedadora recombinante" o "célula transformada" son términos que se refieren a una nueva célula (u organismo) individual que surge como resultado de haber introducido en dicha célula al menos una molécula de ácido nucleico. La célula hospedadora es preferentemente una célula vegetal o una célula bacteriana. La célula hospedadora puede contener el ácido nucleico como una molécula replicativa extracromosómica (episómica), o comprender el ácido nucleico integrado en el genoma nuclear o plastídico de la célula hospedadora, o como un cromosoma introducido, por ejemplo, minicromosoma.
Descripción detallada de la invención
La presente invención desvela una planta Cucumis melo cultivada que comprende resistencia frente al virus asociado al amarilleamiento del melón (MYaV). En particular, la resistencia es conferida por un fragmento de introgresión en el cromosoma 6 del melón, en el que dicho fragmento de introgresión procede de una planta silvestre de la especie Cucumis melo o de un pariente silvestre del melón.
Los presentes inventores cruzaron dos accesiones distintas de C. melo, semillas representativas que se depositaron con el NCIMB 41966 y NCIMB 41969, con una línea reproductiva de melón susceptible a MYaV y con una variedad de melón susceptible, respectivamente, y llevó a cabo el mapeo de QTL, basándose en datos de fenotipado obtenidos de campos infestados por MYaV cerca de Mossoro (Rio Grande do Norte, Brasil).
Sorprendentemente, en ambas poblaciones de mapeo, se encontró en el cromosoma 6 del melón un QTL altamente significativo para la resistencia a MYaV, lo que indicó que distintas accesiones de Cucumis melo silvestre comprenden un locus de resistencia a MYaV en el cromosoma 6, que se transfirió a C. melo cultivado y confirió resistencia a MYaV a la planta de melón cultivada. En las dos poblaciones de mapeo, el QTL, que se llamó MYaV6.1, explicó el 32,6 % y el 91,7 % de la variación fenotípica observada para la resistencia a MYaV y, por lo tanto, es muy significativa.
Debe tenerse en cuenta que cuando se hace referencia en el presente documento a un (un) QTL (MYaV6.1) o a un locus que confiere resistencia a MYaV (o una parte que confiere resistencia del mismo) en el cromosoma 6 del genoma de C. melo, puede ser que en el cromosoma 6 haya en realidad dos (o más) QTL ligados entre sí, ya que la puntuación LOD tiene dos picos en ambas poblaciones de mapeo (véase la Figura 1). Por lo tanto, la referencia a un QTL o a un locus abarca la posibilidad de que haya dos (o más) QTL o dos (o más) locus acoplados entre sí en el cromosoma 6. Igualmente, en el presente documento la referencia a un fragmento de introgresión en el cromosoma 6 que tiene un QTL o un locus que confiere resistencia a MYaV (o una parte que confiere resistencia del mismo) abarca que el fragmento de introgresión comprenda todos los locus que confieren resistencia, o en casos de fragmentos de introgresión más pequeños, al menos una región de introgresión lo suficientemente grande (con uno, dos o más QTL) como para que el fragmento de introgresión confiera resistencia a MYaV cuando el fragmento de introgresión está en forma heterocigótica u homocigótica en el genoma de C. melo. Por tanto, en caso de fragmentos de introgresión más pequeños, el fragmento de introgresión comprende preferentemente al menos el QTL principal (es decir, el mayor de los dos picos del LOD en la Figura 1).
Por tanto, en un aspecto, se descubrió que está presente en el cromosoma 6 de los melones silvestres un locus de rasgo cuantitativo (QTL MYaV6.1) que confiere resistencia a MYaV y que este QTL, cuando se transfiere (introgresa) a una variedad o línea reproductiva de melón cultivado susceptible a MYaV, y cuando está presente en forma heterocigótica u homocigótica, confiere resistencia a MYaV a la planta de melón cultivada. El QTL, o el fragmento de introgresión que comprende el QTL (que comprende el alelo de resistencia a MYaV) es, por tanto, dominante, es decir, es suficiente tener el fragmento de introgresión en uno de los cromosomas 6 (un cromosoma 6 recombinante), mientras que el cromosoma 6 homólogo del par puede ser un cromosoma 6 (no recombinante) de C. melo cultivado que carece del fragmento de introgresión.
Aunque las fuentes actuales de introgresiones de alelos de resistencia a MYaV son dos fuentes silvestres (NCIMB 41966 y NCIMB 41969, de India y Uzbekistán, respectivamente), probablemente hay otras accesiones de Cucumis silvestres que comprenden alelos de MYaV o alelos ortólogos de MYaV en el mismo locus en el cromosoma 6. Dichos alelos de MYaV o alelos ortólogos de MYaV también se pueden identificar e introgresar en C. melo cultivado como se describe en el presente documento, para generar una planta de C. melo cultivada que comprenda un genoma de C. melo y un cromosoma 6 recombinante, por lo que el cromosoma 6 recombinante comprende un fragmento de introgresión de especies de Cucumis silvestre, que confiere un fenotipo de resistencia a MYaV al cultivo a la planta de C. melo cultivada cuando está presente en forma homocigótica o heterocigótica.
Las accesiones de melones silvestres y parientes silvestres del melón, tales como accesiones obtenibles de la colección del USDA National Plant Germplasm System u otras colecciones de semillas, pueden cribarse en cuanto a la resistencia a MYaV utilizando ensayos fenotípicos y/o de marcadores de MYaV, y las accesiones resistentes pueden cruzarse con una planta de Cucumis melo que carezca de resistencia a MYaV. Después, la generación F2 (o una generación posterior, tal como la F3 o una generación de retrocruzamiento) puede cribarse en cuanto a plantas recombinantes que tengan el fenotipo de resistencia MYaV y/o el fragmento de introgresión o una parte del mismo, utilizando los ensayos de marcadores moleculares descritos en el presente documento.
Plantas, semillas y partes de planta desveladas en la invención
Por tanto, en una primera divulgación se proporciona una planta de Cucumis melo cultivada que comprende resistencia frente al virus asociado al amarilleamiento del melón (MYaV).
La presencia de un fenotipo de resistencia MYaV se puede determinar utilizando el ensayo de resistencia a MYaV, por el cual las plantas se criban en cuanto a la resistencia en condiciones naturales de campo en una o más zonas donde la incidencia del MYaV sea alta, tal como el noreste de Brasil. Las plantas desveladas de acuerdo con la invención tienen resistencia a MYaV si su puntuación promedio de la enfermedad, en una escala de 9 = hojas totalmente verdes (en el primer 1/3 de la planta) a 1 = hojas totalmente amarillas (en el primer 1/3 de la planta), es
significativamente más alta que la puntuación promedio de la enfermedad de las variedades susceptibles a MYaV, cuando se cultivan en las mismas condiciones ambientales. La puntuación promedio de la enfermedad de las plantas de melón cultivadas resistentes a MYaV es, en una realización, de al menos 3, preferentemente de al menos 4, en una escala de 1 = hojas totalmente amarillas a 9 = hojas totalmente verdes, cuando se cultivan en el campo en el noreste de Brasil, o en cualquier otro campo donde la incidencia del MYaV sea alta. En otra realización, la puntuación promedio de la enfermedad es al menos de 5, 6, 7, 8 o 9. Se puede ver si la incidencia del MYaV es alta debido a los síntomas graves de amarilleamiento (puntación de la enfermedad promedio = 1) que se desarrollan en las plantas de control susceptibles, tales como los cultivares Sancho, Amaregal u otros. Alternativamente o además, se pueden determinar los niveles de virus MYaV en el tejido de melón, por ejemplo, utilizando anticuerpos policlonales desarrollados para la detección de MYaV.
Las puntuaciones de la enfermedad promedio se calculan preferentemente basándose en al menos cuatro plantas de una línea o variedad, preferentemente al menos 5, 10, 15, 20 o más plantas cultivadas en las mismas condiciones ambientales.
La resistencia frente al MYaV es conferida por un fragmento de introgresión en el cromosoma 6, en el que el fragmento de introgresión procede de un genoma de melón silvestre o de un pariente silvestre del melón. El fragmento de introgresión comprende el locus del rasgo cuantitativo (QTL) denominado en el presente documento MYaV6.1, locus que a su vez comprende un alelo de resistencia MYaV, o un alelo de resistencia ortólogo de MYaV, del gen de resistencia a MYaV.
Las plantas de melón cultivadas desveladas en el presente documento, por tanto, tienen un cromosoma 6 recombinante, que comprende un fragmento de introgresión de un cromosoma 6 de melón silvestre o de un cromosoma 6 ortólogo de un pariente silvestre del melón.
Como la resistencia es dominante, el fenotipo de resistencia se observa cuando el alelo de resistencia está en forma heterocigótica u homocigótica, las plantas de melón cultivadas desveladas en el presente documento tienen el fragmento de introgresión o la parte que confiere resistencia del mismo, en el cromosoma 6 en forma heterocigótica u homocigótica.
El fragmento de introgresión puede proceder de (o procede de), o es obtenible de (o se obtiene de) una planta silvestre de la especie Cucumis melo, que comprende el QTL de MYaV (MYaV6.1) en el cromosoma 6. Como alternativa, el fragmento de introgresión puede proceder de (o procede de), o es obtenible de (o se obtiene de) un pariente silvestre de Cucumis melo, que se puede cruzar con Cucumis melo (opcionalmente utilizando técnicas de rescate de embriones u otras, para ayudar a la producción de una descendencia viable), para que el fragmento del cromosoma 6 ortólogo pueda introgresarse en el cromosoma 6 de C. melo, especialmente C. melo cultivado.
En una divulgación específica, el fragmento de introgresión que comprende el locus de resistencia a MYaV puede proceder de (o procede de) o es obtenible de (o se obtiene de) plantas de C. melo silvestre, de las que se ha depositado una muestra representativa de semillas con el número de referencia NCIMB 41966 o NCIMB41969. En un aspecto, la invención desvela una planta de C. melo cultivada que comprende resistencia frente a MYaV, en la que la resistencia es conferida por un fragmento de introgresión en el cromosoma 6 del melón, en el que dicho fragmento de introgresión (que confiere dicha resistencia a MYaV) procede (o se puede obtener de) un cruce de una planta cuyas semillas se depositaron con el número de referencia NCIMB 41966 o NCIMB41969 con una planta de melón cultivada. Ambas accesiones de C. melo silvestre tienen un fenotipo de resistencia a MYaV, con una puntuación de la enfermedad promedio de 9,0 (las hojas permanecen verdes), en comparación con una puntación de la enfermedad promedio por debajo de 2,0, o por debajo de 1,5, para las variedades susceptibles de melón, tales como Amaregal F1. El fragmento de introgresión también puede proceder (o procede de) otras plantas de C. melo silvestres u otros parientes silvestres del melón, que tengan una puntación de la enfermedad por MYaV promedio de al menos 7, preferentemente de al menos 8, más preferentemente de 9, como, por ejemplo, se determina en el ensayo de resistencia a MYaV.
Otra divulgación se refiere a una planta desvelada en el presente documento, es decir, una planta de Cucumis melo cultivada que comprende resistencia frente al virus asociado al amarilleamiento del melón (MYaV), en la que dicha resistencia es conferida por un fragmento de introgresión en el cromosoma 6 en forma homocigótica o heterocigótica, y en la que dicho fragmento de introgresión procede de una planta silvestre de la especie Cucumis melo, en la que el fragmento de introgresión es idéntico al fragmento que confiere resistencia a MYaV en el cromosoma 6 como está presente en las semillas depositadas con el número Nc IMB 41966, NCIMB 41969, NCIMB 42113 o NCIMB 42198.
El experto en la materia es capaz de identificar e introgresar el QTL MYaV6.1 que comprende la región encontrada en otras accesiones de melón silvestre u otros parientes silvestres del melón, en C. melo cultivado como se explicará más adelante. El experto en la materia también puede identificar otros marcadores moleculares ligados a (asociados con) el QTL, que pueden utilizarse para identificar la presencia de un fragmento de introgresión de otros melones silvestres o parientes silvestres del melón en el cromosoma 6 de C. melo. Se descubrió que dos de los marcadores moleculares proporcionados en el presente documento están asociados con el QTL de resistencia a MYaV, cuando el fragmento de introgresión se obtuvo de dos fuentes silvestres distintas. Estos dos marcadores también pueden estar ligados a (asociados con) la resistencia a MYaV en el cromosoma 6, o en los cromosomas 6 ortólogos y, por tanto, pueden ser útiles para obtener el QTL de distintas fuentes. Como alternativa, el experto en la materia puede identificar
otros marcadores moleculares utilizando procedimientos conocidos.
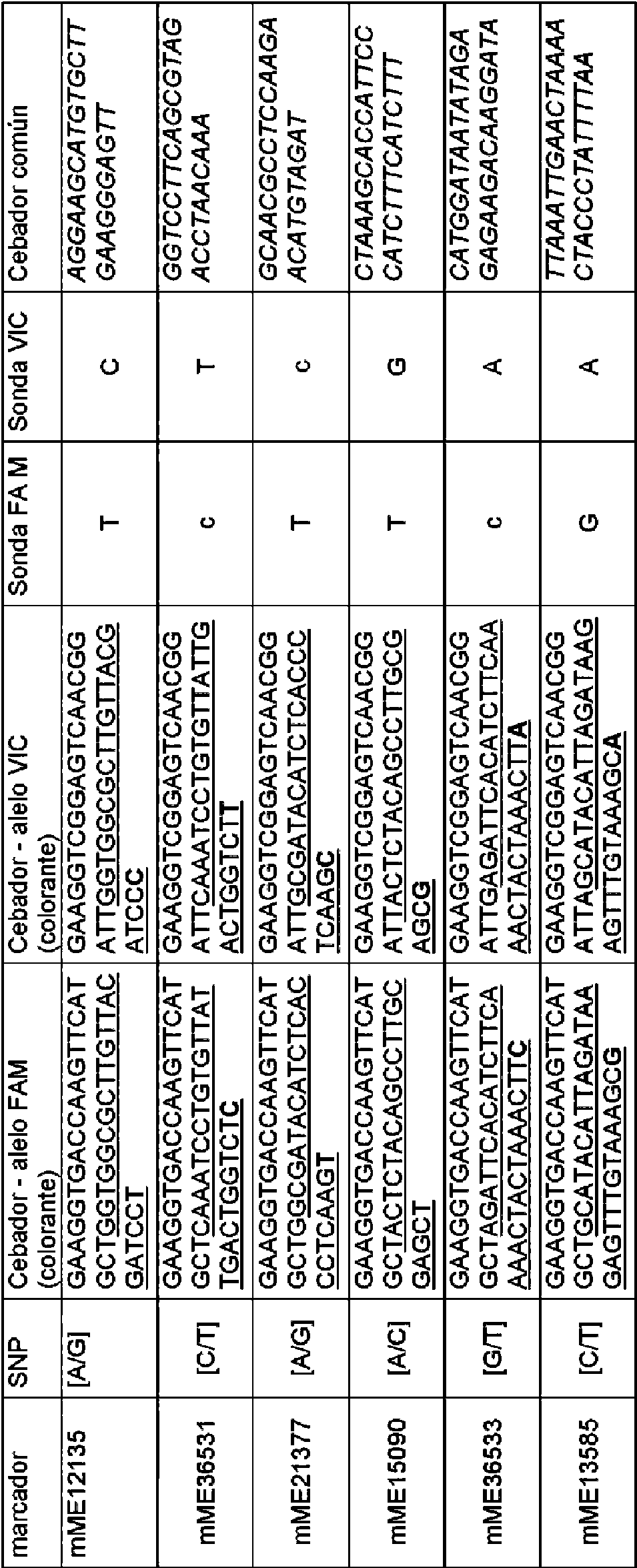
En una realización, la presencia del fragmento de introgresión, o la región del cromosoma 6 (o región del cromosoma 6 ortólogo), que comprende el locus de resistencia a MYaV, es detectable mediante un ensayo de marcadores moleculares que detecta al menos uno, preferentemente al menos los siguientes dos marcadores de polimorfismo mononucleotídico (SNP):
a) el genotipo CC o AC para el marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 (o la SEQ ID NO: 9);
b) el genotipo AA o AG para el marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3 (o la SEQ ID NO: 10).
Como se mencionó, se descubrió que estos dos marcadores de SNP están genéticamente ligados a (o asociados con) el fragmento de introgresión en el cromosoma 6 que comprende el QTL MYaV6.1 en ambas poblaciones de mapeo, es decir, en plantas que comprenden el QTL de resistencia de dos accesiones de melón silvestre distintas.
Por tanto, en un aspecto desvelado en el presente documento, las plantas resistentes al MYaV desveladas en el presente documento comprenden al menos una Citosina (C) (es decir, el genotipo CC o AC) en lugar de dos Adeninas (AA) en el nucleótido 71 de la SEQ ID NO: 1 (o la SEQ ID NO: 9) (denominado marcador de SNP mME15090) y/o comprenden al menos una Adenina (A) (es decir, el genotipo AA o AG) en lugar de dos Guaninas (GG) en el nucleótido 71 de la SEQ ID NO: 3 (o la SEQ ID NO: 10) (denominado marcador de SNP mME12135). Genotipo de SNP se refiere a dos nucleótidos, y a secuencias genómicas que comprenden uno de estos dos nucleótidos, uno en cada cromosoma 6. Entonces, una planta que tiene un genotipo CC para mME15090 tiene un nucleótido (C) idéntico en ambos cromosomas, mientras que una planta que tiene un genotipo AC para mME15090 tiene un cromosoma con una A en el nucleótido 71 de la SEQ ID NO: 1 y un cromosoma con una C en el nucleótido 71 de la SEQ ID NO: 1.
En una realización adicional, el fragmento de introgresión, o la región del cromosoma 6 (o región del cromosoma 6 ortólogo), que comprende el locus de resistencia a MYaV, es detectable mediante un ensayo de marcadores moleculares que detecta adicionalmente al menos uno, dos, tres, cuatro, cinco, seis, siete, o los ocho marcadores de polimorfismo mononucleotídico (SNP) seleccionados del grupo que consiste en:
a) el genotipo GG o AG para el marcador de SNP mME40332 en la SEQ ID NO: 2;
b) el genotipo TT o AT para el marcador de SNP mME28908 en la SEQ ID NO: 4;
c) el genotipo TT para el marcador de SNP mME36531 en la SEQ ID NO: 5;
d) el genotipo AA o AT para el marcador de SNP mME9692 en la SEQ ID NO: 6;
e) el genotipo CC o CT para el marcador de SNP mME50656 en la SEQ ID NO: 7;
f) el genotipo AA o AG para el marcador de SNP mME21377 en la SEQ ID NO: 8;
g) el genotipo TT o GT para el marcador de SNP mME36533 en la SEQ ID NO: 11;
h) el genotipo TT o CT para el marcador de SNP mME13585 en la SEQ ID NO: 12.
Por tanto, la planta de melón resistente a MYaV desvelada en el presente documento comprende adicionalmente al menos una Guanina (G) (es decir, el genotipo GG o AG) en lugar de dos Adeninas (AA) en el nucleótido 71 de la SEQ ID NO: 2 (denominado marcador de SNP mME40332), y/o al menos una Timina (T) (es decir, el genotipo TT o AT) en lugar de dos Adeninas (AA) en el nucleótido 71 de la s Eq ID NO: 4 (denominado marcador de SNP mME28908), y/o dos Timinas (TT ) (es decir, el genotipo TT) en lugar de dos Citosinas (CC) o en lugar de CT en el nucleótido 71 de la SEQ ID NO: 5 (denominado marcador de SNP mME36531), y/o al menos una Adenina (A) es decir, el genotipo AA o AT) en lugar de dos Timinas (TT) en el nucleótido 71 de la Se Q ID NO: 6 (denominado marcador de SNP mME9692), y/o al menos una Citosina (C) (es decir, el genotipo CC o CT) en lugar de dos Timinas (TT) en el nucleótido 71 de la SEQ ID NO: 7 (denominado marcador de SNP mME50656), y/o al menos una Adenina (A) es decir, el genotipo AA o AG) en lugar de dos Guaninas (GG) en el nucleótido 71 de la SEQ ID NO: 8 (denominado marcador de SNP mME21377), y/o al menos una Timina (T) (es decir, el genotipo TT o GT) en lugar de dos Guaninas (GG) en el nucleótido 71 de la SEQ ID NO: 11 (denominado marcador de SNP mME36533), y/o al menos una Timina (T) (es decir, el genotipo TT o CT) en lugar de dos Citosinas (CC) en el nucleótido 71 de la SEQ ID NO: 12 (denominado marcador de SNP mME13585).
En un aspecto, el fragmento de introgresión, o la región del cromosoma 6 (o región del cromosoma 6 ortólogo), que comprende el locus de resistencia a MYaV, que es detectable mediante los marcadores anteriores, procede de una planta silvestre de la especie Cucumis melo, y en un aspecto procede de una planta de la cual se ha depositado una muestra representativa de semillas con los números de referencia NCIMB 41966 y NCIMB 41969, por tanto, el QTL y la región del cromosoma 6 que comprende el QTL, es en un aspecto el QTL como se encuentra en el NCIMB 41966 o en el NCIMB 41969. En un aspecto, el fragmento de introgresión, o el cromosoma 6 recombinante, se obtiene al
cruzar una planta cultivada a partir de semillas depositadas con el número de referencia NCIMB 41966 o NCIMB 41969 con otra planta de melón, especialmente una planta de melón cultivada de la especie C. melo.
Por tanto, en un aspecto, la planta de melón resistente a MYaV desvelada en el presente documento comprende un fragmento de introgresión en el cromosoma 6, que se puede obtener a partir de semillas de las que se ha depositado una muestra representativa con el NCIMB 41966 y en el que dicho fragmento de introgresión comprende al menos dos, opcionalmente al menos 3, 4, 5, 6 o 7, marcadores de SNP seleccionados del grupo que consiste en:
a) el genotipo CC o AC para el marcador de SNP mME15090 en la SEQ ID NO: 1;
b) el genotipo GG o AG para el marcador de SNP mME40332 en la SEQ ID NO: 2;
c) el genotipo AA o AG para el marcador de SNP mME12135 en la SEQ ID NO: 3.
d) el genotipo TT o AT para el marcador de SNP mME28908 en la SEQ ID NO: 4;
e) el genotipo TT para el marcador de SNP mmME36531 en la SEQ ID NO: 5;
f) el genotipo AA o AT para el marcador de SNP mME9692 en la SEQ ID NO: 6;
g) el genotipo CC o CT para el marcador de SNP mME50656 en la SEQ ID NO: 7.
En otro aspecto, la planta de melón resistente a MYaV desvelada en el presente documento comprende un fragmento de introgresión en el cromosoma 6, que se puede obtener a partir de semillas de las que se ha depositado una muestra representativa con el NCIMB 41969 y en el que dicho fragmento de introgresión comprende al menos dos, opcionalmente al menos 3, 4 o 5 marcadores de SNP seleccionados del grupo que consiste en:
a) el genotipo AA o AG para el marcador de SNP mME21377 en la SEQ ID NO: 8;
b) el genotipo CC o AC para el marcador de SNP mME15090 en la SEQ ID NO: 9;
c) el genotipo AA o AG para el marcador de SNP mME12135 en la SEQ ID NO: 10;
d) el genotipo TT o GT para el marcador de SNP mME36533 en la SEQ ID NO: 11;
e) el genotipo TT o CT para el marcador de SNP mME13585 en la SEQ ID NO: 12.
Para obtener el fragmento de introgresión de las semillas depositadas, se cultiva una planta a partir de la semilla y la planta se cruza con una planta susceptible de C. melo para obtener semillas F1. La semilla híbrida F1 y las plantas cultivadas a partir de ella, contienen un cromosoma 6 del parental susceptible (sin QTL MYaV6.1) y un cromosoma 6 del parental silvestre resistente a MYaV. Para generar eventos de recombinación entre estos dos cromosomas 6 homólogos, debe tener lugar la meiosis y las plantas que comprenden los cromosomas 6 recombinantes deben identificarse. Por ejemplo, la F1 puede autofecundarse para producir plantas F2, y/o las plantas F2 resistentes o plantas F3, etc., puede retrocruzarse con el parental susceptible. Las plantas que son resistentes a MYaV pueden cribarse y seleccionarse en cuanto a, la presencia de uno o más de los marcadores de SNP anteriores, para identificar plantas que comprenden un cromosoma 6 recombinante, que comprenda un fragmento de introgresión que confiere una resistencia a MYaV de las semillas depositadas.
De forma análoga, las plantas de melón cultivadas que comprenden resistencia frente a MYaV, en que la resistencia se confiere mediante un fragmento de introgresión en el cromosoma 6, pueden generarse y/o identificarse utilizando distintos procedimientos. Por ejemplo, para obtener una planta de melón cultivada que comprenda un fragmento de introgresión que confiere resistencia a MYaV procedente de un melón silvestre o un pariente silvestre del melón, en primer lugar se identifica un melón silvestre o un pariente silvestre del melón que tenga un fenotipo de resistencia MYaV y/o que comprenda uno o más de los marcadores de SNP asociados con la resistencia a MYaV desvelados en el presente documento, por ejemplo, uno cualquiera, o más, o todos los marcadores anteriores. La planta identificada se cruza con una planta susceptible de C. melo para obtener semillas F1. La semilla híbrida F1 y las plantas cultivadas a partir de ella, contienen un cromosoma 6 del parental susceptible (sin QTL MYaV6.1) y un cromosoma 6 del parental silvestre resistente a MYaV. Para generar eventos de recombinación entre estos dos cromosomas 6 homólogos debe tener lugar la meiosis y las plantas que comprenden los cromosomas 6 recombinantes deben identificarse. Por ejemplo, la F1 puede autofecundarse para producir plantas F2, y/o las plantas F2 resistentes o plantas F3, etc., puede retrocruzarse con el parental susceptible. Las plantas que son resistentes a MYaV pueden cribarse y/o seleccionarse en cuanto a la presencia de uno o más de los marcadores de SNP anteriores, y/o cribarse y/o seleccionarse en cuanto a la presencia del fenotipo de resistencia a MYaV, para identificar plantas que comprendan un cromosoma 6 recombinante que comprenda un fragmento de introgresión que confiere una resistencia a MYaV procedente de un melón silvestre o un pariente silvestre del melón. Como alternativa o además, se puede llevar a cabo el mapeo del QTL para identificar marcadores moleculares adicionales ligados al QTL MYaV6.1 y/o generar cultivos de plantas de C. melo que comprenden un fragmento de introgresión en el cromosoma 6, que confiere resistencia a MYaV.
En una realización, la presencia del fragmento de introgresión, o la región del cromosoma 6 (o región del cromosoma
6 ortólogo), que comprende el locus de resistencia a MYaV, es detectable mediante un ensayo de marcadores moleculares que detecta al menos uno de los siguientes marcadores:
a) el genotipo CC o AC para el marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 (o la SEQ ID NO: 9);
b) el genotipo AA o AG para el marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3 (o la SEQ ID NO: 10)
En una realización, se detecta al menos el marcador de a) y de b).
Los marcadores moleculares descritos en el presente documento pueden detectarse de acuerdo con el procedimiento convencional. Por ejemplo, los marcadores de SNP se pueden detectar fácilmente utilizando un ensayo KASP (véase www.kpbioscience.co.uk) u otros ensayos. Se ha desarrollado un ensayo KASP para varios de los SNP en el Ejemplo 3. Para desarrollar el ensayo KASP, se seleccionaron 70 pares de bases corriente arriba y 70 pares de bases corriente abajo del SNP y se diseñaron dos cebadores directos específicos de alelo y un cebador inverso específico de alelo. Véase, por ejemplo, Allen y col. 2011, Plant Biotechnology J. 9, 1086-1099, en especial las pág. 097-1098 en cuanto al procedimiento del ensayo KASP.
Por tanto, en un aspecto, los marcadores de SNP y la presencia/ausencia del marcador asociado con el alelo de resistencia a MYaV se determinan utilizando un ensayo KASP, pero igualmente se pueden utilizar otros ensayos. Por ejemplo, de forma opcional, también se puede utilizar secuenciación de ADN.
Se puede llevar a cabo mapeo físico utilizando los BAC (cromosomas artificiales bacterianos) y el desarrollo de marcadores para BAC, para mapear la ubicación física de MYaV6.1 en el cromosoma 6 y para desarrollar marcadores que se encuentren físicamente entre cualquiera de los marcadores mencionados, y para determinar distancias físicas entre marcadores y/o determinar el tamaño de la introgresión.
El tamaño de un fragmento de introgresión también puede determinarse, por ejemplo, mediante la visualización de la introgresión utilizando imágenes de hibridación fluorescente in situ (FISH, forma siglada de fluorescent in situ hybridization) (Verlaan y col. 2011, Plant Journal 68: 1093-1103).
En un aspecto desvelado, el fragmento de introgresión que confiere resistencia a MYaV tiene un tamaño igual o inferior a 10 Mb, preferentemente un tamaño igual o inferior a 8 Mb, un tamaño igual o inferior a 7, 6, 5, 4, 3, 2 o 1 Mb, más preferentemente incluso inferior, tal como igual o inferior a 500 kb, 400 kb, 300 kb, 200 kb, 100 kb, 50 kb, 25 kb, 20 kb, 15 kb o inferior, pero aún comprende el alelo de resistencia a MYaV y aún confiere resistencia a MYaV a una planta de C. melo que de otro modo sería susceptible. La resistencia es conferida por el cromosoma 6 recombinante y el fragmento de introgresión que comprende el alelo de MYaV cuando el fragmento de introgresión está en forma heterocigótica u homocigótica. Las plantas con fragmentos de introgresión más pequeños en el cromosoma 6 pueden generarse al generar nuevas plantas recombinantes a partir de una población de plantas obtenidas de un cruce entre una planta cultivada susceptible a MYaV y un melón o pariente del melón resistente a MYaV silvestre. Como alternativa, cuando se identifica una planta de C. melo cultivada que tiene un fragmento de introgresión que confiere resistencia a MYaV, el tamaño de la introgresión puede reducirse, por ejemplo, autofecundando esa planta y seleccionando una progenie recombinante que tenga tamaños de introgresión más pequeños.
En el tomate, por ejemplo, el gran fragmento de introgresión en el cromosoma 6 (de aproximadamente 27 cM) de S. chilense que comprende el alelo Ty-3 se ha reducido seleccionando una línea de progenie recombinante (LA1931-AL-F2), que comprende un fragmento de introgresión de S. chilense mucho más pequeño (de aproximadamente 6 cM) que comprende a Ty-3 (véase Ji y col. 2007, Mol. Breeding 20: 271-284).
La planta de melón cultivada desvelada puede ser endogámica o un híbrido F1. En un aspecto, el híbrido F1 comprende el fragmento de introgresión en forma heterocigótica, es decir, producido al cruzar dos líneas parentales endogámicas, una de las cuales posee el fragmento de introgresión (preferentemente en forma homocigótica, aunque no necesariamente), y recogiendo las semillas híbridas F1 de dicho cruce. El híbrido F1 también puede comprender el fragmento de introgresión en forma homocigótica, es decir, producido al cruzar dos líneas parentales endogámicas, comprendiendo cada una el fragmento de introgresión en forma homocigótica o heterocigótica.
La planta de melón cultivada puede ser de cualquier tipo. Preferentemente, tiene buenas características agronómicas y de buena calidad del fruto, tal como un tamaño promedio grande del fruto (al menos de 500 g, 600 g, 700 g, 800 g, 900 g, 1000 g o más), un alto brix promedio de los frutos (por ejemplo, un % de sólidos solubles totales promedio de refractómetro de al menos el 10 %, 12 %, 14 %, 16 %, 18% o más), muchos frutos producidos por planta, pulpa del fruto firme, etc. El melón cultivado puede ser un C. melo cantalupensis, C. melo inodorous y C. melo reticulatus. Los C. melo cantalupensis también se denominan cantalupos y son principalmente de forma redonda con estrías prominentes y casi sin reticulado. La mayoría tiene una pulpa naranja y dulce, y habitualmente son muy fragantes. En contraste con el melón europeo, el "cantalupo" norteamericano no es de este tipo, pero pertenecen a los melones almizcleños verdaderos. Los C. melo inodorous (o melones de invierno) se pueden subdividir en distintos tipos, tal como el melón Honeydew, Piel de sapo, melón Sugar, melón japonés, etc. C. melo reticulatus es el melón almizcleño verdadero, que tiene una piel reticulada (con forma de red) e incluye melones Galia, melones Sharlyn y el cantalupo
norteamericano. Los melones tienen muchos tamaños y formas, entre ellas redonda, ovalada y cilindrica. La pulpa es en general naranja y bastante dulce, pero algunas variedades de melón y, específicamente, los melones persas, puede tener pulpa verde o blanca. Algunos melones con pulpa verde son bastante dulces, pero la mayoría de los melones con pulpa verde y blanca tienen un sabor menos dulce, pero sí un sabor muy refrescante.
Además, se pueden introducir otras resistencias en las plantas de melón desveladas, tal como resistencia a una o más de las siguientes enfermedades: marchitez bacteriana, podredumbre de la raíz, colapso del melón, óxido del melón, oídio, marchitamiento por Vertiállium, quemadura por azufre, gomosis, mosaico de la sandía, mildiu velloso, Fusarium oxysporum f.sp. melonis (Fom) raza 0, Fusarium oxysporum f.sp. melonis (Fom) raza 1, Fusarium oxysporum f.sp. melonis (Fom) raza 2, Fusarium oxysporum f.sp. melonis (Fom) raza 1,2, marchitamiento por Fusarium R2, nematodo formador de agallas, antracnosis, mosaico del pepino y mosaico de la calabaza, y/o resistencia a una o más de las siguientes plagas: resistencia a los áfidos, gusano del pepino, tenebriónido de tierra, escarabajo del pepino con bandas, ácaros, escarabajo de occidental manchado del pepino, saltamontes del melón, gusano del melón, escarabajo occidental rayado del pepino o minador del melón. Además, se pueden introducir otros genes de resistencia frente a virus patógenos, hongos, bacterias o plagas.
En un aspecto, se desvelan semillas a partir de las cuales se pueden cultivar plantas como se desvelan en el presente documento. En un aspecto, las semillas son semillas F1 híbridas, que comprenden el cromosoma 6 recombinante en forma homocigótica o heterocigótica, y que tienen un fenotipo de resistencia a MYaV cuando se cultivan en el campo.
Además, se desvelan recipientes y envases que contienen o comprenden semillas a partir de las cuales se pueden cultivar plantas desveladas en el presente documento. Estos pueden etiquetarse como que contienen semillas de melón cultivado que tienen resistencia a MYaV.
Además, se desvelan semillas de progenie y plantas de progenie de plantas desveladas en el presente documento, que conservan en el cromosoma 6 la introgresión que confiere resistencia a MYaV, o una introgresión más pequeña, es decir, una parte del fragmento de introgresión que confiere resistencia. La progenie puede ser cualquier generación obtenida por autofecundación de una planta de melón desvelada en el presente documento y/o cruzando una o más veces una planta de melón desvelada en el presente documento con otra planta de melón. La progenie es, por lo tanto, ya sea la generación (semillas) producida a partir del primer cruce (F1) o por autofecundación (S1), o cualquier otra generación producida por cruce y/o autofecundación (F2, F3, etc.) y/o retrocruzamiento (BC1, BC2, etc.) de una o más plantas seleccionadas de la generación F1 y/o S1, y/o BC1 (o plantas de cualquier generación posterior, por ejemplo, la F2) con otra planta de melón (y/o con un pariente silvestre del melón). La progenie se selecciona preferentemente para conservar el cromosoma 6 recombinante que comprende el fragmento de introgresión del melón silvestre o de un pariente silvestre del melón. Por lo tanto, la progenie también tiene el fenotipo de resistencia a MYaV, preferentemente el mismo nivel de resistencia a MYaV que la planta utilizada en el cruce o autofecundación inicial. La presencia (o retención) del fragmento de introgresión que comprende el QTL MYaV6.1 puede determinarse en el ensayo de resistencia a MYaV, fenotípicamente y/o por el ensayo (o ensayos) de marcadores moleculares descritos en el presente documento. En cuanto a la evaluación fenotípica, obviamente se debe tener en cuenta la naturaleza de dominancia del alelo MYaV.
En un aspecto adicional, se desvelan partes de las plantas de melón de acuerdo con la invención. Las partes incluyen, por ejemplo, células y cultivos celulares, cultivos de tejidos, tejidos vegetales vegetativos (hojas, raíces, etc.), flores, polen, embriones, frutos, partes de frutos, etc. Las partes de planta comprenden el fragmento de introgresión en el cromosoma 6, como se describe, y como se puede detectar utilizando uno o más de los ensayos de marcadores de MYaV descritos. Además, cuando se regeneran plantas enteras a partir de tales partes de melón, tales como células, cultivos de células o tejidos, las plantas regeneradas comprenden el cromosoma 6 recombinante y el fenotipo de resistencia MYaV.
Por tanto, también se desvela una célula vegetal, tejido o parte de planta de una planta o de una semilla desvelada en el presente documento que comprende al menos un cromosoma 6 recombinante, en el que dicho cromosoma 6 recombinante comprende un fragmento de introgresión de una planta de C. melo silvestre y en el que dicho fragmento de introgresión comprende un alelo que confiere resistencia a MYaV.
Además, se desvelan en el presente documento cultivos celulares in vitro y cultivos de tejidos in vitro, de células o tejidos que comprenden un cromosoma 6 recombinante descrito. Preferentemente, las células o tejidos pueden regenerarse en una planta de melón entera, es decir, las células son células regenerables y los tejidos comprenden células regenerables. Por tanto, también se desvelan en el presente documento propagaciones vegetativas de las plantas de acuerdo con la invención. Por tanto, se desvela una planta de melón cultivada propagada vegetativamente que comprende el fenotipo de resistencia MYaV y un cromosoma 6 recombinante como se describe en el presente documento.
En un aspecto específico, se desvela un fruto de melón cosechado a partir de una planta de acuerdo con la invención. Los frutos de melón comercializables generalmente se clasifican por tamaño y calidad después de la cosecha. Además, se desvelan recipientes o envases que comprenden o consisten en frutos de melón cosechados. De nuevo, las células de los frutos se pueden distinguir de otros melones por la presencia del cromosoma 6 recombinante (como se puede determinar en uno o más de los ensayos de marcadores moleculares y/o en un ensayo de resistencia a
MYaV, por ejemplo, cultivando las semillas presentes en los frutos, o la progenie obtenida autofecundando las plantas cultivadas a partir de las semillas).
La invención también desvela un alimento o producto alimenticio que comprende o que consiste en una parte de planta descrita en el presente documento preferentemente un fruto de melón, o una parte de la misma, y/o un extracto de una parte de planta descrita en el presente documento. La comida o el producto alimenticio puede ser fresco o procesado, por ejemplo, enlatado, al vapor, hervido, frito, escaldado y/o congelado, etc. Por ejemplo, también se proporcionan en el presente documento recipientes tales como latas, cajas, cajones, bolsas, cajas de cartón, envases de atmósfera modificada, películas (por ejemplo, películas biodegradables), etc., que comprende partes de planta tales, como frutos o partes de frutos (frescos y/o procesados), descritas en el presente documento.
Procedimientos y usos de acuerdo con la invención
La invención desvela un procedimiento para la producción de una nueva planta de melón cultivada que comprende un fragmento de introgresión que confiere resistencia a MYaV cuando está en forma homocigótica, como se describe. El procedimiento comprende cruzar una planta desvelada en el presente documento, o una planta de progenie de la misma, ya sea como parental masculino o femenino, con una segunda planta de melón (o un pariente silvestre del melón) una o más veces, y/o autofecundar una planta de melón desvelada en el presente documento, o una planta de progenie de la misma una o más veces, y seleccionar la progenie de dicho cruce y/o autofecundación. La primera y/o la segunda planta de melón pueden ser, por ejemplo, una línea o variedad de las especies C. melo cantalupensis, C. melo inodorous o C. melo reticulatus.
Por tanto, se desvela en el presente documento un procedimiento para transferir el cromosoma 6 recombinante, que comprende el locus que confiere resistencia a MYaV (MYaV6.1), de una planta de melón (cultivada) a otra planta de melón (cultivada), especialmente a variedades o líneas de reproducción susceptibles a MYaV.
El procedimiento comprende las etapas de:
a) proporcionar una primera planta de melón que comprende al menos un cromosoma 6 recombinante que tiene un fragmento de introgresión que comprende un alelo que confiere resistencia a MYaV en forma homocigótica,
b) proporcionar una segunda planta de melón, especialmente una planta de melón susceptibles a MYaV,
c) cruzar dicha planta de melón de a) con dicha planta de melón de b),
d) recoger semillas F1 híbridas de dicho cruce y, opcionalmente
e) autofecundar la planta cultivada a partir de dichas semillas F1 híbridas para producir semillas F2, y opcionalmente seleccionar las semillas F2 que tienen el cromosoma 6 recombinante, y opcionalmente
f) llevar a cabo mejora genética adicional con plantas cultivadas a partir de dichas semillas F2 para producir una planta de melón que tenga buenas características agronómicas y que comprenda el fragmento de introgresión en forma homocigótica o heterocigótica.
La presencia o ausencia del cromosoma 6 recombinante y del fragmento de introgresión, puede determinarse mediante uno o más de los ensayos de marcadores moleculares descritos en el presente documento y/o mediante ensayos de resistencia a MYaV. La mejora genética adicional de la etapa f) puede comprender autofecundación, cruce, producción de haploides dobles, retrocruzamiento, etc. En el presente documento se describen plantas y semillas obtenibles por el procedimiento anterior.
Además, se desvela un procedimiento para la producción de plantas F1 híbridas de C. melo que comprendan un fenotipo de resistencia MYaV, que comprende:
a) proporcionar una primera planta de melón endogámica que comprenda al menos un cromosoma 6 recombinante que tiene un fragmento de introgresión que comprende un alelo que confiere resistencia a MYaV,
b) proporcionar una segunda planta de melón endogámica con o sin cromosoma 6 recombinante que tenga un fragmento de introgresión que comprende un alelo que confiere resistencia a MYaV,
c) cruzar dicha planta de melón de a) con dicha planta de melón de b),
d) recoger semillas F1 híbridas de dicho cruce.
La planta de melón endogámica de a) y b) puede ser homocigótica y/o heterocigótica para el fragmento de introgresión, y puede contener fragmentos de introgresión de distintos tamaños y/o de distinto origen, es decir, de distintos melones silvestres o parientes silvestres del melón.
Las semillas F1 híbridas comprenden preferentemente al menos un cromosoma 6 recombinante y las plantas F1 cultivadas a partir de las semillas son, por lo tanto, resistentes a MYaV en su fenotipo.
La presencia o ausencia del cromosoma 6 recombinante y del fragmento de introgresión, puede determinarse mediante uno o más de los ensayos de marcadores moleculares descritos en el presente documento y/o mediante ensayos de resistencia a MYaV. En el presente documento se describen plantas y semillas obtenibles por el procedimiento anterior.
En un aspecto distinto se desvela un procedimiento para la producción de una planta de C. melo cultivada que comprende un fragmento de introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV, comprendiendo dicho procedimiento las etapas:
a) proporcionar una primera planta de melón cultivada que sea susceptible al MYaV,
b) proporcionar una segunda planta de melón silvestre con resistencia a MYaV,
c) cruzar dicha planta de melón de a) con dicha planta de melón de b),
d) recolectar semillas F1 de dicho cruce y realizar un retrocruzamiento de una planta F1 con la planta de melón de a) para producir una población de retrocruzamiento (BC1), o autofecundar dichas plantas F1 una o más veces para producir una población autofecundada de generación F2 o F3 o superior,
e) opcionalmente retrocruzar una planta de d) una o más veces con la planta de melón de a) para producir una población de retrocruzamiento de mayor generación, y
f) identificar una generación F2, F3, o autofecundación de generación superior, o BC1 o planta de retrocruzamiento de generación superior que comprende una introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV.
Cuando se hace referencia a poblaciones de retrocruzamiento en el procedimiento, las poblaciones de retrocruzamiento también pueden ser autofecundadas, es decir, BC1S1, BC1S2, BC2S1, BC2S2 u otras.
En una o más de las etapas b) a f), se puede analizar la presencia del alelo de resistencia a MYaV (o el fragmento de introgresión o la región del cromosoma 6 silvestre que comprende el alelo) (y se pueden seleccionar las plantas) llevando a cabo un ensayo de marcadores moleculares como se describe en otra parte en el presente documento, por ejemplo, determinando si la planta comprende el genotipo CC o AC para el marcador de SNP mME15090 en la SEQ ID NO: 1 y el genotipo AA o AG para el marcador de SNP mME12135 en la SEQ ID NO: 3, o cualquier marcador específico del genoma de melón silvestre o de un pariente silvestre del melón entre el marcador mME15090 y mME12135.
Utilizando este procedimiento, se pueden generar y/o seleccionar nuevas plantas de melón cultivadas que comprendan una introgresión con el QTL MYaV6.1 de una fuente silvestre, tal como un melón silvestre o un pariente silvestre del melón (tal como del NCIMB 41966 o NCIMB 41969, u otros melones silvestres o parientes silvestres del melón).
En un aspecto, se desvela en el presente documento el procedimiento para la producción de una planta de C. melo cultivada que comprende un fragmento de introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV, que comprende las etapas:
a) proporcionar una primera planta de melón cultivada que sea susceptible al MYaV,
b) proporcionar una segunda planta de melón silvestre con resistencia a MYaV,
c) cruzar dicha planta de melón de a) con dicha planta de melón de b),
d) recolectar semillas F1 de dicho cruce y realizar un retrocruzamiento de una planta F1 con la planta de melón de a) para producir una población de retrocruzamiento (BC1), o autofecundar dichas plantas F1 una o más veces para producir una población F2 o F3,
e) opcionalmente, autopolinizar la población de retrocruzamiento para producir, por ejemplo, una población BC1S1 o BC1S2,
f) identificar una planta F2, F3, BC1 BC1S1 o BC1S2 que comprenda el genotipo CC o AC para el marcador de SNP mME15090 en la SEQ ID NO: 1 y el genotipo AA o AG para el marcador de SNP mME12135 en la SEQ ID NO: 3, o cualquier marcador específico del genoma de melón silvestre o de un pariente silvestre del melón entre el marcador mME15090 y mME12135.
Además, se proporciona un procedimiento para identificar una planta de melón silvestre que comprende resistencia a MYaV en el cromosoma 6, comprendiendo dicho procedimiento:
a) proporcionar una accesión de melón silvestre o varias accesiones de melón silvestre;
b) cribar dicha accesión (o accessiones) de melón silvestre utilizando un ensayo de marcadores moleculares que detecta al menos un marcador de SNP seleccionado del grupo que consiste en:
marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y marcador de SNP mME12135 en el
nucleótido 71 de la SEQ ID NO: 3; y
c) identificar y/o seleccionar una planta de melón silvestre que comprende al menos el genotipo CC o AC para el marcador de SNP mME15090 en el nucleótido 71 de la Se Q ID NO: 1 y el genotipo AA o AG para el marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3; y, opcionalmente
d) confirmar la resistencia a MYaV en un ensayo de resistencia a MYaV.
En la etapa c) también se pueden utilizar otras pruebas de marcadores moleculares descritas en otra parte en el presente documento. Con este procedimiento se puede, por tanto, cribar las accesiones de melón silvestre o parientes silvestres del melón en cuanto a la presencia de uno o más de los marcadores y, por tanto, la presencia del QTL MYaV6.1 e introgresar la parte que confiere resistencia de estas nuevas fuentes de resistencia en plantas de melón cultivadas susceptibles a MYaV. Además, se desvelan plantas y semillas obtenidas mediante este procedimiento.
En otro aspecto más se proporciona un procedimiento para la identificación de una planta de C. melo cultivada que comprende un fragmento de introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV, comprendiendo dicho procedimiento:
a) proporcionar una población de plantas de C. melo cultivadas recombinantes (tal como una autopolinización de generación F2, F3 o superior, población de retrocruzamiento de generación BC1, BC2, BC1S1 o superior),
b) cribar dicha población utilizando un ensayo de marcadores moleculares que detecta al menos un marcador de SNP seleccionado del grupo que consiste en:
marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3; y
c) identificar y/o seleccionar una planta que comprende al menos el genotipo CC o AC para el marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y el genotipo AA o AG para el marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3.
En este procedimiento también se pueden utilizar otras pruebas de marcadores moleculares descritas en otra parte en el presente documento. Por tanto, utilizando este procedimiento, se puede detectar la presencia de un fragmento de introgresión en el cromosoma 6 que comprende el QTL MYaV6.1 en plantas o partes de plantas de melón cultivadas.
En aún otro aspecto se proporciona un procedimiento para detectar si una planta de C. melo cultivada comprende un fragmento de introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV, comprendiendo dicho procedimiento:
a) proporcionar una planta de C. melo cultivada,
b) cribar dicha planta utilizando un ensayo de marcadores moleculares que detecta al menos un marcador de SNP seleccionado del grupo que consiste en:
marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3.
El cribado de marcadores moleculares obviamente implica obtener material vegetal y analizar el ADN genómico del material en cuanto al genotipo del marcador.
En este procedimiento también se pueden utilizar otras pruebas de marcadores moleculares descritas en otra parte en el presente documento. Por tanto, utilizando este procedimiento, se puede detectar la presencia de un fragmento de introgresión en el cromosoma 6 que comprende el QTL MYaV6.1 en plantas o partes de plantas de melón cultivadas. Si están presentes uno o más de los marcadores que están ligados al QTL, se puede concluir que la planta comprende un fragmento de introgresión que confiere resistencia a MYaV en el cromosoma 6.
Además, se pueden utilizar los procedimientos y los marcadores descritos en el presente documento para reducir el tamaño del fragmento de introgresión silvestre que comprende el QTL MYaV6.1, es decir, para generar y seleccionar recombinantes que tienen un fragmento de introgresión más pequeño en el cromosoma 6, pero que conserven la resistencia a MYaV que confiere parte del fragmento de introgresión. Se pueden desarrollar igualmente marcadores moleculares alternativos ligados a MYaV6.1 para su uso en cualquiera de los procedimientos mencionados anteriormente.
En un aspecto, la invención desvela el uso de un cromosoma 6 recombinante que comprende un fragmento de introgresión de una planta de C. melo silvestre, comprendiendo dicho fragmento de introgresión un alelo que confiere resistencia a MYaV, para la mejora genética de variedades de melón con resistencia a MYaV.
En un aspecto, la invención desvela el uso de un cromosoma 6 recombinante que comprende un fragmento de introgresión de una planta de C. melo silvestre, comprendiendo dicho fragmento de introgresión un alelo que confiere resistencia a MYaV, para la mejora genética de variedades de melón con resistencia a MYaV, en los que dichos
cromosomas 6 recombinantes es el cromosoma 6 recombinante como se encuentra en las semillas depositadas con el número de referencia NCIMB 42113 o NCIMB 42198, o se obtiene de dicho cromosoma 6 recombinante. Por tanto, en un aspecto, se desvela una planta de melón cultivada que comprende un cromosoma 6 recombinante obtenido mediante (obtenible mediante) el cruce de una planta cultivada a partir de semillas depositadas con el número de referencia NCIMB 42113, o NCIMB 42198, o de la progenie de las mismas que conservan el cromosoma 6 recombinante, con otra planta de melón.
En un aspecto, las plantas, células, tejidos y partes de planta desvelados no comprenden el fragmento de introgresión de PI313970, fragmento de introgresión que comprende un QTL de resistencia a CYSDV ligado a al menos un marcador ubicado en el cromosoma equivalente al grupo de ligamiento (GL) 6 de la accesión de melón PI313970 como se describe y reivindica en el documento EP1962578B1. Como se mencionó, en el documento EP1962578B1 el GL6 nombrado de manera arbitraria es el GL VI de la ICuGI de melón, pero corresponde al Grupo de Ligamiento V (GL V) de la ICuGI. En un aspecto, las plantas de melón cultivadas desveladas en el presente documento comprenden un cromosoma 5 (GL V de la ICuGI) y dicho cromosoma 5 no comprende la introgresión de PI313970, introgresión que comprende un QTL de resistencia a CYSDV ligado a al menos un marcador ubicado en el cromosoma equivalente al grupo de ligamiento (GL) 6 de la accesión de melón PI313970 como se describe y reivindica en el documento EP1962578B1.
En otro aspecto, se desvela en el presente documento una planta de melón cultivada desvelada en el presente documento que comprende un cromosoma 6 recombinante de acuerdo con la invención y que comprende adicionalmente un cromosoma 5 recombinante que comprende una introgresión de PI313970, introgresión que comprende un QTL de resistencia a CYSDV ligado a al menos un marcador ubicado en el cromosoma equivalente al grupo de ligamiento (GL) 6 de la accesión de melón PI313970 como se describe y reivindica en el documento EP1962578B1, es decir, una planta de melón cultivada, partes y células de la misma, que comprende al menos dos fragmentos de introgresión del melón silvestre, uno que confiere resistencia a MYaV en el cromosoma 6 (como se describe en la memoria descriptiva) y otro que confiere resistencia a CYSDV al cromosoma 5 (GL V de la ICuGI).
ADN y cromosomas desvelados
En un aspecto, se desvela en el presente documento un cromosoma 6 modificado (recombinante) de C. melo cultivado, que comprende un fragmento de introgresión de un melón silvestre o de un pariente silvestre del melón, como se describe a lo largo de la memoria descriptiva. En un aspecto desvelado, el cromosoma 6 recombinante se aísla de su entorno natural. En otro aspecto se desvela una célula vegetal, especialmente una célula de melón, especialmente una célula de C. melo cultivado. Además, se desvela en el presente documento una parte aislada del cromosoma 6 recombinante que comprende el alelo MYaV.
En un aspecto adicional, se desvela una molécula de ácido nucleico recombinante, especialmente una molécula de ADN recombinante, que comprende un alelo MYaV de acuerdo con la invención. En un aspecto, el alelo MYaV es detectable por uno o más de los ensayos de marcadores moleculares descritos en el presente documento. Además, se desvela un vector de ADN que comprende el ADN recombinante. La molécula de a Dn recombinante o el vector de ADN puede ser una molécula de ácido nucleico aislada. El ADN que comprende el alelo MYaV puede estar en un microorganismo, tal como una bacteria (por ejemplo, Agrobacterium).
Se describe en el presente documento el uso de tal molécula de ácido nucleico (aislada o extraída) y/o de tal cromosoma 6 recombinante o parte del mismo para generar células vegetales y plantas que comprenden un alelo MYaV. En un aspecto, puede utilizarse para generar células de melón, plantas de melón y partes de melón transgénicas (por ejemplo, frutos) que comprendan el alelo MYaV, y la planta comprende un fenotipo de resistencia MYaV.
Por tanto, se desvelan en el presente documento células vegetales transgénicas, por ejemplo, células de melón transgénicas, que comprenden en su genoma un cromosoma 6 recombinante como se describe y/o una molécula de ácido nucleico recombinante que comprende un alelo MYaV. En un aspecto, la molécula de ADN que comprende el alelo MYaV está integrada de manera estable en el genoma del melón.
El alelo MYaV también se puede clonar y se puede fabricar un gen quimérico, por ejemplo, uniendo operativamente un promotor expresable en planta al alelo MYaV. Dicho gen quimérico puede introducirse en una célula vegetal y la célula vegetal puede regenerarse en una planta completa para producir una planta transgénica. En un aspecto, la planta transgénica es una planta de melón.
Por tanto, en el presente documento se desvelan plantas transgénicas, especialmente plantas de melón cultivadas transgénicas, que comprenden un alelo de resistencia MYaV y que tienen un fenotipo de resistencia MYaV.
Se desvelan especialmente células o cultivos celulares que comprenden un cromosoma 6 recombinante, independientemente de si el cromosoma 6 recombinante se introduce mediante procedimientos transgénicos o mediante procedimientos de mejora genética. Las células están, por ejemplo, in vitro y son regenerables en plantas de melón que comprenden el cromosoma 6 recombinante desvelado en el presente documento.
Además, las secuencias de marcadores moleculares (y las moléculas de ácido nucleico aisladas que comprenden la
secuencia) desveladas en el presente documento y los marcadores moleculares entre cualquiera de los marcadores moleculares mencionados descritos en el presente documento y representados en la Figura 1, ligados al QTL que confiere resistencia a MYaV, y su uso en la detección y/o generación de plantas de melón resistentes a MYaV están abarcados en el presente documento.
LEYENDAS DE LAS FIGURAS
Figura 1: El perfil de LOD de MYaV6.1, un QTL en el grupo de ligamiento de melón VI (GLVI) que confiere resistencia a MYaV. Los mapas de ligamiento del GLVI para los dos cruces [(990631-2)-Q-1-K x NCIMB41966 y Amaregal x NCIMB41969] están representados por barras rellenas, y los marcadores de SNP y las distancias en cM (centiMorgan) están en los lados derecho e izquierdo de las barras, respectivamente. Los marcadores de SNP comunes entre los dos mapas se indican con líneas de conexión. El perfil de LOD en el mapa de (990631-2)-Q-1-K x NCIMB41966 muestra los resultados de las evaluaciones de campo de las familias F3 reproducidas en 2010, mientras que el de Amaregal x NCIMB41969 muestra los resultados de 2011 de las evaluaciones de campo de las plantas f2. El LOD máximo para el cruce (990631-2) -Q-1-K x NCIMB41966 fue de 6,3, lo que explica el 32,6 % de la variación observada en 2010. El LOD máximo del cruce Amaregal x NCIMB41969 fue de 50,3, lo que explica el 91,7 % de la variación observada en 2011.
Figura 2: Fotografía tomada en Brasil de la variedad de melón susceptible Hibrix (fila central) que muestra síntomas de MYaV. El rectángulo muestra la parte de la planta de melón que se fenotipa para detectar los síntomas.
Depósitos de semillas
Nunhems B.V. depositó una muestra representativa de semillas de accesiones de melón silvestre que comprenden el QTL (designado MYaV6.1) para la resistencia a MYaV en el cromosoma 6 el 2 de mayo de 2012 en la NCIMB Ltd. (Edificio Ferguson, Craibstone Estate, Bucksburn Aberdeen, Escocia AB21 9YA, Reino Unido) de acuerdo con el Tratado de Budapest, a tenor de la Solución del Experto (EPC 2000, Norma 32 (1)). Las semillas recibieron los siguientes números de depósito: NCIMB 41966 y NCiMb 41969.
Nunhems B.V. depositó una muestra representativa (2600) de semillas (BC1S2) de una planta de melón cultivada que comprende el QTL para la resistencia a MYaV en el cromosoma 6 en forma homocigótica (designado MYaV6.1) el 15 de febrero de 2013 en la NCIMB Ltd. (Edificio Ferguson, Craibstone Estate, Bucksburn Aberdeen, Escocia AB21 9YA, Reino Unido) de acuerdo con el Tratado de Budapest, a tenor de la Solución del Experto (EPC 2000, Norma 32 (1)). Las semillas recibieron el siguiente número de depósito: NCIMB 42113.
Nunhems B.V. depositó una muestra representativa (1300) de semillas (BC4F2) de una planta de melón cultivada que comprende el QTL para la resistencia a MYaV en el cromosoma 6 en forma homocigótica (designado MYaV6.1) el 12 de diciembre de 2013 en la NCIMB Ltd. (Edificio Ferguson, Craibstone Estate, Bucksburn Aberdeen, Escocia AB21 9YA, Reino Unido) de acuerdo con el Tratado de Budapest, a tenor de la Solución del Experto (EPC 2000, Norma 32 (1)). Las semillas recibieron el siguiente número de depósito: NCIMB 42198.
El solicitante solicita que las muestras del material biológico y cualquier material obtenido del mismo solo se entreguen a un Experto designado en conformidad con la Norma 32(1) de la EPC o la legislación relacionada de países o tratados que tengan normas y regulaciones similares, hasta la indicación de la concesión de la patente, o durante 20 años a partir de la fecha de presentación si la solicitud es rechazada, retirada o considerada como retirada.
El acceso al depósito estará disponible durante la tramitación de la presente solicitud para las personas que el Director de la Oficina de Patentes de Estados Unidos determine que tienen derecho a solicitarlo. Sometido a 37 C.F.R. § 1.808(b), todas las restricciones impuestas por el depositante sobre la disponibilidad al público del material depositado se eliminarán de manera irrevocable al otorgar la patente. El depósito se mantendrá durante un período de 30 años, o 5 años después de la solicitud más reciente, o durante la vigencia exigible de la patente, lo que sea más largo, y se reemplazará si en algún momento se vuelve no viable durante ese período. El solicitante no renuncia a ningún derecho otorgado a tenor de la presente patente en esta solicitud o a tener de la Ley de Protección de Variedades Vegetales (7 USC 2321 y siguientes).
Los siguientes Ejemplos no limitantes describen cómo se pueden obtener plantas que comprenden un cromosoma 6 recombinante. A menos que se indique lo contrario en los Ejemplos, todas las técnicas de a Dn recombinante se llevan a cabo de acuerdo con protocolos convencionales como se describen en Sambrook y col. (1989) Molecular Cloning: A Laboratory Manual, Segunda edición, Cold Spring Harbor Laboratory Press, y Sambrook y Russell (2001) Molecular Cloning: A Laboratory Manual, Tercera edición, Cold Spring Harbor Laboratory Press, NY; y en los volúmenes 1 y 2 de Ausubel y col. (1994) Current Protocols in Molecular Biology, Current Protocols, EE.UU. Los materiales y procedimientos convencionales para el trabajo molecular en plantas se describen en Plant Molecular Biology Labfax (1993) por R.D.D. Croy, publicado conjuntamente por BIOS Scientific Publications Ltd (RU) y Blackwell Scientific Publications, RU. Los procedimientos de mejora genética convencionales se describen en 'Principles of Plant breeding', Segunda edición, Robert W. Allard (iSBN 0-471-02309-4).
Ejemplo 1 - Resistencia en el cromosoma 6 de NCIMB 41966
1. 1 Material y procedimientos
1.1.1 Desarrollo de las poblaciones F2 y F3
Se realizó un cruce entre la línea de reproducción (990631-2) -Q-1-K, que es susceptible a MYaV, y una accesión de melón silvestre, Cucmis melo ssp. agrestis, obtenida de los EE. UU. pero originaria de la India, cuyas semillas depositó Nunhems B.V. con el número de referencia NCIMB 41966.
La progenie F1 obtenida del cruce se autofecundó para obtener una población F2, que se utilizó para el genotipado (se genotiparon 96 plantas F2). Las plantas F2 se autofecundaron para obtener familias F3, que se fenotiparon en un ensayo de resistencia a MYaV en el campo, cerca de Mossoro, Brasil, en 2010, como se describe a continuación. 1.1.2 Ensayo de resistencia a MYaV de las familias F3
Los ensayos de resistencia a MYaV se realizaron en 2010 en campo abierto cerca de Mossoro, a una alta incidencia natural de MYaV. Cada familia F3 se plantó en tres repeticiones de 20 plantas por repetición, en 2010, junto con controles susceptibles (4 plantas, 3 repeticiones) y el control resistente NCIMB41966 (20 plantas). Se utilizó un diseño aleatorizado completo, dado que la presión de la enfermedad fue uniforme en todo el campo.
Los controles susceptibles fueron Glory F1 (Origene Seeds), Ruidera F1, Amaregal F1, Guapore, Goldex, DRY9150 y Sancho (Syngenta).
El fenotipado de los síntomas de MYaV se realizó de forma visual, cuando los controles susceptibles mostraron claros síntomas de amarilleamiento.
Cada planta recibió una puntuación de enfermedad en la siguiente escala, mediante la cual solo se utilizan las hojas más antiguas, es decir, el primer tercio (1/3) de la planta alrededor del tallo principal y el sistema de raíces. Por tanto, al referirse en el presente documento a "todas las hojas" o "pocas hojas" o un determinado porcentaje del área foliar total, solo se hace referencia a las hojas en el 1/3 más antigua de la planta, véase también la Figura 2, donde el rectángulo negro indica el 1/3 de la planta que se puntúa de acuerdo con la siguiente escala:
(continuación)
La puntuación de la enfermedad promedio se calculó por familia F3 y por control.
1.1.3 Genotipado de familias F2
El genotipado de las familias F2 se realizó utilizando la matriz Illumina Infinium de SNP (polimorfismo de un único nucleótido), que contiene 4600 SNP. Además se analizaron algunos marcadores SSR (repeticiones de secuencia simples) de la ICuGI y sirvieron como marcadores de anclaje junto con algunos otros marcadores de SNP de anclaje, para determinar el número y la orientación del grupo de ligamiento.
1.1.4 Análisis de datos de los datos del genotipo F2 y del fenotipo F3
El mapeo de ligamiento se realizó utilizando JoinMap v4 y el análisis de QTL se realizó con el programa informático MapQTL v5.
1.2 Resultados
1.2.1 Resultados del ensayo de resistencia a MYaV en 2010
Los resultados de las verificaciones de susceptibles y resistentes se muestran a continuación:
1.2.2 Resultados del mapeo del QTL de familias F2 y F3
Los marcadores de SNP mapearon en 12 grupos de ligamiento, correspondientes al número de cromosomas haploide del melón.
Para los datos de fenotipo de 2010 se encontró un QTL significativo para la resistencia a MYaV en el grupo de ligamiento VI (basado en la nomenclatura de la ICuGI), con una puntuación de LOD máxima de 6,3 y que explica el 32,6 % de la variación fenotípica observada para la resistencia a MYaV.
Los resultados se muestran en la Figura 1.
Los siguientes marcadores de SNP se asociaron con el fenotipo de resistencia MYaV. También se indica en la Tabla el genotipo del parental resistente y del susceptible en el locus del marcador.
Tabla 1
Ejemplo 2 - Resistencia en el cromosoma 6 de NCIMB 41969
2. 1 Material y procedimientos
2.1.1 Desarrollo de la población F2
Se realizó un cruce entre la variedad híbrida de melón Galia Amaregal F1, que es susceptible a MYaV, y una accesión de melón silvestre, obtenida de España pero originaria de la India, cuyas semillas depositó Nunhems B.V. con el número de referencia NCIMB 41969.
La progenie F1 obtenida del cruce se autofecundó para obtener una población F2, la cual se utilizó para genotipado (181 plantas F2). Las plantas F2 se fenotiparon en un ensayo de resistencia a MYaV en el campo, cerca de Mossoro, Brasil, en 2011, como se describe a continuación.
2.1.2 Ensayo de resistencia a MYaV de plantas F2
Los ensayos de resistencia a MYaV se realizaron en 2011 en campo abierto cerca de Mossoro, a una alta incidencia natural de MYaV.
Los controles susceptibles (10 plantas por parcela) fueron Amaregal (Nunhems), Sancho (Syngenta) y Caribbean Gold. Además, se incluyó el NCIMB 41969 como verificación de resistentes (20 plantas por parcela).
El fenotipado de los síntomas de MYaV se realizó de forma visual, cuando los controles susceptibles mostraron claros síntomas de amarilleamiento.
Cada planta recibió una puntuación de enfermedad en la escala descrita anteriormente en 1.1.2.
La puntuación de la enfermedad promedio se calculó por línea o variedad vegetal.
2.1.3 Genotipado de familias F2
El genotipado de las plantas F2 se realizó utilizando un conjunto genómico amplio de 96 marcadores en una plataforma KASP para el mapa de armazón inicial. Además se analizaron algunos marcadores SSR (repeticiones de secuencia simples) de la ICuGI y sirvieron como marcadores de anclaje junto con algunos otros marcadores de SNP de anclaje, para determinar el número y la orientación del grupo de ligamiento.
2.1.4 Análisis de datos de los datos del genotipo F2 y del fenotipo F2
El mapeo de ligamiento se realizó utilizando JoinMap v4 y el análisis de QTL se realizó con el programa informático MapQTL v5.
2.2 Resultados
2.2.1 Resultados del ensayo de resistencia a MYaV en 2011
Los resultados de las verificaciones de susceptibles y resistentes se muestran a continuación:
2.2.2 Resultados del mapeo del QTL de plantas F2
Los marcadores de SNP mapearon en 12 grupos de ligamiento, correspondientes al número de cromosomas haploide del melón.
Se encontró un QTL significativo para la resistencia a MYaV en el grupo de ligamiento VI (basado en la nomenclatura de la ICuGI), con una puntuación de LOD máxima de 50,3 y que explica el 91,7 % de la variación fenotípica observada para la resistencia a MYaV.
Los resultados se muestran en la Figura 1.
Los siguientes marcadores de SNP se asociaron con el QTL. También se indica en la Tabla el genotipo del parental resistente y del susceptible en el locus del marcador.
Tabla 2
Los anteriores Ejemplos 1 y 2, muestran que un fragmento de introgresión de melones silvestres, que comprende un locus que confiere resistencia a MYV, confiere resistencia a MYaV cuando se transfiere al melón cultivado. Dado que el QTL mapeó en el grupo de ligamiento 6, el QTL se denominó MYaV6.1. Se han depositado semillas de tales plantas de melón cultivadas que comprenden el QTL denominado MYaV6.1, con el número de depósito NCIMB 42113 (que comprenden el fragmento de introgresión de NCIMB 41969) y NCIMB 42198 (que comprenden el fragmento de introgresión de NCIMB 41966).
El QTL MYaV6.1 se encontró en dos accesiones de melón silvestre, de orígenes distintos (India y Uzbekistán), y se encontró que dos marcadores de SNP (mME12135 y ME15090) estaban comúnmente ligados al QTL en ambas poblaciones, mientras que cinco marcadores de SNP (mME40332, mME28908, mME36531, mME9692 y mME50656) y tres marcadores de SNP (mME21377, mME36533 y mME13585) estaban asociados con (ligados a) el QTL obtenido de NCIMB41966 y NCIMB41969, respectivamente.
Uno o más (al menos dos, tres, cuatro, cinco, seis, siete o más), o todos los marcadores de SNP asociados con MYaV6.1 proporcionados en el presente documento, pueden utilizarse para diversos fines, tal como
a) para detectar la presencia de un fragmento de introgresión en el cromosoma 6 que comprende el QTL MYaV6.1 en plantas o partes de plantas de melón cultivadas;
b) para transferir el cromosoma 6 recombinante, que comprende el locus que confiere resistencia a MYaV (MYaV6.1), de un melón cultivado a otras plantas de melón cultivadas, especialmente variedades o líneas de reproducción susceptibles a MYaV;
c) para generar y/o seleccionar nuevas plantas de melón cultivadas que comprendan una introgresión con el QTL MYaV6.1 de una fuente silvestre, tal como un melón silvestre o un pariente silvestre del melón (tal como del NCIMB 41966 o NCIMB 41969, u otros melones silvestres o parientes silvestres del melón),
d) para reducir el tamaño del fragmento de introgresión silvestre que comprende el QTL MYaV6.1, es decir, para generar y seleccionar recombinantes que tienen un fragmento de introgresión más pequeño en el cromosoma 6, pero que conserven la resistencia a MYaV que confiere parte del fragmento de introgresión;
e) para desarrollar marcadores moleculares alternativos para cualquiera de los fines mencionados anteriormente, ligados a MYaV6.1;
f) para cribar las accesiones de melón silvestre o parientes silvestres del melón en cuanto a la presencia de uno o más de los marcadores y, por tanto, la presencia del QTL MYaV6.1 y para introgresar la parte que confiere resistencia de estas nuevas fuentes de resistencia en plantas de melón cultivadas susceptibles a MYaV.
Ejemplo 3 - Ensayos de SNP (ensayo KASP) o "ensayo de marcadores de MYaV "
Para cribar plantas en cuanto a la presencia de uno o más de los marcadores moleculares anteriores, ligados al fragmento de introgresión que confiere resistencia a MYaV, se desarrolló un ensayo KASP (un ensayo de genotipado de SNP o ensayo de genotipado de PCR específica de alelo de KBioscience) para los marcadores de SNP mME21377, mME1590, mME12135, mME36533, mME13585 y mME36531.
Basándose en las secuencias genómicas que comprenden el SNP (véase la Tabla 3 a continuación y el listado de secuencias), para cada marcador de SNP se desarrollaron dos cebadores directos específicos de alelo (es decir, que detectan el nucleótido del parental susceptible o resistente en el locus del SNP) y un cebador inverso común (en cursiva) , indicados en la Tabla 3 y 4 (todas las secuencias se dan en dirección 5' a 3').
Claims (5)
1. Un procedimiento de identificación de una planta de C. melo cultivada que comprende un fragmento de introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV, que comprende:
a) proporcionar una población de plantas de C. melo cultivada recombinantes (tal como una población F2, F3, BC1, BC2, BC1S1),
b) cribar dicha población utilizando un ensayo de marcadores moleculares que detecta al menos un marcador de SNP seleccionado del grupo que consiste en:
marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3; y
c) identificar y/o seleccionar una planta que comprende al menos el genotipo CC o AC para el marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y el genotipo AA o AG para el marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3.
2. Un procedimiento de identificación de una planta de melón silvestre que comprende resistencia a MYaV en el cromosoma 6, comprendiendo dicho procedimiento:
a) proporcionar una accesión de melón silvestre o varias accesiones de melón silvestre;
b) cribar dicha accesión (o accessiones) de melón silvestre utilizando un ensayo de marcadores moleculares que detecta al menos un marcador de SNP seleccionado del grupo que consiste en:
marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3; y
c) identificar y/o seleccionar una planta de melón silvestre que comprende al menos el genotipo CC o AC para el marcador de SNP mME15090 en el nucleótido 71 de la Se Q ID NO: 1 y el genotipo AA o AG para el marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3; y, opcionalmente
d) confirmar la resistencia a MYaV en un ensayo de resistencia a MYaV.
3. Un procedimiento de detección de si una planta de C. melo cultivada comprende un fragmento de introgresión en el cromosoma 6, en el que dicho fragmento de introgresión comprende un alelo de resistencia a MYaV, comprendiendo dicho procedimiento:
a) proporcionar una planta de C. melo cultivada,
b) cribar dicha planta utilizando un ensayo de marcadores moleculares que detecta al menos un marcador de SNP seleccionado del grupo que consiste en:
marcador de SNP mME15090 en el nucleótido 71 de la SEQ ID NO: 1 y marcador de SNP mME12135 en el nucleótido 71 de la SEQ ID NO: 3.
4. El procedimiento de acuerdo con una cualquiera de las reivindicaciones precedentes, que comprende adicionalmente determinar el genotipo
A) de uno o más marcadores seleccionados del grupo del marcador de SNP
mME40332 en el nucleótido 71 de la SEQ ID NO: 2,
mME28908 en el nucleótido 71 de la SEQ ID NO: 4,
mME36531 en el nucleótido 71 de la SEQ ID NO: 5,
mME9692 en el nucleótido 71 de la SEQ ID NO: 6,
mME50656 en el nucleótido 71 de la SEQ ID NO: 7, o
B) de uno o más marcadores seleccionados del grupo de marcadores de SNP
mME21377 en el nucleótido 71 de la SEQ ID NO: 8,
mME36533 en el nucleótido 71 de la SEQ ID NO: 11,
mME13585 en el nucleótido 71 de la SEQ ID NO: 12.
5. El procedimiento de acuerdo con una cualquiera de las reivindicaciones precedentes, en el que los marcadores de SNP son detectados utilizando un ensayo KASP.
Applications Claiming Priority (3)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| EP12196771 | 2012-12-12 | ||
| EP13162350 | 2013-04-04 | ||
| PCT/EP2013/076454 WO2014090968A1 (en) | 2012-12-12 | 2013-12-12 | Melon plants with melon yellowing associated virus (myav) resistance |
Publications (1)
| Publication Number | Publication Date |
|---|---|
| ES2786507T3 true ES2786507T3 (es) | 2020-10-13 |
Family
ID=49759329
Family Applications (2)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| ES19175414T Active ES2983766T3 (es) | 2012-12-12 | 2013-12-12 | Plantas de melón con resistencia al virus asociado al amarilleamiento del melón (MYaV) |
| ES13803041T Active ES2786507T3 (es) | 2012-12-12 | 2013-12-12 | Plantas de melón con resistencia al virus asociado al amarilleamiento del melón (MYaV) |
Family Applications Before (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| ES19175414T Active ES2983766T3 (es) | 2012-12-12 | 2013-12-12 | Plantas de melón con resistencia al virus asociado al amarilleamiento del melón (MYaV) |
Country Status (6)
| Country | Link |
|---|---|
| US (1) | US10034441B2 (es) |
| EP (2) | EP3560331B1 (es) |
| BR (1) | BR112015013615B1 (es) |
| ES (2) | ES2983766T3 (es) |
| MX (2) | MX2015007086A (es) |
| WO (1) | WO2014090968A1 (es) |
Families Citing this family (11)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| MX384547B (es) | 2014-05-22 | 2025-03-14 | Nunhems Bv | Plantas de melon con resistencia a la mosca blanca. |
| ES2897766T3 (es) * | 2014-06-06 | 2022-03-02 | Nunhems Bv | Plantas de melón con un gen dominante de resistencia al virus asociado al amarilleamiento del melón (MYAV) |
| EP3238533A1 (en) * | 2016-04-28 | 2017-11-01 | Semillas Fito, S. A. | Begomovirus-resistant melon plants |
| US11591611B2 (en) | 2016-07-12 | 2023-02-28 | Nunhems B.V. | TolCNDV resistant melon plants |
| US10947557B2 (en) | 2016-07-12 | 2021-03-16 | Nunhems B.V. | ToLCNDV resistant melon plants |
| NZ749964A (en) * | 2016-07-12 | 2025-11-28 | Nunhems Bv | Tolcndv resistant melon plants |
| IL265093B2 (en) | 2016-08-30 | 2024-10-01 | Seminis Vegetable Seeds Inc | Melon plants with improved traits |
| CN108754006B (zh) * | 2018-05-31 | 2021-05-07 | 河南农业大学 | 与甜瓜蔓茎长短性状基因SI/si紧密连锁的分子标记 |
| WO2019233863A1 (de) | 2018-06-04 | 2019-12-12 | Bayer Aktiengesellschaft | Herbizid wirksame bizyklische benzoylpyrazole |
| WO2021245435A1 (en) * | 2020-06-03 | 2021-12-09 | Vilmorin & Cie | Melon plants resistant to scab disease, aphids and powdery mildew |
| US20230389501A1 (en) * | 2020-10-29 | 2023-12-07 | Syngenta Crop Protection Ag | Novel type of long shelf-life melon plants |
Family Cites Families (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| EP1800535A1 (en) | 2005-12-21 | 2007-06-27 | De Ruiter Seeds R&D B.V. | Closterovirus-resistant melon plants |
-
2013
- 2013-12-12 EP EP19175414.2A patent/EP3560331B1/en active Active
- 2013-12-12 EP EP13803041.6A patent/EP2931025B1/en active Active
- 2013-12-12 BR BR112015013615-0A patent/BR112015013615B1/pt active IP Right Grant
- 2013-12-12 ES ES19175414T patent/ES2983766T3/es active Active
- 2013-12-12 WO PCT/EP2013/076454 patent/WO2014090968A1/en not_active Ceased
- 2013-12-12 US US14/651,485 patent/US10034441B2/en active Active
- 2013-12-12 ES ES13803041T patent/ES2786507T3/es active Active
- 2013-12-12 MX MX2015007086A patent/MX2015007086A/es active IP Right Grant
-
2015
- 2015-06-04 MX MX2019011805A patent/MX2019011805A/es unknown
Also Published As
| Publication number | Publication date |
|---|---|
| EP3560331B1 (en) | 2024-03-06 |
| US20150313107A1 (en) | 2015-11-05 |
| EP2931025A1 (en) | 2015-10-21 |
| MX2015007086A (es) | 2016-02-10 |
| MX2019011805A (es) | 2019-11-07 |
| US10034441B2 (en) | 2018-07-31 |
| EP3560331A1 (en) | 2019-10-30 |
| WO2014090968A1 (en) | 2014-06-19 |
| BR112015013615A2 (pt) | 2017-11-14 |
| ES2983766T3 (es) | 2024-10-24 |
| EP2931025B1 (en) | 2020-02-12 |
| BR112015013615B1 (pt) | 2023-01-10 |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| ES2786507T3 (es) | Plantas de melón con resistencia al virus asociado al amarilleamiento del melón (MYaV) | |
| ES2897766T3 (es) | Plantas de melón con un gen dominante de resistencia al virus asociado al amarilleamiento del melón (MYAV) | |
| AU2013231277B2 (en) | Tomato plants with intense phenotype and TYLCV resistance | |
| CN116193982B (zh) | 番茄中导致ToBRFV抗性的基因 | |
| US10687494B2 (en) | Watermelon plants with cucumber vein yellowing virus (CVYV) resistance | |
| ES2968531T3 (es) | Plantas de espinacas resistentes al menos a las razas 8, 9, 11, 13 y 16 de Peronospora farinosa | |
| ES3043087T3 (en) | Melon plants with whitefly resistance | |
| US20240206414A1 (en) | Introgression of tolcndv-es resistance conferring qtls in cucumis sativus plants | |
| AU2021330660A1 (en) | Novel disease resistant watermelon plants | |
| KR20260047584A (ko) | 파파야 링스팟 바이러스(prsv) 저항성을 갖는 신규한 스쿼시 식물 |