[0001] Este pedido reivindica benefício sob USC 35 § 119(e) do pedido provisional dos Estados Unidos N° de Série 60/529.182, depositado em 11 de dezembro de 2003, que é por meio do qual incorporado por referência em sua totalidade.
Campo da Invenção
[0002] A presente invenção refere-se ao campo de biologia molecular da planta. Mais especificamente, a presente invenção refere- se ao milho transgênico com lisina aumentada, e aos ensaios e métodos para identificar o DNA exógeno específico fornecendo lisina aumentada.
Antecedente da Invenção
[0003] Zea mays,comumente conhecido como milho, é um grão amplamente empregado na alimentação animal. O grão, isto é, O caroço, é uma fonte de proteína, amido, e óleo para porco, gado vacum e aves domésticas. Dos dez aminoácidos supostos essenciais em uma fonte de alimento de grão misturada, o milho é particularmente limitante em lisina, treonina, e metionina. A falta desses aminoácidos, especialmente lisina, requer que o milho alimentício ou farinha de milho sejam suplementados com esses nutrientes, geralmente fornecidos pela adição de farinha de soja. Seria de benefício para a técnica aumentar o nível de lisina no caroço de milho como um meio de tornar a semente e farinha, mais nutritivos como um alimento animal.
[0004] A fim de aumentar os níveis de lisina empregando um método biológico molecular, uma versão insensível a retroalimentação de pelo menos uma das enzimas de via de lisina, isto é, ácido dihidrodipicolínico sintase (referido aqui como DHDPS), tem sido identificado e empregado. Um gene de DHDPS bacteriano isolado de E. coli foi mostrado in vitroser cerca de 200 vezes menos sensível a inibição por aumento nos níveis de lisina e, quando introduzido em tabaco transgênico, a superexpressão do gene de DHDPS de E. coli resultou em níveis aumentados de lisina no tecido da folha (Glassman e outros, Patente U.S. 5.288.300). Falco e outros, descrevem as plantas transgênicas com níveis aumentados de lisina na semente e genes úteis para a produção de tais plantas transgênicas (Patentes U.S. 5.773.691 e 6.459.019; Publicação do Pedido de Patente U.S. 2003/0056242, cada dos quais está incorporado aqui por referência em sua totalidade). Nesses relatórios, Falco e outros descrevem a isolação e o uso de DHDPS insensível a retroalimentação de E. coli e DHDPS de Corynebacterium (também conhecido como co rd a pA) para gerar plantas de colza, tabaco, milho e soja transgênicas com níveis aumentados de lisina na semente. Para milho, Falco e outros reportam um aumento de aproximadamente 130% em lisina livre nos caroços transformados com o gene de cordapA relativo aos caroços não transformados.
[0005] Seria vantajoso ser capaz de detectar a presença ou ausência de um transgene particular em uma planta ou semente, ou progénie de tais plantas ou sementes, não somente com respeito ao transgene propriamente dito, porém também com respeito a sua localização no genoma de uma semente ou planta hospedeira. A identificação com respeito à localização também fornece identificação do evento transgênico pelo qual um construtor genético inseriu o transgene na planta progenitora da planta ou semente.
Sumário da Invenção
[0006] A presente invenção fornece constructos úteis para gerar eventos transgênicos e materiais e métodos úteis para identificar os eventos transgênicos particulares que resultaram em plantas transgênicas que acumulam níveis mais elevados de lisina do que fazem as plantas estritamente relacionadas que não incluem o constructo. Em particular, esta invenção compreende uma linhagem de milho transgênico livre de marcador compreendendo um DNA exógeno específico que foi introduzido através da transformação de milho padrão, referido aqui como "o Evento LY038" ou "Evento LY038". A presente invenção também fornece um método para detectar a presença ou ausência do Evento LY038 no DNA obtido de amostras de sementes, tecido ou plantas de milho. A planta de milho da presente invenção compreendendo o Evento LY038 exibe a lisina aumentada no caroço relativo a um progenitor ou outra planta substancialmente relacionada. Além disso, a presente invenção fornece um constructo de DNA exógeno compreendendo um promotor de globulina 1 de milho, um íntron de actina 1 de arroz, uma molécula de DNA de codificação de peptídeo de trânsito de cloroplasto dihidrodipicolinato sintase de milho, uma molécula de DNA de codificação de dihidrodipicolinato sintase de Corynebacterium, e uma região não transladada 3' de globulina 1 de milho que, quando operavelmente ligada e expressada em plantas e células de planta transgênica, resulta em conteúdo de lisina aumentado no caroço ou partes desta ou um produto processado derivado do caroço ou planta. Em outra modalidade, o constructo também compreende um sítio lox, presente como um componente de um mecanismo para remoção do gene marcador empregado para identificar os transformantes bem-sucedidos.
[0007] Com respeito à identificação de uma planta ou semente derivada de um evento transgênico particular, as composições e métodos são fornecidos para detectar a presença da região de inserção genômica de uma nova planta de milho compreendendo o Evento LY038, isto é, o sítio no genoma onde o constructo reside. As moléculas de DNA são fornecidas, as quais compreendem pelo menos uma porção do DNA exógeno, inserida no genoma e uma porção do DNA do genoma de milho flanqueando o sítio de inserção (referido aqui como uma "sequência de junção").
[0008] Em ainda outra modalidade da presente invenção, as novas moléculas de DNA são fornecidas as quais compreendem pelo menos cerca de 20 pares de base de SEQ ID NO: 1 ou 2, onde os pares de base 1781-1782 ou 200-201, respectivamente, são incluídos. Também fornecidas pela presente invenção são as moléculas de DNA compreendendo a sequência de um amplicon tendo a sequência de SEQ ID NO: 6, obtida por um método de amplificação de DNA empregando os iniciadores das SEQ ID NOs: 3 e 4; e uma sonda de hibridização complementar ao referido amplicon, tendo a sequência SEQ ID NO: 5 e complementes deste. As moléculas de DNA tendo a sequência de SEQ ID NO:5 ou 6 abrangem a junção entre o DNA exógeno e o DNA genômico de milho de flanqueamento e são diagnóstico para o DNA de vento LY038 quando empregadas em testes analíticos adequados. Outras moléculas de DNA preferidas da presente invenção que abrangem a junção do DNA exógeno/ região de inserção genômica do Evento LY038 são as moléculas tendo a sequência de SEQ ID NOs 1,2 e 11, e complementos destes. Uma semente ou planta de milho estavelmente transformada compreendendo essas moléculas é outro aspecto desta invenção.
[0009] Os iniciadores são referidos serem de "comprimento suficiente" quando eles são de um comprimento que permite o iniciador funcionar em uma reação de PCR e especificamente amplificar uma sequência alvo; um comprimento de cerca de 11 nucleotídeos ou mais é suficiente, mais preferivelmente cerca de 18 nucleotídeos ou mais, ainda mais preferivelmente cerca de 24 nucleotídeos ou mais, ainda mais preferivelmente cerca de 30 nucleotídeos é suficiente para realizar e especificamente amplificar uma sequência alvo. Alguém versado na técnica saberia que um iniciador de comprimento ainda maior do que cerca de 30 nucleotídeos pode ser de modo útil empregado em uma reação de PCR e, conseqüentemente, é de um comprimento suficiente.
[00010] Os iniciadores de PCR úteis para identificar o Evento LY038 compreendem um comprimento suficiente de uma porção de transgene da sequência de DNA de SEQ ID NO: 1 e um comprimento suficiente de uma sequência de DNA de milho de flanqueamento 5'da SEQ ID NO:1, ou um comprimento suficiente de uma porção de transgene da sequência de DNA de SEQ ID NO: 2 e um comprimento suficiente de uma sequência de DNA de milho de flanqueamento 3'da SEQ ID NO: 2. Esses iniciadores são úteis nos métodos de PCR para fornecer um produto de amplicon de DNA que é diagnóstico para o Evento LY038 e sua progénie. Os iniciadores de PCR homólogos ou complementares a qualquer comprimento adequado das SEQ ID NOs: 1 e 2 que podem produzir um amplicon ou sonda que seja diagnóstico para o Evento LY038, são outros aspectos da presente invenção. Por exemplo, sem limitação, os iniciadores preferidos que são diagnóstico para o Evento LY038 incluem aqueles tendo pelo menos cerca de 18 nucleotídeos contíguos da sequência ou de SEQ ID NO: 3 ou 4. Os amplicons produzidos empregando os iniciadores de DNA que são diagnóstico para o Evento LY038 e sua progénie são um aspecto desta invenção. Um diagnóstico de amplicon preferido para o Evento LY038 tem a sequência da SEQ ID NO: 6.
[00011] Outro aspecto da presente invenção fornece métodos para detectar a presença ou ausência de DNA correspondendo ao Evento LY038 em uma amostra. Tais métodos compreendem obter o DNA de uma planta, semente ou tecido de milho, contatando o DNA de amostra com um grupo de iniciador de PCR, realizando PCR e detectando a presença ou ausência de um amplicon. O diagnóstico dos iniciadores de PCR preferido para Evento LY038 inclui os iniciadores de oligonucleotídeo tendo as sequências de SEQ ID NOs: 3 e 4, que produzem um amplicon específico de evento LY038 tendo a sequência de, por exemplo, SEQ ID NO: 6, que é detectável por uma sonda específica de evento LY038 tendo a sequência de, por exemplo, SEQ ID NO: 5.
[00012] A hibridização de uma sonda indicando a presença do Evento LY038 para um amplicon compreendendo DNA específico para o Evento LY038 pode ser detectada por qualquer meio adequado disponível para técnicas de manipulação de ácido nucléico, incluindo ensaios de TaqMan®, métodos de southern blot entre outros métodos conhecidos por aqueles versados na técnica de biologia molecular. Alguém versado na técnica saberia que a detecção do amplicon pode ser realizada através da detecção que não envolve hibridização de uma sonda para um amplicon, tal como análise de gel acrilamida ou gel agarose. Alguém versado na técnica também saberia que ambos o comprimento e a sequência de ambos o iniciador e a sonda podem ser variados das sequências exemplificadas presentes nas SEQ ID NOs: 3, 4, e 5, e ainda produzir um amplicon de PCR, ou grupo de amplicon e sonda, que é diagnóstico para o Evento LY038.
[00013] Em outro aspecto, a presente invenção fornece um método para produzir as plantas progénies compreendendo o DNA do Evento LY038. A plantas progénies podem ser plantas congênitas ou híbridas. Em uma outra aplicação, a presente invenção fornece um método para realizar reprodução auxiliada por marcador para o DNA do Evento LY038. De acordo com outro aspecto da presente invenção, uma planta de milho estavelmente, transformada compreendendo o DNA do Evento LY038 e também compreendendo a lisina aumentada no caroço ou partes desta é fornecida.
[00014] A presente invenção também se refere a um kit de detecção de DNA compreendendo pelo menos uma molécula de DNA de comprimento suficiente de nucleotídeos contíguos homólogos ou complementares a SEQ ID NO: 1 ou 2, que funciona como um iniciador ou sonda de DNA específico para Evento LY038 ou sua progénie.
[00015] Esta presente invenção também se refere às plantas e sementes às plantas e sementes e produtos processados destes de milho com alto teor de lisina (Zea mays)compreendendo o Evento LY038 e a progénie derivada deste tendo a semente representativa depositada como ATCC No. de acesso PTA-5623. Adicionalmente fornecida pela presente invenção é uma planta de milho ou uma parte desta, incluindo, por exemplo, pólen ou semente, produzida pelo crescimento de uma planta que compreende o DNA de Evento LY038. A semente e planta de milho compreendendo o DNA do Evento LY038 para o qual as moléculas do iniciador de DNA da presente invenção são de modo útil empregadas para detecção das sequências específicas de evento são também aspectos da invenção.
[00016] Um produto processado do Evento LY038 compreende uma parte de um caroço de milho, por exemplo, o endosperma. Uma farinha de milho da presente invenção pode ser feita do caroço compreendendo a molécula de DNA transgênica de LY038, onde a farinha é elevada em lisina relativa a outras farinhas de milho não contendo a molécula de DNA.
[00017] Os anteriores e outros aspectos da presente invenção se tornarão mais evidentes a partir da seguinte descrição detalhada, exemplos e figuras acompanhantes. Os seguintes exemplos são incluídos para demonstrar os exemplos de certas modalidades preferidas da presente invenção. Deve ser observado por aqueles versados na técnica que as técnicas descritas nos exemplos que seguem representam os métodos que os inventores constataram funcionar bem na prática da presente invenção, e desse modo podem ser considerados constituir os exemplos dos modos preferidos para sua prática. Entretanto, aqueles versados na técnica devem, levando em consideração a presente descrição, observar que muitas alterações podem ser feitas nas modalidades específicas que são descritas e ainda obtém um resultado igual ou similar sem afastar-se do espírito e escopo da invenção.
Breve Descrição dos Desenhos
[00018] Figura 1 é um mapa de plasmídeo de pMON55221.
[00019] Figura 2A é um esquemático do Evento LY038 de inserção de DNA exógeno. O DNA exógeno e os pares de base pertinentes são indicados por fonte em itálico, o DNA genômico de milho e pares de base pertinentes são indicados por fonte regular.
[00020] Figura 2B é a sequência na junção 5'.
[00021] Figura 2C é a sequência na junção 3'.
Breve Descrição das Sequências
[00022] As moléculas tendo as sequências definidas empregadas no contexto da presente invenção são apresentadas na Listagem de Sequência depositada concomitantemente com este pedido. Um resumo da Listagem de Sequência segue:
[00023] SEQ ID NO: 1 é uma sequência de polinucleotídeo de 1961 pares de base (bp) do DNA 5' compreendendo a porção genômica do milho (1-1781 pares de base) flanqueando o lado 5' do sítio de inserção e porção de inserção de transgene (1782-1961 pares de base) do DNA do evento LY038.
[00024] SEQ ID NO: 2 é uma sequência de polinucleotídeo de 867 pares de base do DNA 3' compreendendo a porção genômica do milho 3' (201-867 pares de base) flanqueando o lado 3' do sítio de inserção e sequência de inserção de transgene (1-200 pares de base) do DNA do evento LY038.
[00025] SEQ ID NOs: 3 e 4 são sequências de polinucleotídeo de iniciadores de PCR úteis para a produção de um diagnóstico de amplicon para o DNA do Evento LY038.
[00026] SEQ ID NO: 5 é uma sequência de polinucleotídeo de uma sonda de oligonucleotídeo útil para hibridizar para um amplicon para detecção do DNA do Evento LY038.
[00027] SEQ ID NO: 6 é uma sequência de polinucleotídeo de um diagnóstico de amplicon para o DNA do Evento Ly038.
[00028] SEQ ID NO: 7 é uma sequência de polinucleotídeo de um promotor de globulina 1 de milho (48 a 1440 pares de base; Kriz, Biochem. Genet.,27:239-251, 1989; Belanger e Kriz, Genetics, 129:863-872, 1991; Patente U.S. 6.329.574, incorporada aqui por referência em sua totalidade), um íntron de actina 1 de arroz (1448 a 1928 pares de base; McElroy e outros, Plant Cell,2: 163-171, 1990), um peptídeo de trânsito de cloroplasto de DHDPS de milho (1930 a 2100 pares de base; Frisch e outros, Mol. Gen. Genet.,228:287-293, 1991), um gene de DHDPS de Corynebacteríum (2101 a 3003 pares de base; Bonnassie e outros, Nucleic Acids Research, 18:6421, 1990); Richau e outros, J. Bacteriol., 166:297-300, 1986), uma região não transladada 3' de globulina 1 de milho (3080 a 4079 pares de base; Belanger e Kriz, supra), e um sítio P lox (4091 a 4124 pares de base; Russel e outros, Mol. Gen. Genet.,234:45-59, 1992).
[00029] SEQ ID NO: 8 é uma sequência de polinucleotídeo de um gene de DHDPS de Corynebacteríum (Bonnassie e outros, Nucleic Acids Research, 18:6421, 1990; Richaud e outros, J. Bacteriol., 166: 297-300, 1986).
[00030] SEQ ID NO: 9 é uma sequência de polinucleotídeo de 1736 pares de base de DNA genômico de milho adicional fanqueando o lado 5' do sítio de inserção do Evento LY038 (observe a Figura 2A).
[00031] SEQ ID NO: 10 é uma sequência de polinucleotídeo de 359 pares de base de DNA genômico de milho adicional flanqueando o lado 3' do sítio de inserção do Evento LY038 (observe a Figura 2A).
[00032] SEQ ID NO:11 é uma sequência de polinucleotideo de 20 pares de base consistindo em 10 nucleotideos contíguos de DNA de inserção de transgene e 10 nucleotideos contíguos de DNA genômico de milho da sequência de junção ilustrada na Figura 2C.
Descrição Detalhada da Invenção
[00033] Como empregado aqui, "DNA exógeno"se refere ao DNA que não naturalmente se origina do constructo, célula ou organismo particular no qual aquele DNA é encontrado. O DNA exógeno pode incluir uma sequência de DNA ou RNA nativa a um genoma porém em uma nova localização no genoma ou ligada a outros elementos da sequência, não naturalmente associados com o DNA exógeno em seu estado nativo. Os constructos de DNA recombinantes empregados para a transformação das células da planta compreendem o DNA exógeno e geralmente outros elementos como descrito abaixo. Como empregado aqui "transgene" significa um DNA exógeno que foi incorporado em um genoma hospedeiro ou que é capaz de replicação autônoma em uma célula hospedeira e que é capaz de causar a expressão de um ou mais produtos celulares. Os transgenes exemplares fornecem as plantas ou células hospedeiras regeneradas destes, com um novo fenótipo relativo à planta ou célula progenitora não transformada correspondente, ou uma planta ou célula progenitora transformada correspondente compreendendo outros transgenes porém não o transgene particular em questão. Os transgenes podem ser diretamente introduzidos em uma planta por transformação genética, ou podem ser herdados de uma planta de qualquer geração anterior que tenha sido transformada com o DNA exógeno.
[00034] Como empregado aqui, "gene" ou "sequência de codificação" significa uma sequência de DNA da qual uma molécula de RNA é transcrita. O RNA pode ser um mRNA que codifica um produto de proteína, um RNA que funciona como uma molécula de anti-sentido, ou uma molécula de RNA estrutural tal como um tRNA, rRNA, snRNA, ou outros RNA. Como empregado aqui, "expressão" se refere à combinação dos processos intracelulares, incluindo transcrição e translação, pelo qual uma molécula de DNA, tal como um gene, é empregado para produzir um polipeptídeo ou uma molécula de RNA. Uma sequência de codificação exemplar é um gene de dihidrodipicolinato sintase de Corynebacteríum (DHDPS; Bonnassie e outros, Nucleic Acids Research, 18:6421, 1990; Richaud e outros, J. Bacteríol., 166:297-300, 1986; 2101 a 3003 pares de base das SEQ ID NOs: 7 e 8), úteis para a produção de caroços de milho com lisina aumentada. Uma planta de milho, transformada para conter e expressar um gene de DHDPS de Corynebacteríum, resultando em lisina aumentada no tecido do caroço, é também referida como uma planta de milho com alto teor de lisina.
[00035] Como empregado aqui, "promotor" significa uma região da sequência de DNA que é essencial para a iniciação da transcrição de DNA, resultando na geração de um RNA que é complementar ao DNA transcrito; esta região pode também ser referida como uma "região reguladora 5'". Os promotores estão localizados a montante da sequência de codificação a ser transcrita e têm regiões que atuam como os sítios de ligação para RNA polimerase e têm regiões que funcionam com outros fatores para promover a transcrição de RNA. Os promotores de planta úteis incluem aqueles que são constitutivos, induzíveis, específicos de tecido, temporalmente regulados, circadiano na regulação, induzível de secura, induzível de tensão, regulado de modo desenvolvimental, induzível de frio, induzível de luz, e outros. De importância particular para a presente invenção é um promotor específico de embrião, tal como, sem limitação, o promotor de globulina 1 de milho (Kriz, Biochem. Genet.,27: 239-251, 1989; Belanger e Kriz, Genetics,129: 863-872, 1991; 48 a 1440 pares de base da SEQ ID NO: 7)
[00036] Como se sabe na técnica, os constructos de DNA recombinantes tipicamente também compreendem outros elementos reguladores além de um promotor, tal como porém não limitado às regiões não transladadas 3' (tal como sítios de poliadenilação ou sinais de terminação transcricionais), peptídeos de trânsito ou sinal, introns, e elementos de genes marcadores. Uma região não transladada 3' (3' UTR) útil na prática da presente invenção é a UTR 3' de globulina 1 (Kriz, Biochem. Genet.,27:239-251, 1989; Belanger e Kriz, Genetic, 129:863-872, 1991; 3080 a 4079 pares de base da SEQ ID NO: 7). Um peptídeo de trânsito particularmente útil é o peptídeo de trânsito de DHDPS de milho (Frisch e outros, Mol. Gen. Genet.,228:287-293,1991; 1930 a 2100 pares de base da SEQ ID NO: 7). Um íntron útil no contexto da presente invenção é o íntron 1 de actina 1 de arroz (McElroy e outros, Plant Cell,2: 163-171, 1990; 1448 a 1928 pares de base da SEQ ID NO: 7).
[00037] Como empregado aqui, o termo "milho" significa Zea mays, também conhecido como milho, e inclui todas as variedades de planta que pode ser reproduzida com milho, incluindo espécies de milho silvestre. Os métodos e composições para transformação de plantas introduzindo-se um DNA exógeno em um genoma da planta na prática desta invenção podem incluir qualquer dos métodos bem-conhecidos e demonstrados. Até hoje, a liberação de gene mediada por Agrobacteriume micropartícula são os dois métodos de transformação de planta mais comumente empregados. A transformação mediada por micropartícula se refere à liberação de DNA revestido em micropartículas que são propulsadas em tecidos alvos por vários métodos. A transformação mediada por Agrobacteriumé obtida através do uso de uma bactéria de solo geneticamente construída pertencendo ao gênero Agrobacterium.Várias espécies de Agrobacteriummediam a transferência de um DNA específico conhecido como "T-DNA", que pode ser geneticamente construído para carregar qualquer pedaço desejado de DNA dentro de muitas espécies de planta. Os métodos preferidos de transformação de planta são bombardeios de microprojéteis como ilustrado nas Patentes U.S. 5.015.580, 5.550.318, 5.538.880, 6.160.208, 6.399.861, e 6.403.865; e transformação mediada por Agrobacteriumcomo ilustrado nas Patentes U.S. 5.635.055, 5.824.877, 5.591.616, 5.981.840, e 6.384.307, todas das quais estão incorporadas aqui por referência.
[00038] Como empregado aqui, um organismo "transgênico" é um cujo genoma tenha sido alterado pela incorporação de material genético estrangeiro ou cópias adicionais de material genético nativo, por exemplo, por transformação ou recombinação. O organismo transgênico pode ser uma planta, mamífero, fungos, bactéria, ou vírus. Como empregado aqui "planta transgênica" significa uma planta estavelmente transformada ou planta progénie de qualquer geração subseqüente derivada desta, onde o DNA da planta ou progénie desta contém um DNA exógeno introduzido não originalmente presente em uma planta não transgênica do mesmo filamento. A planta transgênica pode adicionalmente conter sequências que são nativas à planta sendo transformada, porém onde o DNA exógeno tenha sido alterado a fim de alterar o nível ou padrão de expressão do gene.
[00039] Como empregado aqui, uma planta "estavelmente" transformada é uma planta na qual o DNA exógeno é hereditável. O DNA exógeno pode ser hereditável como um fragmento de DNA mantido na célula da planta e não inserido no genoma do hospedeiro. Preferivelmente, a planta estavelmente transformada compreende o DNA exógeno inserido no DNA cromossômico no núcleo, mitocôndria, ou cloroplasto, mais preferivelmente no DNA cromossômico nuclear.
[00040] Como empregado aqui uma "planta transgênica Ro" é uma planta que tenha sido diretamente transformada com um DNA exógeno ou que tenha sido regenerada de uma célula ou feixe de célula que tenha sido transformado com um DNA exógeno. Como empregada aqui "progénie" significa qualquer geração subseqüente, incluindo as sementes e plantas desta, que é derivada de uma planta parental particular ou grupo de plantas parentais; a linhagem da progénie resultante pode ser congênita ou híbrida. A progénie de uma planta transgênica desta presente invenção pode ser, por exemplo, autocruzada, cruzada com uma planta transgênica, cruzada com uma planta não transgênica, e/ou contra cruzada.
[00041] As sementes das plantas desta presente invenção podem ser colhidas de plantas transgênicas férteis e serem empregadas para desenvolver as gerações de progénie de plantas desta presente invenção, incluindo uma linhagem de planta híbrida compreendendo o DNA exógeno do Evento LY038, que fornece o benefício de lisina aumentada no caroço de milho. O caroço de milho pode ser processado em produtos de farinha ou óleo ou o caroço pode alimentar aos animais sem processamento. O produto de farina, em particular, contém um traço agronômico realçado, a lisina aumentada. A presente invenção contempla uma farinha de milho com lisina aumentada relativa a outras farinhas de milho, onde a farinha de milho compreende DNA exógeno do Evento LY038.
[00042] O termo "DNA do Evento LY038" se refere a um segmento de DNA compreendendo um DNA exógeno inserido em um local particular em um genoma e adjacente ao DNA genômico de flanqueamento que seria esperado ser transferido pra uma planta progénie de uma planta parente contendo o DNA exógeno. Mais especificamente, o DNA do Evento LY038 também se refere a cada das regiões de DNA que incluem uma interface do DNA genômico e o DNA exógeno inserido no genoma do transformante Ro, por exemplo, uma região ao redor de uma interface onde a terminação 5' está no DNA genômico e a terminação 3' está no DNA exógeno. Além disso, a sequência do DNA exógeno compreendendo um DNA de evento pode ser alterada ao mesmo tempo em que residente em seu local particular em um genoma hospedeiro, por exemplo, uma porção da sequência pode ser alterada, deletada, ou amplificada, e ainda constitui o referido DNA de evento desde que o referido DNA exógeno continue a residir no mesmo local no genoma.
[00043] Um evento "transgênico" é produzido por transformação de uma célula de planta com um constructo de DNA exógeno, a regeneração de uma planta resultante da inserção do DNA exógeno no genoma da planta, e seleção de uma planta particular caracterizada por DNA de evento. Tipicamente, várias células de planta são transformadas, produzindo uma população de plantas das quais uma planta particular é selecionada. O termo "evento" se refere ao transformante original Ro e progénie do transformante que inclui o DNA exógeno inserido em um local único e particular no genoma, isto é, DNA de evento. O termo "evento" também se refere à progénie produzida por um "outcross" sexual, um autocruzamento, ou contra cruzamento repetido, onde pelo uma das plantas empregadas na reprodução é de qualquer geração do transformante Ro original contendo DNA de evento.
[00044] Desse modo, um "evento" transgênico é uma planta compreendendo e definida por um "DNA de evento". Desse modo, "Evento LY038" compreende "DNA de Evento LY038". Uma planta pode compreender dois ou mais DNAs de evento diferentes e desse compreende dois ou mais eventos diferentes. Além disso, uma planta sem um determinado evento de transgene X não compreende aquele DNA X em questão. O DNA de evento pode ser transformado de planta para planta, geração para geração, por qualquer esquema de reprodução, método, ou instrumento conhecido por aqueles versados na técnica de reprodução de milho.
[00045] A transformação de plantas tipicamente utiliza um marcador selecionável e método de seleção para distinguir as células transformadas da cultura das células não transformadas. Em alguns casos o gene marcador selecionável permanece na planta transgênica; em outros casos é desejável remover o gene marcador selecionável ou outras sequências introduzidas no DNA exógeno. A recombinação homóloga é um método útil para a deleção dos genes marcadores residindo em uma planta transgênica (Patente U.S. 6.580.019, incorporada aqui por referência em sua totalidade). Outro instrumento útil para remover as sequências de uma planta envolve o uso de enzimas recombinase de sítio específico e seus respectivos sítios alvos de sítio específico.
[00046] Vários sistemas de recombinase de sítio específico diferentes podem ser empregados de acordo com a presente invenção, incluindo, porém não limitado ao, sistema Cre/lox de bacteriófago P1, e o sistema FLPZ FRT de levedura. Os sistemas Cre/lox de bacteriófafago P1 e FLP/FRP de levedura constituem dois sistemas particularmente úteis para integração de sítio específico ou excisão de transgenes. Nesses sistemas, uma recombinase (Cre ou FLP) irá interagir especificamente com sua respectiva sequência de recombinação de sítio específico (lox ou FRT, respectivamente) para inverter ou excisar as sequências de intermédio . A sequência para cada desses dois sistemas é relativamente curta (34 pares de base para lox, e 47 pares de base para FRT) e portanto, conveniente para uso com os vetores de transformação. Os sistemas de recombinase de FLP/FRT e Cre/lox têm sido demonstrados funcionar eficientemente em células de planta. Em uma modalidade preferida, um sistema de recombinase de Cre/lox é empregado para sequências de marcadores selecionáveis removidas, particularmente um gene marcador NPT II (observe a Figura 1) flanqueado por sítios de recombinação lox P (4091 a 4124 pares de base, SEQ ID NO: 7; Russel e outros, Mol. Gen. Genet.,234:45-59, 1922).
[00047] Uma planta transgênica, semente ou parte desta, que mostra um traço desejado realçado, por exemplo, "lisina aumentada", é uma planta compreendendo um DNA exógeno que concede uma alteração mensurável, desejada em um traço em comparação com uma planta de substancialmente o mesmo genótipo que é desprovido do DNA exógeno desejado. Preferivelmente, o traço desejado realçado é medido comparando-se o traço em uma planta transgênica com o DNA exógeno associado com o traço desejado realçado, com o traço em uma planta de substancialmente o mesmo genótipo porém desprovida daquele DNA exógeno. Uma tal planta que é desprovida desse DNA exógeno pode ser uma planta tipo silvestre natural ou uma planta transgênica, preferivelmente da mesma espécie como a planta transgênica. Preferivelmente, a planta em falta do DNA exógeno é uma irmã necessitando do DNA exógeno desejado da planta compreendendo o DNA exógeno desejado. Uma tal planta irmã pode compreender outros DNAs exógenos. A lisina aumentada pode ser exibida pela planta pelo acúmulo de quantidades aumentadas do aminoácido no caroço e pode ser medida por qualquer método adequado, tal como aquele de espectrofotometria de massa ou cromatografia líquida de alto desempenho de tecido apropriadamente extraído.
[00048] Como empregado aqui, uma "sonda" é um oligonucleotídeo isolado ao qual pode ser ligado uma molécula repórter ou rótulo detectável, por exemplo, um isótopo radioativo, ligando, agente quimioluminescente, tinta, ou enzima. Uma tal sonda é complementar a um filamento de um ácido nucléico alvo. No caso da presente invenção, uma tal sonda é complementar a um filamento de DNA genômico do Evento LY038, por exemplo, DNA genômico de uma planta ou semente de milho ou outra parte da planta do Evento LY038. As sondas, de acordo com a presente invenção são materiais incluindo DNA, RNA, e poliamidas que se ligam especificamente a uma sequência de DNA alvo, e pode ser empregado para detectar a presença daquela sequência de DNA alvo.
[00049] Os "iniciadores"são oligonucleotídeos isolados que podem se associar a um filamento de DNA alvo complementar por hibridização de ácido nucléico e em seguida ser prolongado junto ao filamento do DNA alvo por uma polimerase, por exemplo, um DNA polimerase. Como empregado aqui, os iniciadores da presente invenção são empregados para amplificação de DNA de uma sequência de ácido nucléico alvo, por exemplo, pela reação em cadeia de polimerase (PCR) e podem também ser referido como "iniciadores de PCR".
[00050] As sondas e iniciadores são de comprimento de nucleotídeo suficiente para se ligar à sequência de DNA alvo especificamente sob as condições de hibridização ou condições de reação determinadas por um técnico versado. Este comprimento pode ser qualquer comprimento que seja de comprimento suficiente para ser útil no método de detecção de escolha. Geralmente, cerca de 11 nucleotídeos ou mais no comprimento, preferivelmente cerca de 18 nucleotídeos ou mais, mais preferivelmente cerca de 24 nucleotídeos ou mais, e mais preferivelmente, cerca de 30 nucleotídeos ou mais são empregados. Tais sondas e iniciadores hibridizam especificamente para um alvo. Preferivelmente, as sondas e iniciadores de acordo com a presente invenção têm similaridade de sequência de DNA completa de nucleotídeos contíguos com a sequência alvo, embora as sondas diferindo da sequência de DNA alvo e que retêm a capacidade de hibridizar para as sequências de DNA alvo possam ser designadas por métodos convencionais. Os métodos para a preparação e uso de sondas e iniciadores são conhecidos por aqueles versados na técnica, empregando protocolos publicados em, por exemplo, Sambrook e outros, Molecular Cloning: A Laboratory Manual, Segunda Edição,Cold Spring Harbor Laboratory Press, 1989, e outros.
[00051] A identificação das sequências de DNA genômico de flanqueamento ao redor do sítio de inserção dos eventos transgênicos leva em conta o projeto dos métodos de detecção que são específicos para um determinado evento transgênico inserido em um local particular em um genoma. Um tal método de detecção, que pode diferenciar entre os transgenes iguais ou similares localizados em diferentes sítios de inserção em um genoma, é chamado um método de detecção de DNA específico de evento, por exemplo, um ensaio específico de evento. Os ensaios específicos de evento, por exemplo, para evento de milho tolerante a glifosato nk603 têm sido descritos (Publicação do Pedido de Patente U.S. 2002/0013960, incorporado aqui por referência em sua totalidade).
[00052] Em uma modalidade preferida, uma sonda de ácido nucléico da presente invenção especificamente hibridiza para o amplicon específico do Evento LY038 tendo a sequência de ácido nucléico de SEQ ID NOs: 3-6, ou complementos desta, mais preferivelmente SEQ ID NO: 5 ou complemento desta. Em outro aspecto da presente invenção, uma molécula de sonda de ácido nucléico preferida da presente invenção compartilha entre cerca de 80%, preferivelmente cerca de 90%, mais preferivelmente cerca de 95%, ainda mais preferivelmente cerca de 98%, e mais preferivelmente cerca de 99% de identidade de sequência com a sequência de ácido nucléico apresentada em uma ou mais das SEQ ID NOs: 3-6, ou complementos ou fragmentos destas. O diagnóstico de sondas exemplares para o Evento LY038 tem a sequência de SEQ ID NO: 6. Tais moléculas de sonda podem ser empregadas por aqueles versados na técnica como marcadores em métodos de reprodução de planta para identificar a progénie dos cruzamentos genéticos. A hibridização da sonda para a molécula de DNA alvo pode ser detectada por qualquer número de métodos conhecidos por aqueles versados na técnica. Esses métodos de detecção podem incluir, porém não estão limitados a, rótulos fluorescentes, rótulos radioativos, rótulos com base em anticorpo, e rótulos quimioluminescentes.
[00053] Como empregado aqui, "homólogo" se refere a uma sequência de ácido nucléico que especificamente hibridiza para o complemento da sequência de ácido nucléico a qual está sendo comparada sob condições de rigorosidade elevada. As condições de rigorosidade apropriadas, incluindo aquelas condições de tempo, temperatura, e condição do sal, que promovem a hibridização de DNA são conhecidas por aqueles versados na técnica. Ambos temperatura e sal podem ser variados, ou quer a temperatura quer a concentração de sal podem ser mantidos constantes ao mesmo tempo em que as outras variáveis são alteradas. Em uma modalidade preferida, um ácido polinucléico da presente invenção especificamente hibridizará para uma ou mais das moléculas de ácido nucléico apresentadas na SEQ ID NO: 1 ou 2, ou complementos destas ou fragmentos de qualquer uma sob condições de rigorosidade de forte a moderadamente. Em uma modalidade particularmente preferida, um ácido nucléico da presente invenção especificamente hibridizará para uma ou mais das moléculas de ácido nucléico apresentadas na SEQ ID NO: 1 ou 2 ou complementos ou fragmentos de qualquer uma sob condições de rigorosidade elevada. A hibridização da sonda para a molécula de DNA alvo pode ser detectada por qualquer quantidade de métodos conhecidos por aqueles versados na técnica, esses podem incluir, porém não estão limitados a, rótulos fluorescentes, rótulos radioativos, rótulos com base em anticorpo, e rótulos quimioluminescentes.
[00054] Como empregado aqui, "amplicon"se refere ao produto de amplificação de ácido nucléico de uma sequência de ácido nucléico alvo que é parte de um modelo de ácido nucléico. Por exemplo, para determinar se a planta de milho resultante de um cruzamento sexual contém DNA genômico de evento transgênico da planta de milho compreendendo DNA de LY038 exógeno, o DNA extraído de uma amostra de um tecido de planta de milho pode ser submetido a um método de amplificação de ácido nucléico empregando um par de iniciador de DNA que inclui um primeiro iniciador derivado de sequência de flanqueamento no genoma da planta adjacente ao sítio de inserção de DNA heterólogo inserido, e um segundo iniciador derivado do DNA heterólogo inserido para produzir um amplicon que é diagnóstico para a presença do DNA de evento. O amplicon é de um comprimento e tem uma sequência que é também diagnóstico para o evento. O amplicon pode variar no comprimento do comprimento combinado dos pares de iniciador mais um par de base de nucleotídeo, preferivelmente mais cerca de 20 pares de base de nucleotídeo, mais preferivelmente mais cerca de 50 pares de base de nucleotídeo, e ainda mais preferivelmente mais cerca de 150 pares de base de nucleotídeo e mais dependente do método empregado para detectar o amplicon. Alternativamente, um par de iniciador pode ser derivado da sequência de flanqueamento em ambos lados do DNA inserido a fim de produzir um amplicom que inclui a sequência de nucleotído de inserção total. Um membro de um par de iniciador derivado da sequência genômica da planta pode estar localizado a uma distância da sequência de DNA inserida. Esta distância pode variar de um par de base de nucleotídeo até os limites da reação de amplificação, ou cerca de 20.000 pares de base de nucleotídeo. O uso do termo "amplicon"especificamente exclui os dímeros do iniciador que podem ser formados na reação de amplificação térmica de DNA.
[00055] A amplificação de ácido nucléico pode ser concluída por qualquer dos vários métodos de amplificação de ácido nucleic conhecidos na técnica, incluindo a reação em cadeia de polimerase (PCR). A sequência da inserção de DNA heterólogo ou sequência de DNA de flanqueamento do Evento LY038 pode ser verificada (e corrigida se necessário) por amplificação de tais sequências de DNA extraídas das plantas ou semente do depósito de ATCC No. de Acesso PTA-5623 empregando os iniciadores de DNA derivados das sequências fornecidas aqui seguido por seqüenciamento de DNA padrão do amplicon de PCR ou do DNA clonado.
[00056] Os iniciadores ou sondas do DNA genômico de flanqueamento e sequências de inserção descritas aqui podem ser empregados para confirmar (e, se necessário, corrigir) as sequências de DNA descritas por métodos convencionais, por exemplo, por reclonagem e seqüenciamento de tais moléculas de DNA.
[00057] Os amplicons produzidos por métodos de amplificação podem ser detectados por uma pluralidade de técnicas, incluindo porém não limitadas a análise com base em gel, análise de bitgenético (Nikiforov e outros, Nucleic Acid Res.,22:4167-4175, 1994), pirosseqüenciamento )Winge, M., Pyrosequencing - a new approach to DNA analysis, (2000), Innovations in Pharmaceutical Technology, vol. 00, 4, p18-24), polarização fluorescente (Chen e outros, Genoma Res., 9:492-498', 1999), e faróis moleculares (Tyangi e outros, Nature Biotech., 14:303-308, 1996).
[00058] De interesse particular para a presente invenção é a detecção por ensaio de Taqman® (disponível de Applied Biosystems, Foster City, Califórnia). O ensaio de Taqman® é um método de detecção e quantificação da presença de uma sequência de DNA que é bem conhecida na técnica, e é totalmente descrita nas instruções fornecidas pelo fabricante. Este método envolve o uso de amplificação de PCR e detecção do produto da amplificação por hibridização empregando uma sonda de oligonucleotídeo FRET especial. A sonda de oligonucleotídeo FRET é designada ter uma tinta repórter fluorescente 5' e uma tinta extintora 3' covalentemente ligada às extremidades 5' e 3' da sonda. A sonda é designada se sobrepor à junção do DNA genômico e DNA inserido. A sonda FRET e iniciadores de PCR (um iniciador na sequência de DNA de transgene exógeno e um na sequência genômica de flanqueamento) são girados na presença de um termoblasto polimerase e dNTPs. A hibridização da sonda FRET resulta na divagem e liberação da porção fluorescente longe da porção de extinção da sonda FRET. Um sinal fluorescente indica a presença da sequência de inserção de flanquemanto/ transgene devido à amplificação e hibridização bem sucedidas.
[00059] Os iniciadores de PCR preferíveis para uso com ensaio de Taqman® são designados (a) terem um comprimento na faixa de tamanho de 18 a 25 bases e combinar sequências no DNA genômico de flanquamento e na inserção de transgene, (b) ter uma temperatura de fusão calculada na faixa de cerca de 57 a cerca de 60°C, por exemplo, correspondendo a uma temperatura de recozimento de PCR ideal de cerca de 52 a cerca de 55°C, e (c) produzir um produto que inclui a junção entre o DNA genômico de flanquamento e a inserção de transgene e têm um comprimento na faixa de tamanho de cerca de 75 a cerca de 250 pares de base. Os iniciadores de PCR estão preferivelmente localizados no local a fim de que a sequência de junção seja pelo menos uma base longe da extremidade 3' de cada iniciador de PCR. Os iniciadores de PCR não devem conter regiões que sejam extensivamente auto- ou intercomplementares.
[00060] As sondas FRET são designadas abranger a sequência da sequência de junção. Em uma modalidade preferida, as sondas FRET terão incorporado em sua extremidade 3' uma porção química que, quando a sonda for recozida para o DNA modelo, se ligue ao sulco menor do DNA, desse modo realçando a estabilidade do complexo de sonda modelo. A sonda preferivelmente tem um comprimento na faixa de cerca de 12 a cerca de 17 bases, e com a porção de ligação do sulco menor 3', tem a temperatura de fusão calculada de cerca de 5 a cerca de 7°C acima daquela dos iniciadores de PCR. O projeto da sonda é descrito nas Patentes U.S. 5.538.848, 6.084.102 e 6.127.121.
[00061] Outro ensaio que emprega as sequências da presente invenção é aquele de um ensaio de zigosidade. Um ensaio de zigosidade é útil para determinar se uma planta compreendendo um evento é homozigota para o DNA de evento, isto é compreendendo o DNA exógeno no mesmo local em cada cromossomo de um par cromossômico, ou heterozigoto para um DNA de evento, isto é compreendendo o DNA exógeno em somente um cromossomo de um par cromossômico. Em uma modalidade, um ensaio de três iniciadores é empregado onde o iniciador 1 hibridiza e se estende especificamente do DNA exógeno inserido, iniciador 2 hibridiza e se estende especificamente do DNA flanqueando o lado 5' do DNA exógeno inserido, e iniciador 3 hibridiza e se estende especificamente do DNA flanqueando o lado 3' do DNA exógeno inserido. Os três iniciadores são diagnósticos para evento. Tipicamente, o DNA exógeno é de um tal tamanho, por exemplo, cerca de 3 a cerca de 7 quilobases ou mais, tal que o iniciador 1 e iniciador 3 não mais produzam um amplicon na reação de PCR. Quando os três iniciadores são misturados juntos em uma reação de PCR com DNA extraído de uma planta homozigota para um determinado evento, um único amplicom é produzido pelo iniciador 1 e iniciador 2, o tamanho e sequência do qual serão indicativos de e diagnósticos para o DNA de evento. Quando os três iniciadores são misturados juntos em uma reação de PCR com DNA extraído de uma planta que não compreende o determinado evento, um único amplicom é produzido pelo iniciador 1 e iniciador 3, o tamanho e sequência do qual serão indicativos de e diagnósticos para o DNA genômico de milho em falta de um DNA exógeno. Quando os três iniciadores são misturados juntos em uma reação de PCR com DNA extraído de uma planta que é heterozigoto para um determinado evento, 2 amplicons são produzidos: (1) um amplicon é produzido pelo iniciador 1 e iniciador 3, o tamanho e sequência do qual serão indicativos de e diagnósticos para o DNA genômico de milho em falta de um DNA exógeno, e (2) um amplicon é produzido pelo iniciador 1 e iniciador 2, o tamanho e sequência do qual serão indicativos de e diagnósticos para o DNA de evento. Os métodos de detecção dos vários amplicons produzidos pelo ensaio de zigosidade são conhecidos por aqueles versados na técnica e incluem, porém não estão limitados a, eletroforese em gel, ensaios de TaqMan®, Southern blot, Tecnologia Invader, seqüenciamento, faróis moleculares, pirosseqüenciamento, e outros.
[00062] Os kits de detecção podem ser desenvolvidos empregando as composições descritas aqui e os métodos bem-conhecidos na técnica de detecção de DNA. Os kits são úteis para identificação de DNA de Evento LY038 de milho em uma amostra e podem ser aplicados a métodos para reprodução de plantas de milho contendo o DNA de Evento LY038. Os kits contêm sequências de DNA que são úteis como iniciadores ou sondas e que são homólogas ou complementares ao DNA contido em qualquer dos elementos genéticos de transgene de pMON55221 (Figura 1) que tenham sido inseridos em um genoma de planta de milho para formar o Evento LY038 (Figura 2). Essas sequências de DNA podem ser empregadas em métodos de amplificação de DNA (PCR) ou como sondas em métodos de hibridização de ácido polinucléico, isto é, análise Southern, ou análise Northern. A molécula de DNA (SEQ ID NO: 7) contida no genoma de Evento LY038 compreende os elementos genéticos de transgene heterólogos que incluem um promotor de globulina 1 de milho (P-ZM glob 1), um íntron de actina 1 de arroz (l-Os actina), uma molécula de codificação de DNA de peptídeo de trânsito de cloroplasto de dihidrodipicolinato sintase de milho (Zm DHDPS CTP), uma molécula de DNA de codificação de dihidrodipicolinato sintase de Corybacterium (DHDPS), uma região não transladada 3' de globulina 1 de milho (T-Zm glob 1), e um sítio lox P e pode ser empregado como modelo para amplificação de DNA, ou para selecionar as moléculas de DNA homólogas ou complementares que podem ser empregadas como uma sonda ou iniciador de DNA em um método de detecção de DNA. A presente invenção contempla que alguém versado na técnica de detecção de DNA pode selecionar uma ou mais moléculas de DNA homólogas ou complementares ao DNA transgênico da SEQ ID NO: 7 que ser útil em um método para detectar o DNA transgênico no genoma de LY038 e progénie deste.
[00063] Os seguintes exemplos são incluídos para demonstrar os exemplos de certas modalidades preferidas da presente invenção. Deve ser observado por aqueles versados na técnica que as técnicas descritas nos exemplos que seguem representam os métodos que os inventores constataram funcionar bem na prática da presente invenção, e desse modo pode ser considerado constituir os exemplos dos modos preferidos para sua prática. Entretanto, aqueles versados na técnica devem, levando em consideração a presente descrição, observar que muitas alterações podem ser feitas nas modalidades específicas que são descritas e ainda obtém um resultado diferente ou similar sem afastar-se do espírito e escopo da invenção.
Exemplo 1
Preparação de Plantas Transqênicas
[00064] Os embriões imaturos de linhagem de milho H99 foram isolados para transformação. O DNA de cassete isolado do vetor pMON55221 (observe a Figura 1) compreendendo um promotor de globulina 1 de milho (Kriz (1989), supra; Belanger e Kriz (1991), supra; Patente U.S. No. 6.329.574, incorporada aqui por referência em sua totalidade; 48 a 1440 pares de base da SEQ ID NO: 7), um íntron de activa 1 de arroz (Mc Elroy e outros (1990), supra; 1448 a 1928 pares de base de SEQ ID NO: 7), uma molécula de DNA de codificação de peptídeo de trânsito de cloroplasto de DHDPS de milho (Frisch e outros (1991), supra-, 1930 a 2100 pares de base da SEQ ID NO: 7), uma molécula de DNA de codificação de dihidrodipicolinato sintase de Corynebacterium (Bonnassie e outros, (1990), supra-, Richaud e outros (1986), supra', 2101 a 3003 pares de base da SEQ ID NO: 7), uma região não transladada 3' de globulina 1 de milho (Belanger e Kriz (1991), supra-, 3080 a 4079 pares de base de SEQ ID NO:7), um sítio lox P (Patente U.S. 5.658.772, especificamente incorporada aqui por referência em sua totalidade; 4091 a 4124 pares de base de SEQ ID NO: 7), bem como um promotor 35S (Kay e outros, Science, 236:1299- 1302, 1987; Patente U.S. 5.164.316), uma molécula de DNA de codificação de marcador selecionável de NPTII (Potrykus e outros, (1985), supra), um UTR 3' nos (Fraley e outros, Proc. Natl. Acad. Sei. (U.S.A.), 80: 4803-4807 (1983), supra), e um sítio lox P (Patente U.S. 5.658.772, especificamente incorporada aqui por referência por referência em sua totalidade) foi aderido às partículas de ouro. O bombardeio de microprojéteis foi empregado para introduzir o DNA exógeno nos embriões de milho imaturos empregando os métodos conhecidos por aqueles versados na técnica. As células transformadas foram selecionadas empregando um esquema de seleção de canamicina. Os calos resistentes à canamicina foram obtidos e regenerados em várias plantas transgênicas Ro, férteis empregando métodos padrão.
Exemplo 2
Esquema de Reprodução e Análise de Lisina
[00065] A Tabela 1 sumariza o esquema de reprodução e dados de lisina livre empregados para o desenvolvimento do Evento LY038 de milho, que exibe alto teor de lisina no tecido do caroço de milho. As plantas produzidas pelo método de transformação descrito no Exemplo 1 foram inicialmente avaliadas quanto à presença ou ausência da sequência de DHDPS de Corynebacteríum empregando PCR. A tecnologia do ensaio de Taqman® foi empregada para determinar o número de cópias de inserções transgênicas. As plantas que compreenderam uma molécula de DNA, tendo a sequência de DHDPS de Corynebacteríum, operavelmente ligadas como descrito no Exemplo 1 e Figura 1, foram permitidas alcançar a maturidade e produzir a semente FIA. Para a produção da semente FIA, as plantas Ro transgênicas primárias foram cruzadas com uma linhagem congênita de milho elite não transgênica.
[00066] As plantas FIA foram avaliadas quanto à presença ou ausência da sequência de NPTII como mostrado empregando-se um teste de resistência à canamicina classificável de campo. A insensibilidade à canamicina indicou que uma planta compreendeu e estava expressando o gene marcador NPTII como mostrado na Figura 1 e descrito no Exemplo 1; essas plantas são referidas a seguir como NPTII+.
[00067] As plantas NPTII+ foram cruzadas com uma linhagem de milho transgênica expressando um Cre recombinase bacteriano para produzir a semente FIB. OS níveis de lisina livre em uma amostra da semente Fw resultante coletada de cada espiga foram determinados. Os caroços Fw irmãos exibindo mais do que 1000 ppm de lisina livre foram avançados para uma sementeira de campo. As plantas progénie Fw foram ensaiadas por PCR e/ou southern blot para determinar a presença ou ausência da sequência de gene de DHDPS, a sequência de codificação de Cre recombinase e a sequência de gene marcador selecionável de NPTII. O gene marcador selecionável de NPTII foi flanqueado pelos sítios lox P (sítios de recombinação) e como tais, a atividade da Cre recombinase resultou na excisão da sequência de codificação de NPTII. As plantas compreendendo o DHDPS e as sequências de Cre recombinase e em falta de sequências de NPTII, referidas a seguir como plantas de marcador excisado, foram permitidas se autopolinizar para produzir a semente F2A. A lisina livre na semente F2A positiva e negativa foi determinada.
[00068] Tendo obtido a semente F2A compreendendo 0 gene de DHDPS exógeno de interesse e em falta do gene marcador selecionável de NPTII, foi agora necessário reproduzir longe das sequências de Cre recombinase. As sementes F2A das plantas de marcador excisado foram plantadas no campo e mais uma vez ensaiadas por PCR e/ou southern blot para determinar a presença ou ausência da sequência de gene DHDPS, a sequência de codificação de Cre recombinase e a sequência de gene marcador selecionável de NPTII. As plantas compreendendo a sequência de DHDPS e em falta das sequências para ambos Cre recombinase e NPTII foram selecionadas como plantas "positivas". As plantas irmãs em falta das sequências de DHDPS, Cre recombinase, e NPTII foram selecionadas como plantas "negativas" para servir como controles negativos. As plantas compreendendo a sequência de DHDPS foram autopolinizadas para criar a semente F3 e avançadas para a próxima geração no campo. Além disso, as plantas negativas carecendo de sequências de DHDPS, Cre recombinase e NPTII foram autopolinizadas para criar a semente F3. A lisina livre na semente F3 positiva e negativa foi determinada.
[00069] As plantas positivas foram cultivadas no campo de semente F3. Uma única planta, determinada pelo ensaio Taqman® ser homozigota, foi selecionada e designada como LY038. As plantas F3 foram ou (A) autopolinizadas para produzir as espigas F4-38, ou foram (B) cruzadas com uma linhagem congênita para produzir as espigas Fi- 38A de ambas seleções positivas e negativas. A lisina livre na semente F4-38 positiva e negativa foi determinada.
[00070] A semente F1-38A do Evento LY038 foi cultivada no campo e permitida se autopolinizar para produzir a semente F2B para que a lisina livre fosse determinada.
[00071] A semente F4-38 do Evento LY038 foi cultivada no campo para produzir as plantas F4-38 e ou (A) autopolinizadas para produzir a semente F5-38, ou (B) cruzada com uma linhagem congênita para produzir a semente F1-38B híbrida empregada para avaliação agronômica. A semente F5-38 do Evento LY038 foi cultivada no campo e ou (A) autopolinizada para produzir a semente Fe-38, ou (B) cruzada com uma variedade de milho de linhagem congênita para produzir a semente F2C híbrida adicional empregada para avaliação agronômica adicional.
[00072] O depósito da semente de milho de Monsanto Company do Evento LY038 descrito acima foi gerado através da autopolinização das plantas F5-38 para produzir a semente Fe-3se a autopolinização das plantas Fe-38 para produzir a semente F7-38. A Coleção de Cultura Tipo Americana (Manassas, VA) número de acesso para 0 Evento LY038 é PTA-5623.
[00073] O acúmulo de lisina livre foi monitorado durante 0 desenvolvimento das linhagens de milho do Evento LY038. Os valores do acúmulo de lisina são sumarizados na Tabela 1 e representam a quantidade de lisina livre presente no grão maduro em uma base de peso seco, em partes por milhão.
[00074] Os métodos diferentes são úteis para avaliar 0 conteúdo de lisina de caroços maduros compreendendo 0 Evento LY038. Outros métodos conhecidos na técnica são úteis para detectar e quantificar a lisina, são contemplados pelos inventores da presente invenção para fornecer as descobertas similares de um aumento no conteúdo de lisina de semente de LY038.
[00075] A cromatografia liquida-espectrofotometria de massa/ espectrofotometria de massa (LC-MS/MS) foi empregada para analisar a lisina livre nos caroços de milho do Evento LY038. As amostras de caroço de milho maduro individuais do Evento LY038 foram primeiro pesadas, moídas para um pó homogêneo, fino e extraídas com um solvente de extração compreendendo metanol, água e ácido fórmico. Em situações onde os caroços são avolumados, aproximadamente 30 mg de pó moído foram empregados. Ambas técnicas espectrométricas de massa (MRM) monitorando a reação múltipla, e cromatografia líquida foram empregadas para separar a lisina no extrato de amostra. Após a separação, a lisina foi quantificada empregando sua área pico de espectrometria de massa contra sua curva de calibração padrão correspondente que foi preparada empregando um padrão interno de d4-lisina deuterada (IS).
[00076] Em outro método, o conteúdo de lisina de caroços de milho foi com base na avaliação dos aminoácidos livres por cromatografia líquida de alto desempenho (HPLC). Os caroços de milho individuais ou grupos de caroços do Evento LY038 foram movidos para um pó homogêneo, fino como descrito, e neste caso, aproximadamente 30 mg do pó foram empregados para análise. Os aminoácidos foram extraídos com 5% de ácido tricloroacético e a detecção de aminoácido foi obtida através de uma derivatização de amina primária de pré-coluna com o- ftalaldeído (OPA). A adução de aminoácido resultante, um isoindol, é hidrofóbica e possui excelentes características de fluorescência, que podem então ser detectadas em um detector de fluorescência. Empregando a cromatografia de fase reversa, a separação é obtida através da hidrofobicidade dos grupos R localizados em cada aminoácido. Para ajudar a estabilizar o fluoróforo, um tiol é adicionado tal como 2-mercaptoetanol (SHCH2CH2OH) ou ácido 3- mercaptopropiônico (SHCH2CH2COOH). Tabela 1: Esquema de reprodução e análise de lisina, empregados para identificar o Evento LY038 de milho com alto teor de lisina

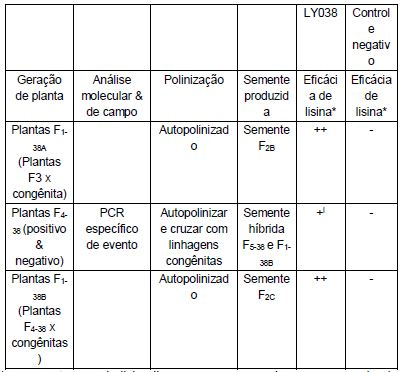
representa ppm de lisina livre nos caroços maduros compreendendo LY038 do Evento ND = Não determinado - indica menos do que cerca de 400 ppm de lisina livre + indica cerca de 1000 a cerca de 1200 ppm de lisina livre ++ indica cerca de 1200 a cerca de 1400 ppm de lisina livre +++ indica mais do que cerca de 1400 ppm de lisina livre i = dados do caroço congênito
[00077] Com base nos experimentos descritos aqui, a lisina livre nos caroços de milho que contêm o constructo de LY038 aumentou entre cerca de 200% (por exemplo, FIB,entre outros) e quase 300% (por exemplo, FIA). OS aumentos intermediários na lisina livre foram também observados (por exemplo, FI-3BA).
Exemplo 3
Determinação da Sequência de Flanqueamento
[00078] O DNA genômico foi isolado das plantas de milho designadas como LY038 e empregadas nos experimentos para determinar a sequência genômica de milho flanqueando a inserção de DNA transgênico. Três métodos diferentes, para determinar as sequências de flanqueamento e a sequência da junção, entre a sequência de flanqueamento genômico e a inserção transgênica, foram empregados: PCR de calda e o kit Genome Walker® de ClonTech (número do catálogo K1807-1, ClonTech Laboratories, Paio Alto, Califórnia), e PCR inversa.
[00079] A PCR de calda é um método para isolar a sequência de DNA genômico flanqueando uma sequência inserida conhecida que emprega os iniciadores degenerativos e uma etapa de captura de biotina. Um iniciador complementar ao DNA exógeno é empregado em reações de PCR primárias junto com uma variedade de iniciadores degenerativos. Tipicamente, os iniciadores específicos para o DNA exógeno e os iniciadores degenerados foram empregados em pares e não em grupos. Os iniciadores degenerados hibridizam a algum grau para a sequência genômica de milho flanqueando o DNA inserido para tomar em consideração a geração de amplicons de PCR. Os amplicons de PCR primários são misturados com um iniciador rotulado de biotina complementar à porção de transgene do amplicon e permitidos recozer. Os amplicons recozidos pelos iniciadores de biotina foram capturados empregando estreptavidina e os amplicons não ligados foram removidos por lavagem. Os amplicons recozidos foram submetidos às reações de PCR secundárias utilizando um iniciador aninhado que foi complementar à porção de DNA exógeno do amplicon e uma variedade de iniciadores degenerados. Os amplicons de PCR da reação de PCR secundária foram submetidos à eletroforese de gel agarose e as bandas foram cortadas do gel e isoladas. Os amplicons de PCR isolados foram seqüenciados. A sequência do DNA genômico de flanqueamento 3' do Evento LY038 foi identificada empregando PCR de calda e seqüenciamento.
[00080] O método de Genome Walker para isolamento do DNA de flanqueamento foi realizado de acordo com as condições sugeridas do fabricante. Ambos PCR de calda e o Kit Genome Walker foram empregados para identificar a sequência do DNA de flanqueamento 5' do Evento LY038. Para Genoma Walker, os produtos da enzima de restrição Seal foram amplificados para produzir os amplicons úteis para identificação da sequência de DNA genômico de flanqueamento 5' do Evento LY038.
[00081] O uso de PCR de calda e dos métodos de Genome Walker gerou várias centenas de pares de base ou mais de sequência de DNA flanqueando o sítio de inserção do constructo de DNA no Evento LY038. A PCR inversa e análise bioinformática e comparação com as bases de dados da sequência de DNA genômica de milho foram empregadas para obter DNA genômico adicional flanqueando esses eventos. Empregando os métodos combinados, as sequências de flanqueamento são identificadas na sequência de SEQ ID NO: 1,2, 9 e 10. Uma planta de milho é um aspecto da presente invenção quando esta planta de milho contém em seu genoma uma molécula de DNA que pode ser empregada como um modelo em uma reação de amplificação de DNA para fornecer um amplicon compreendendo uma molécula de DNA de junção descrita na presente invenção, onde a molécula de DNA de junção é diagnóstico para o DNA de Evento LY038 de milho em uma amostra de DNA extraída de uma amostra de tecido de milho.
Exemplo 4
Evento de Iniciador Específico e Informação do Ensaio da Sonda
[00082] Para cada evento, os iniciadores de PCR e as sondas úteis em um ensaio Taqman® foram designados, isto é, SEQ ID NO: 3 e 4. Empregando os iniciadores de PCR tendo a sequência de SEQ ID NOs: 3 e 4, em um ensaio de Taqman® resultou em um diagnóstico de amplicom para o Evento LY038; o amplicom tem a sequência de SEQ ID NO: 6, e a sonda útil para detecção deste amplicon tem a sequência de SEQ ID NO: 5. Quando os iniciadores e sondas foram submetidos às condições de PCR descritas na Tabela 2, um sinal fluorescente indicou que os amplicons foram produzidos os quais foram detectados pela sonda. Por inclusão das amostras de controle apropriadas, por exemplo, vários controles de DNA negativo e positivo, foi mostrado que os iniciadores de PCR e sondas foram específicos para o evento pretendido.
[00083] Além do conjunto de iniciador e sonda, quaisquer conjunto de iniciador e sonda derivados de SEQ ID NO: 1 ou 2, específicos para o DNA do Evento LY038 que quando empregado em uma reação de amplificação de PCR produz um diagnóstico de amplicon de DNA para o DNA do Evento LY038 são um aspecto da presente invenção e são facilmente preparados por aqueles versados na técnica. As condições de PCR para produzir um diagnóstico de ensaio de Taqman® para o DNA do Evento LY038 são incluídas na Tabela 2.
[00084] Alguém versado na técnica incluiria as amostras de controle apropriadas quando realizando os ensaios de PCR ou Taqman® descritos na presente invenção. A inclusão das amostras de DNA de controle positivo, das amostras de DNA de controle negativo, e outros controles, é apropriada e auxilia na interpretação dos resultados. Além disso, a pessoa versada na técnica saberia como preparar os iniciadores de controle interno e sondas para a reação de PCR de Taqman® empregando os métodos padrão publicados (como publicado em, por exemplo, Applied Biosystems, Foster City, Califórnia). Alguém versado também entenderia que as sequências de iniciadores, sondas, e condições de reação particulares especificadas aqui podem ser modificadas e produzir um ensaio que é diagnóstico para o DNA de Evento LY038. Adicionalmente, alguém versado na técnica saberia que os produtos da reação de PCR podem ser analisados por eletroforese de gel para análise. Tabela 2 - Mistura de reação de PCR e condições do diagnóstico para DNA do Evento LY038


1 Iniciadores misturados ressuspensos em 18 megaohm de água a uma concentração de 20 gM de cada iniciador. Exemplo: 100 pl do primeiro iniciador em uma concentração de 100 gM, 100 pl do segundo iniciador em uma concentração de 100 pM, 300 pl de 18 megaohm de água. 2 * Sonda ressuspensa em 18 megaohm de água a uma concentração de 10 pM. 3 ** Pode incluir porém não ser limitado a: Controle de DNA negativo (por exemplo, DNA não transgênico) Controle de água negativo (nenhum DNA modelo) Controle positivo (Evento LY038) DNA da amostra (da folha, semente, outras amostras da parte da planta) A Combinações de sonda e iniciador de controle interno podem ser feitas para uma ampla variedade de genes ou regiões genômicas, o projeto do qual é conhecido por aqueles versados na técnica.
[00085] Depósitos da semente de milho de Monsanto Company representativa do Evento LY038 descrito acima foram feitos sob o Tratado de Budapeste com a Coleção de Cultura Tipo Americana (ATTC), 10801 University Boulevard, Manassas, Va. 20110. O número de acesso ATCC para o evento LY038 é PTA-5623. O depósito será mantido no depositário durante um período de 30 anos, ou 5 anos após o último requerimento, ou durante a vida útil da patente, seja qual for o tempo, e será substituído quando necessário durante aquele período.
[00086] Tendo ilustrado e descrito os princípios da presente invenção, deve ser evidente às pessoas versadas na técnica que a presente invenção pode ser modificada na disposição e detalhe sem se afastar de tais princípios. Todas as modificações que estão no espírito e escopo das reivindicações anexas são reivindicadas.





